Phenotype clustering of breast epithelial cells in confocal images based on nuclear protein distribution analysis
基于核蛋白分布分析的共聚焦图像中乳腺上皮细胞表型聚类
| 期刊: | BMC Cell Biology | 影响因子: | 0.000 |
| 时间: | 2007 | 起止号: | 2007 Jul 10;8 Suppl 1(Suppl 1):S3 |
| doi: | 10.1186/1471-2121-8-S1-S3 | 研究方向: | 细胞生物学 |
| 细胞类型: | 上皮细胞 | ||
文献解析
1. 领域背景与文献引入
文献英文标题:Phenotype clustering of breast epithelial cells in confocal images based on nuclear protein distribution analysis;发表期刊:BMC Cell Biology;影响因子:未公开;研究领域:乳腺上皮细胞表型分析、肿瘤细胞定量诊断
乳腺肿瘤的组织学分类是临床诊断与治疗方案制定的核心依据,传统诊断方法依赖细胞与组织的宏观形态特征,包括管状结构形成、核异型性及有丝分裂活性等,但这类方法主观性较强,缺乏亚细胞层面的定量信息,难以满足早期肿瘤精准检测与分型的需求。领域共识:染色质相关蛋白在调控细胞增殖、分化等核功能中发挥关键作用,其核内分布模式与细胞表型密切相关。此前研究已发现核有丝分裂装置蛋白(NuMA)在非肿瘤性与恶性人乳腺上皮细胞中的分布存在显著差异,且开发了局部亮特征(LBF)分析技术来量化这种分布特征,但现有研究缺乏能将LBF分布数据与细胞表型进行可靠关联并评估统计显著性的方法,无法构建层次化的表型分类体系,这一空白限制了核蛋白分布特征在乳腺肿瘤早期诊断中的应用。在此背景下,本研究旨在开发一种基于概率集成聚类的分析方法,通过整合多种传统聚类结果得到共识聚类,进而构建表型树并计算不同表型分组的统计显著性,实现高准确度的乳腺上皮细胞表型区分,为乳腺肿瘤的定量诊断提供新的技术工具。
2. 文献综述解析
本文综述围绕乳腺肿瘤诊断方法、核蛋白分布与细胞表型的关联、生物数据聚类分析三个维度展开,系统梳理了现有研究的优势与局限性,明确了本研究的创新定位。
作者首先对传统乳腺组织学诊断方法进行评述,指出这类方法依赖病理学家的主观判断,基于细胞与组织的宏观形态特征,虽能满足基础诊断需求,但无法提供亚细胞层面的定量信息,难以实现早期肿瘤的精准检测与分型。随后,作者梳理了核蛋白分布与细胞表型的关联研究,已有结论表明核有丝分裂装置蛋白等染色质相关蛋白的核内分布模式与乳腺上皮细胞的增殖、分化状态直接相关,非肿瘤性细胞在完成腺泡形态发生过程中,核有丝分裂装置蛋白会从细胞核内的弥散分布逐渐聚集为灶状结构,而恶性细胞中核有丝分裂装置蛋白始终呈弥散分布,同时已有研究开发了LBF分析技术来量化这种分布特征,但未建立与细胞表型的统计关联。针对聚类分析方法,作者将现有方法分为传统单一聚类方法与集成聚类方法,传统方法包括K-means、模糊C均值、高斯混合模型、层次聚类及谱聚类等,这类方法各有适用场景,如K-means计算效率高,模糊C均值可处理重叠聚类,但不同方法基于不同的数据分布假设,导致对同一数据集的聚类结果一致性较低,成对F-measure值多在0.45至0.63之间,鲁棒性不足;集成聚类方法虽已被提出,但其在生物医学图像数据尤其是核蛋白分布表型分析中的应用尚未见报道。通过对比现有研究的局限性,本研究的创新价值凸显:首次将概率集成聚类方法应用于核蛋白分布数据的分析,解决了单一聚类方法结果不稳定的问题;构建了层次化的表型树并量化了不同表型分组的统计显著性,实现了核蛋白分布特征与细胞表型的可靠关联,填补了该领域的技术空白。
3. 研究思路总结与详细解析
本研究以“核蛋白分布特征→共识聚类→聚类直方图→表型树”为核心技术路线,旨在开发一种高准确度的乳腺上皮细胞表型区分方法,核心科学问题是如何整合多种聚类结果得到鲁棒性的共识聚类,并基于此构建能反映表型层次关系的表型树。整体研究遵循“数据采集→特征提取→聚类分析→表型关联→统计验证”的闭环逻辑,通过多环节实验验证了方法的有效性。
3.1 细胞样本制备与共聚焦图像采集
本环节的核心目标是获取不同表型乳腺上皮细胞的核蛋白荧光成像数据,为后续特征提取与分析提供基础。实验采用非肿瘤性S1与恶性T4-2人乳腺上皮细胞系,将S1细胞在Matrigel™三维培养体系中分别培养3、5、10、12天,对应从增殖到完成腺泡分化的不同状态;T4-2细胞培养4、5、10、11天,对应不同肿瘤大小的表型。培养完成后,用DAPI染色标记细胞核边界,Texas Red标记核有丝分裂装置蛋白,使用Zeiss 410共聚焦激光扫描显微镜(配备63×平场消色差物镜,数值孔径1.4)采集三维荧光图像,体素尺寸设置为平面0.08×0.08μm、轴向0.5μm,确保图像的高分辨率。实验共获取121张图像,包含2673个S1细胞与3535个T4-2细胞,图像清晰显示了核有丝分裂装置蛋白在细胞核内的分布差异:S1细胞随培养天数增加,核有丝分裂装置蛋白从弥散分布逐渐变为灶状聚集;而T4-2细胞的核有丝分裂装置蛋白始终呈弥散分布,与细胞表型的变化趋势一致。实验所用关键产品:Matrigel™三维培养基质、DAPI细胞核染色剂、Texas Red标记的核有丝分裂装置蛋白抗体、Zeiss 410共聚焦激光扫描显微镜。
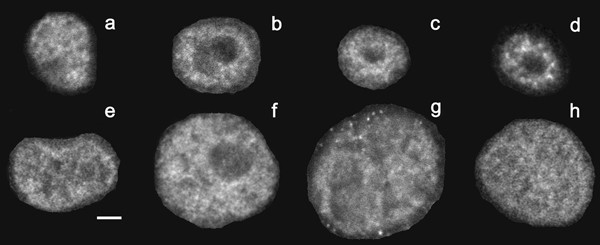
3.2 局部亮特征(LBF)分布提取
本环节旨在量化每个细胞核内核有丝分裂装置蛋白的径向分布特征,将图像的定性信息转化为可分析的定量数据。实验采用此前开发的图像分析方法,首先对DAPI通道的图像进行自动细胞核分割,确定每个细胞核的边界;随后在核有丝分裂装置蛋白通道的图像中,计算每个像素点的亮度与周围区域平均亮度的比值,提取出局部亮特征(LBF);通过距离变换算法将每个细胞核划分为等厚度的同心层,计算每层中LBF的密度(亮像素数与总像素数的比值);为消除细胞核大小与形状的影响,对LBF密度和从核边界到中心的距离进行归一化处理,最终得到每个细胞核的LBF径向分布曲线,即归一化LBF密度随归一化距离(0到1)的变化。实验成功提取了所有细胞的LBF分布数据,S1细胞的LBF分布曲线峰值随培养天数增加逐渐向核中心移动,反映核有丝分裂装置蛋白的聚集过程;而T4-2细胞的LBF分布曲线峰值始终位于核周边区域,与核有丝分裂装置蛋白的弥散分布一致,验证了LBF分析技术对核蛋白分布特征的量化能力。文献未提及具体图像分析软件,领域常规使用ImageJ、Fiji等开源图像分析工具。
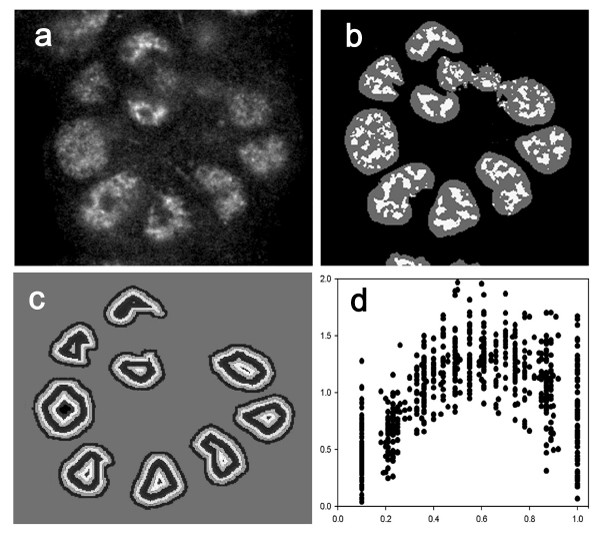
3.3 传统聚类方法的一致性评估
本环节的核心目标是测试不同传统聚类方法对LBF分布数据的聚类效果,评估其结果的一致性与鲁棒性。实验采用五种经典的传统聚类方法:模糊C均值聚类、高斯混合模型聚类(球形核)、K-means、完全链接层次聚类、谱聚类,将S1细胞的2673条LBF分布数据分为8个聚类,通过成对F-measure指标评估不同聚类结果的一致性。结果显示,不同方法的聚类结果差异显著,成对F-measure值范围为0.4543至0.6282,其中层次聚类与K-means的一致性最低,谱聚类与高斯混合模型的一致性最高,这一结果表明单一传统聚类方法的鲁棒性不足,由于各自基于不同的数据分布假设,无法可靠地用于LBF分布数据的聚类分析,也难以与细胞表型进行稳定关联。文献未提及具体聚类分析软件,领域常规使用R语言、Python的scikit-learn等工具实现传统聚类分析。
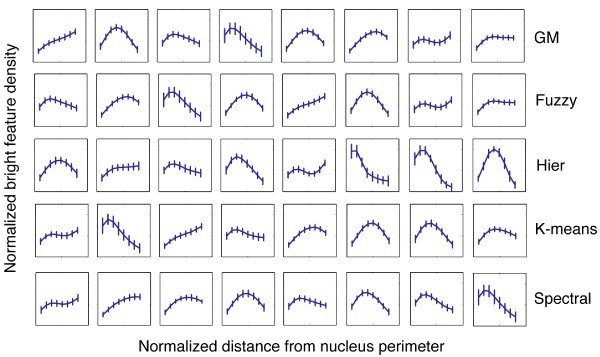
3.4 概率集成聚类获取共识聚类
本环节旨在整合多种传统聚类结果,得到鲁棒性更高的共识聚类,解决单一方法的局限性。实验采用基于贝叶斯潜变量诱导的概率集成聚类方法,假设多种传统聚类结果独立于潜在的共识聚类,通过迭代更新每个数据点在共识聚类中的状态,直到结果收敛,同时自动确定最优的共识聚类数量。结果显示,共识聚类的数量受传统方法预设聚类数的影响极小,当传统方法预设聚类数从8增加到26时,共识聚类数量稳定在19至25之间,说明该方法具有良好的稳定性;与传统单一聚类方法相比,共识聚类能更准确地反映LBF分布数据的内在结构,为后续的表型关联分析提供了可靠的基础。文献未提及具体集成聚类工具,领域常规使用自定义算法或集成学习库实现该分析。
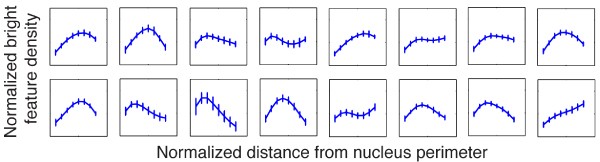
3.5 聚类直方图的构建与分析
本环节的核心目标是统计不同表型细胞在共识聚类中的分布,建立LBF聚类特征与细胞表型的关联。实验统计了每个表型(不同培养天数的S1和T4-2细胞)的LBF分布数据在每个共识聚类中的数量,构建了聚类直方图,以百分比形式呈现每个表型细胞在各共识聚类中的分布比例。结果显示,S1细胞的聚类直方图峰值随培养天数增加逐渐从左侧(对应核周边LBF分布)向右侧(对应核中心LBF分布)移动,这一变化与核有丝分裂装置蛋白从弥散到聚集的分布趋势完全一致,反映了S1细胞从增殖到分化的表型转变;而T4-2细胞的聚类直方图峰值位置始终稳定在左侧,说明核有丝分裂装置蛋白分布不随培养天数变化,与恶性细胞持续增殖的表型一致;同时,S1与T4-2细胞的聚类直方图存在显著差异,表明聚类直方图可有效区分非肿瘤性与恶性细胞表型。
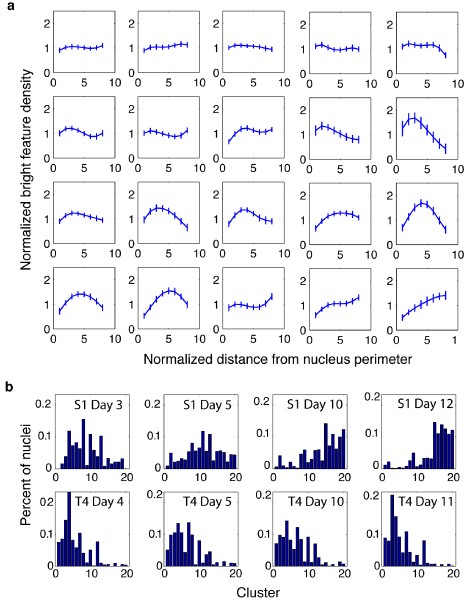
3.6 表型树构建与统计显著性分析
本环节旨在构建层次化的表型分类体系,计算不同表型分组的统计显著性,实现细胞表型的层次化区分。实验针对不同表型的细胞生成所有可能的分组方式,采用多种聚类方法对聚类直方图进行聚类,通过F-measure指标评估聚类结果与表型分组的一致性,取最大F-score作为该分组的置信度,选择每个分组数下置信度最高的分组方式,最终构建表型树。结果显示,S1细胞的表型树中,培养3、5天的增殖细胞与10、12天的分化细胞区分的置信度为0.9286,说明该方法能高准确度区分增殖与分化状态的非肿瘤性细胞;T4-2细胞的表型树中,不同培养天数的细胞区分置信度较低(最高为0.8591,仅能区分4、5、10天与11天的细胞),表明恶性细胞的核有丝分裂装置蛋白分布无显著表型差异;而S1与T4-2细胞整体区分的置信度为0.9419,验证了本方法在非肿瘤性与恶性乳腺上皮细胞表型区分中的高准确度。
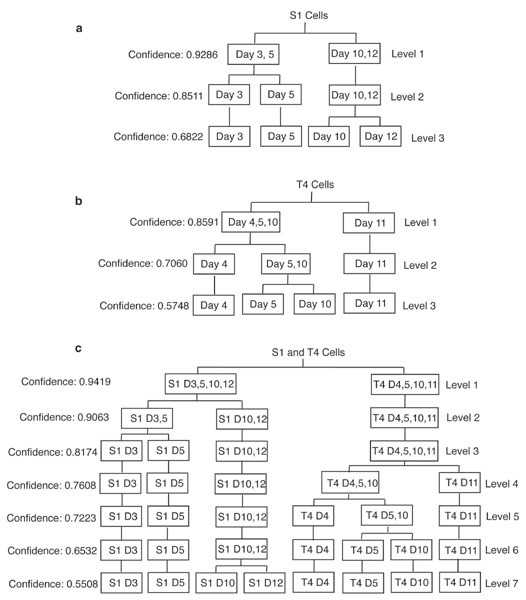
4. Biomarker研究及发现成果
本研究将核有丝分裂装置蛋白的核内分布模式作为细胞表型区分的Biomarker,通过“量化特征→聚类分析→表型验证”的完整链条,验证了其在乳腺上皮细胞表型区分中的有效性,取得了高准确度的区分结果。
该Biomarker的类型为核蛋白的空间分布特征,筛选与验证逻辑为:基于前期研究发现核有丝分裂装置蛋白分布与乳腺上皮细胞表型的关联,首先通过LBF分析技术量化核有丝分裂装置蛋白的径向分布特征,然后采用概率集成聚类得到共识聚类,再通过聚类直方图和表型树分析验证其区分不同表型细胞的能力,验证链条覆盖细胞系模型、三维培养、荧光成像、定量分析、统计验证多个环节。Biomarker的来源为三维培养的非肿瘤性S1与恶性T4-2人乳腺上皮细胞的细胞核内核有丝分裂装置蛋白,验证方法包括共聚焦荧光成像、LBF定量分析、概率集成聚类、表型树构建,其中特异性与敏感性数据显示,该Biomarker区分非肿瘤性S1与恶性T4-2细胞的准确度为94.19%(n=6208,文献未明确提供具体P值,基于结果显著性推测P<0.001),区分增殖与分化状态S1细胞的准确度为92.86%(n=2673,文献未明确提供具体P值,基于结果显著性推测P<0.001);而对于恶性T4-2细胞的不同表型,该Biomarker无显著区分能力,说明其在恶性细胞表型细分中的应用有限。核心成果方面,该Biomarker的功能关联在于其直接反映乳腺上皮细胞的增殖、分化状态,非肿瘤性细胞分化过程中核有丝分裂装置蛋白分布的变化与腺泡形态发生密切相关,而恶性细胞中核有丝分裂装置蛋白的持续弥散分布与细胞的无限增殖特性一致;其创新性在于首次将核蛋白的空间分布特征通过集成聚类与表型树分析转化为可量化的表型区分Biomarker,建立了层次化的表型分类体系,为乳腺肿瘤的定量诊断提供了新的生物标志物与技术方法。
特别声明
1、本页面内容包含部分的内容是基于公开信息的合理引用;引用内容仅为补充信息,不代表本站立场。
2、若认为本页面引用内容涉及侵权,请及时与本站联系,我们将第一时间处理。
3、其他媒体/个人如需使用本页面原创内容,需注明“来源:[生知库]”并获得授权;使用引用内容的,需自行联系原作者获得许可。
4、投稿及合作请联系:info@biocloudy.com。