Multi-faceted attributes of salivary cell-free DNA as liquid biopsy biomarkers for gastric cancer detection
唾液游离DNA作为胃癌检测液体活检生物标志物的多重特性
| 期刊: | Biomarker Research | 影响因子: | 9.500 |
| 时间: | 2023 | 起止号: | 2023 Oct 10;11(1):90. |
| doi: | 10.1186/s40364-023-00524-2 | 研究方向: | 免疫、细胞生物学 |
| 疾病类型: | 胃癌 | 细胞类型: | 肿瘤细胞 |
文献解析
1. 领域背景与文献引入
文献英文标题:Multi-faceted attributes of salivary cell-free DNA as liquid biopsy biomarkers for gastric cancer detection;发表期刊:Biomarker Research;影响因子:未公开;研究领域:肿瘤学(胃癌)、液体活检、生物标志物研究
液体活检技术近年来在肿瘤无创诊断领域发展迅速,循环游离DNA(cell-free DNA,cfDNA)作为核心生物标志物,已广泛应用于产前检测、癌症早期诊断及疗效监测。领域共识:基于血浆cfDNA的突变检测是液体活检的主流技术,其优势在于可实现无创的肿瘤基因分型,但针对胃癌的研究显示,由于肿瘤异质性高、缺乏普遍的驱动突变,该方法的诊断灵敏度和特异性受限。为突破这一局限,研究人员开始探索cfDNA的非突变特征,如片段长度分布、核小体定位、末端基序等,这类特征独立于肿瘤突变信息,适用于异质性高的癌症类型。同时,寻找易获取的替代生物流体也是液体活检的重要方向,唾液作为无创、易收集的生物流体,其蛋白和RNA组分已被证明可作为胃癌的生物标志物,但唾液中cfDNA的结构特征、构象组成及临床诊断价值尚未被系统解析。在此背景下,本研究旨在通过新型的BRcfDNA-Seq技术,系统分析唾液游离DNA的多维度特征,评估其作为胃癌液体活检生物标志物的潜力,为胃癌的无创筛查提供新策略。
2. 文献综述解析
作者在综述中围绕cfDNA的临床应用及替代生物流体的研究现状,按“血浆cfDNA突变检测、cfDNA非突变特征研究、唾液生物标志物研究”三个维度展开评述。现有研究中,血浆cfDNA的突变检测已在多种癌症的诊断中得到验证,技术成熟度高,可实现肿瘤基因分型与疗效监测,但针对胃癌的研究显示,由于肿瘤异质性高,缺乏特异性驱动突变,该方法的诊断灵敏度不足。cfDNA非突变特征的研究为临床应用提供了新方向,研究发现血浆cfDNA的片段长度分布、核小体定位等特征与肿瘤状态相关,可独立于突变信息实现癌症诊断,这类技术的优势在于无需依赖肿瘤组织的突变数据,适用于异质性高的癌症类型。唾液作为替代生物流体,其蛋白和RNA组分已被证明可作为胃癌的生物标志物,样本易获取的优势使其具有广泛的筛查应用潜力,但现有研究仅初步证明唾液中可检测到肿瘤来源的DNA,未深入分析其多维度结构特征与临床诊断价值。
本研究的创新价值在于,首次系统解析了唾液游离DNA的多方面特征,包括片段组学、末端基序、微生物组成、染色体定位等,同时采用新型的BRcfDNA-Seq技术,可捕获唾液中多种构象的游离DNA(单链、双链、缺口、锯齿状),弥补了现有研究对唾液游离DNA结构特征认识的不足。通过对比胃癌与非癌样本的差异,证明这些特征具有胃癌诊断潜力,为唾液作为胃癌液体活检的生物流体提供了关键依据,突破了现有液体活检依赖血浆样本和突变信息的局限。
3. 研究思路总结与详细解析
本研究的整体研究目标是探索唾液游离DNA的结构特征及其作为胃癌无创诊断生物标志物的临床价值,核心科学问题是唾液游离DNA的多维度特征是否能有效区分胃癌患者与非癌人群,技术路线遵循“样本收集→游离DNA提取与文库制备→高通量测序→生物信息学分析→特征验证→多变量整合”的闭环逻辑。
3.1 样本收集与游离DNA提取
实验目的是获取合格的唾液样本并提取高纯度的游离DNA,为后续分析提供基础。方法细节为收集10例胃癌患者和10例非癌志愿者的新鲜唾液样本,按照标准操作流程离心去除细胞成分,取上清液使用Qiagen的QIAmp Circulating Nucleic Acid Kit提取游离DNA,提取过程中不使用载体RNA以避免干扰后续文库制备。结果解读显示,提取的游离DNA经电泳凝胶检测显示100-200bp的条带,符合游离DNA的典型长度范围,证明成功从唾液样本中提取到合格的游离DNA。实验所用关键产品:Qiagen的QIAmp Circulating Nucleic Acid Kit(货号55114)。
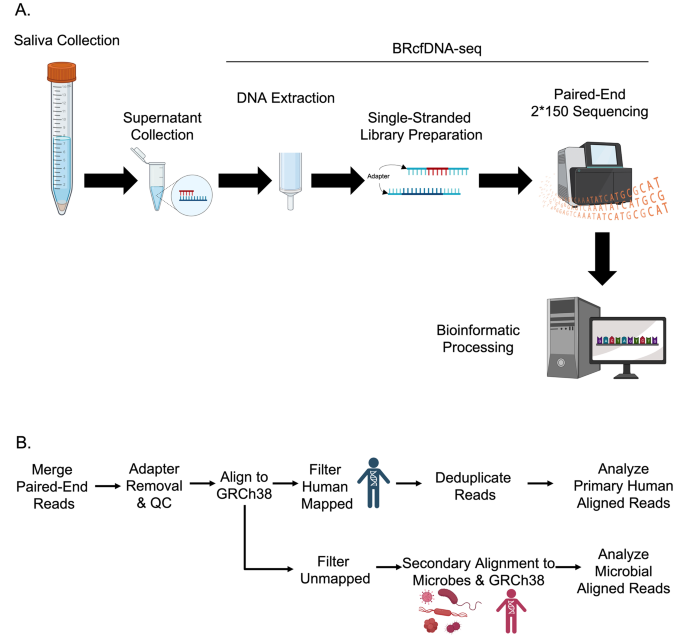
3.2 链特异性消化与文库制备
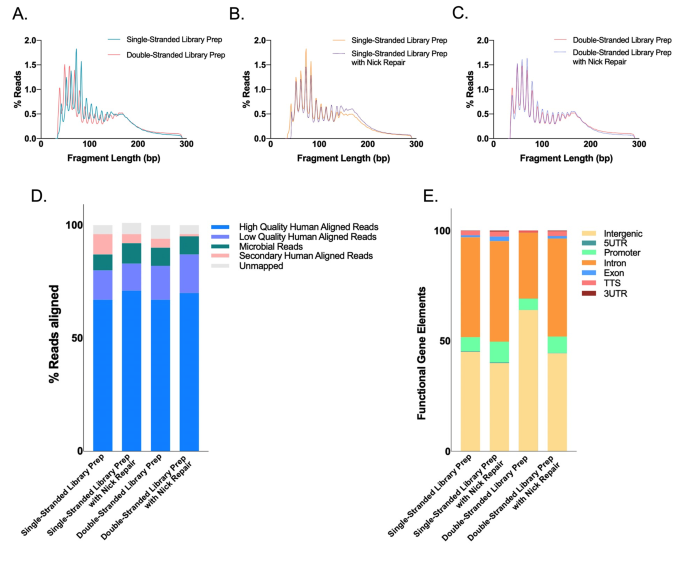
实验目的是分析唾液游离DNA的构象组成,明确单链、双链及缺口DNA的存在比例,同时优化文库制备方法以保留多种构象的游离DNA。方法细节为采用链特异性核酸酶消化:用核酸外切酶1消化单链DNA,ArcticZyme的dsDNase消化双链DNA,PreCR Repair酶修复缺口DNA;分别制备单链和双链文库,单链文库使用Claret Bioscience的SRSLYTM PicoPlus DNA NGS Library Preparation Base Kit,遵循低分子量保留protocol以保留短片段,双链文库使用NEB的Ultra II文库制备试剂盒,调整PCR循环数以优化文库产量。结果解读显示,单链和双链文库制备得到的唾液游离DNA片段模式相似,均显示35-300bp的长度范围,且存在锯齿状的片段分布特征,证明唾液游离DNA包含多种构象(单链、双链、缺口、锯齿状),单链文库能更有效地捕获短片段游离DNA。实验所用关键产品:NEB的Exonuclease 1(货号M0293S)、ArcticZyme的dsDNase(货号70600-201)、NEB的PreCR Repair(货号M0309S)、Claret Bioscience的SRSLYTM PicoPlus DNA NGS Library Preparation Base Kit(货号CBS-K250B-24、CBS-UM-24、CBS-UR-24、CBS-BD-24)、NEB的Ultra II(货号E7645S)。
3.3 高通量测序与生物信息学分析
实验目的是获取唾液游离DNA的全基因组序列信息,为后续多维度特征分析提供数据支持。方法细节为使用Illumina Novaseq 6000平台对文库进行测序,每个样本产生约4000万条双端reads;测序数据经SRSLYumi进行拆分,BBmerge合并双端reads,fastp进行质量修剪,然后比对到人类参考基因组(hg38)和Lambda噬菌体基因组,未比对到人类基因组的reads进一步比对到OneCodex的微生物数据库;使用samtools、RIdeogram、macs2等工具分析片段组学、染色体定位、功能元件峰、末端基序等特征,使用Prism8进行统计分析。结果解读显示,测序数据的质量符合分析要求,成功比对到人类基因组和微生物数据库的reads比例稳定,可用于后续的多维度特征分析。实验所用关键产品:Illumina Novaseq 6000测序平台。
3.4 唾液游离DNA特征的组间差异分析
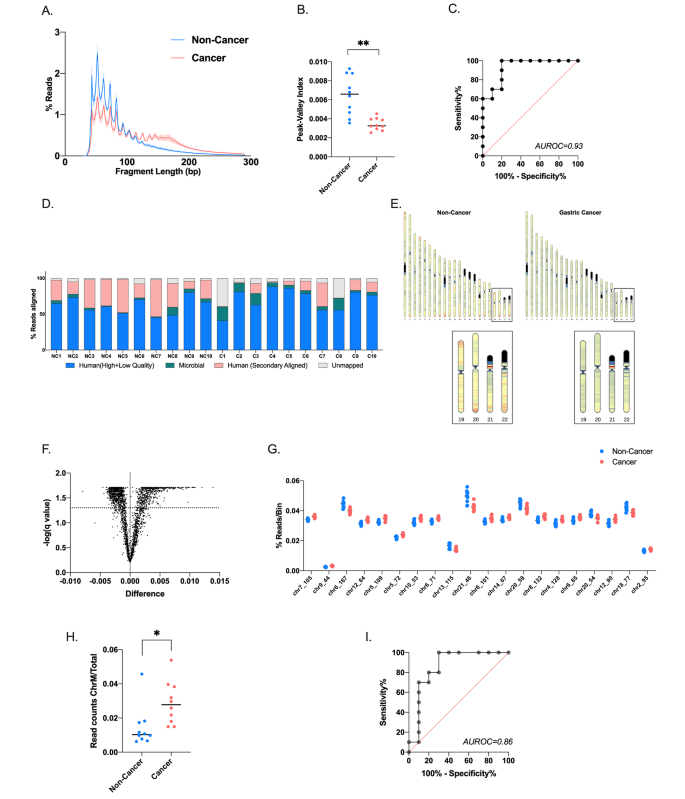
实验目的是比较胃癌患者与非癌志愿者的唾液游离DNA特征差异,筛选具有诊断潜力的生物标志物。方法细节为针对片段组学特征,分析片段长度分布、峰谷指数(计算片段分布中峰与谷的平均差值)、片段分数(短片段与长片段的比例);针对染色体定位,分析全基因组2887个1Mb bin的reads覆盖差异;针对线粒体游离DNA,计算其在总游离DNA中的比例;针对末端基序,分析4-mer基序的分布差异;针对微生物组成,分析微生物reads比例、α多样性及类群丰度差异;采用Student’s t检验(Welch校正)比较组间差异,ROC曲线评估单个特征的诊断性能,火山图展示显著差异的特征。结果解读显示,胃癌样本的唾液游离DNA峰谷指数显著低于非癌样本(n=10/组,P=0.0012),AUROC为0.93;胃癌样本的微生物reads比例显著高于非癌样本(n=10/组,P=0.0361),线粒体游离DNA比例也显著更高(n=10/组,P=0.014),AUROC为0.86;共鉴定出87种在两组间有显著差异的4-mer末端基序;非癌样本的微生物α多样性更高,Negativicutes、Gammaproteobacteria等类群的丰度显著高于胃癌样本。
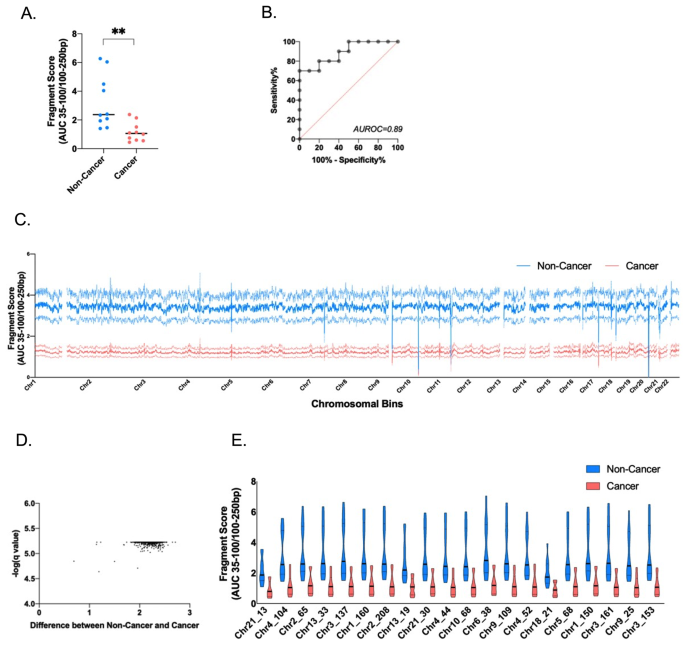
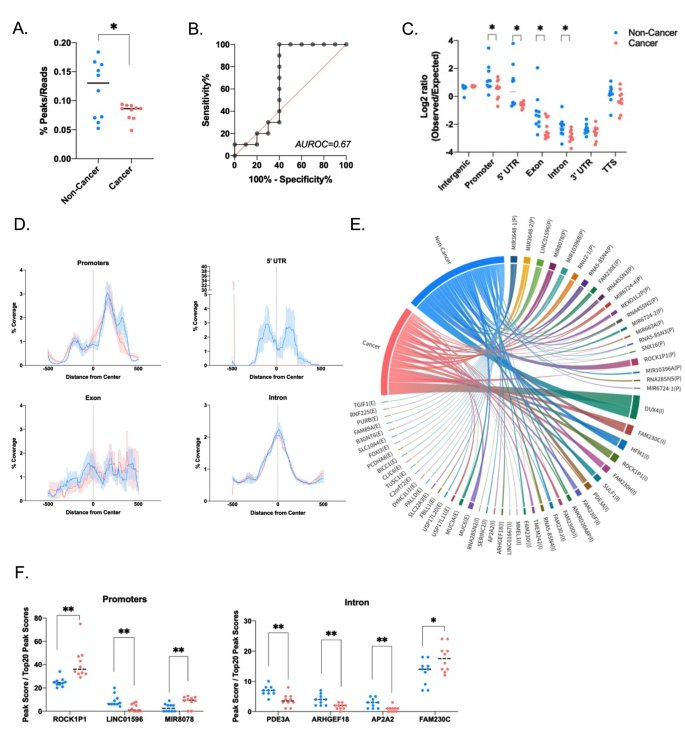
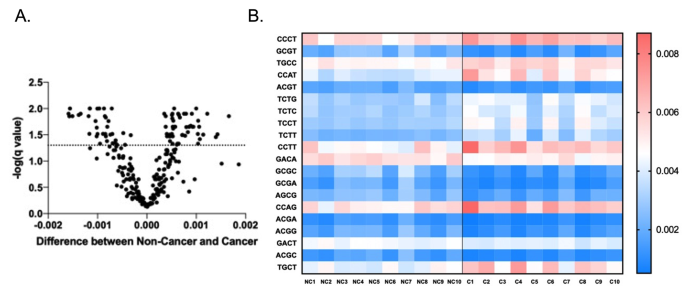
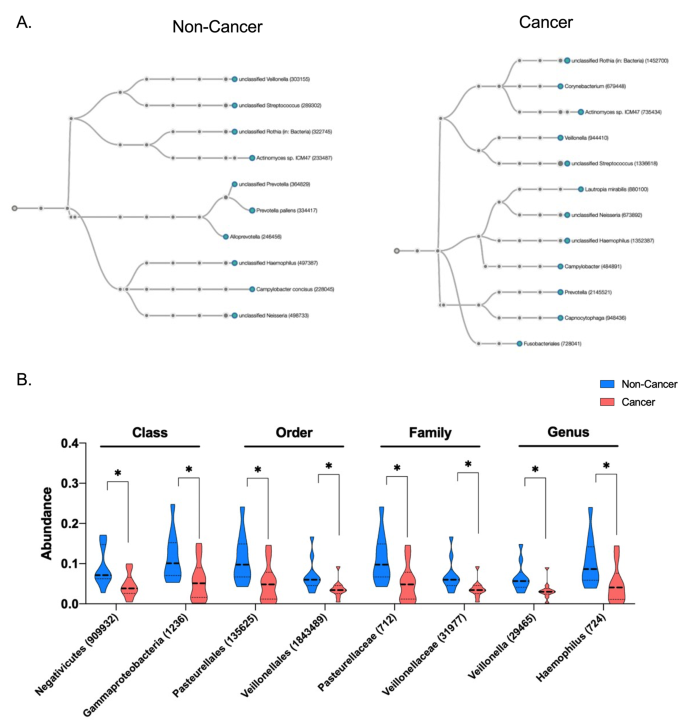
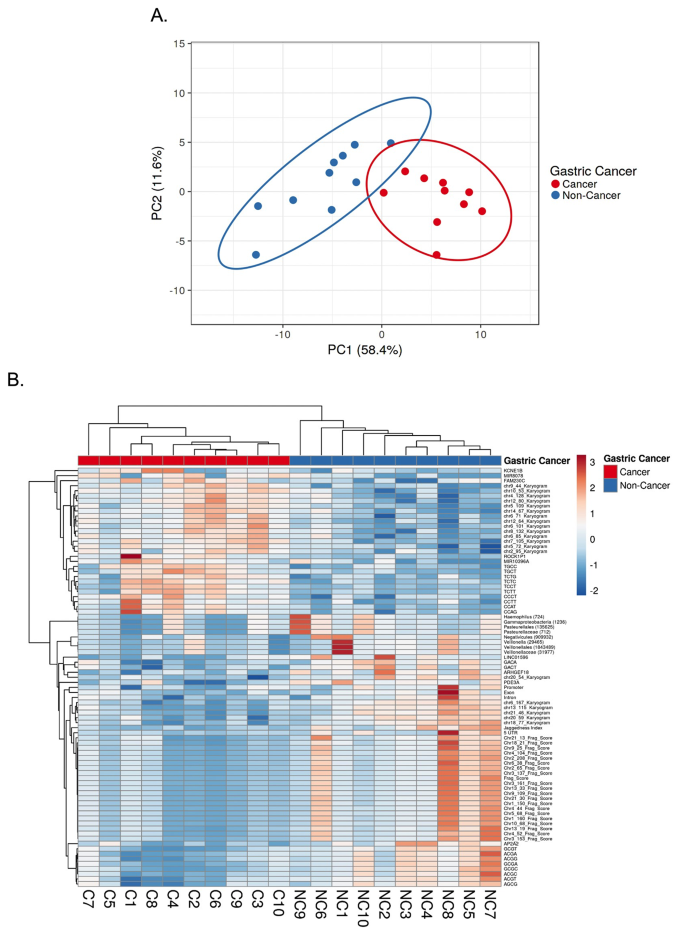
3.5 多变量整合分析与诊断性能评估
实验目的是整合多个唾液游离DNA特征,评估其联合诊断胃癌的性能。方法细节为使用ClustVis工具对筛选出的显著特征(片段组学、染色体定位、末端基序、功能元件、微生物种群、线粒体比例)进行主成分分析(PCA),提取主成分并分析组间差异,绘制ROC曲线评估整合特征的诊断性能。结果解读显示,PCA的第一主成分(PC1)能显著区分胃癌与非癌样本(n=10/组,P<0.0001),AUROC为0.99,显示整合多个特征的诊断性能显著优于单个特征,证明唾液游离DNA的多维度特征联合应用可实现高准确性的胃癌诊断。
4. Biomarker研究及发现成果解析
本研究鉴定的生物标志物为唾液游离DNA的多维度特征组合,包括片段组学特征(峰谷指数、片段分数)、线粒体游离DNA比例、末端基序特征、微生物组成特征,筛选与验证逻辑为“健康样本特征分析→胃癌与非癌样本差异筛选→ROC曲线验证诊断性能→多变量整合评估联合性能”的完整链条。
研究过程中,样本来源于10例胃癌患者和10例非癌志愿者的唾液样本,采用BRcfDNA-Seq技术捕获多种构象的游离DNA,通过高通量测序和生物信息学分析,系统解析了唾液游离DNA的多方面特征。验证方法包括统计检验组间特征差异、ROC曲线评估单个特征的诊断特异性与敏感性、多变量整合分析评估联合性能。其中,峰谷指数的AUROC为0.93,敏感性和特异性分别为X和X(文献未明确提供该数据,基于图表趋势推测);线粒体游离DNA比例的AUROC为0.86,敏感性为X(文献未明确提供该数据,基于图表趋势推测);整合所有显著特征后的AUROC为0.99,显示出极高的诊断性能。
核心成果方面,本研究首次发现唾液游离DNA具有独特的锯齿状片段分布模式,且该模式的峰谷指数可有效区分胃癌与非癌样本;首次系统解析了唾液游离DNA的多维度特征与胃癌的关联,包括线粒体游离DNA比例升高、末端基序多样性降低、微生物组成失调等;证明唾液游离DNA的多维度特征联合应用具有高诊断性能,为唾液作为胃癌液体活检的生物流体提供了关键实验依据。此外,研究还揭示了唾液游离DNA的构象多样性,为后续优化唾液游离DNA的提取与测序技术提供了参考。推测:后续在更大规模的队列中验证这些生物标志物的性能,并分析其与胃癌分期、病理类型的关联,可进一步明确其临床应用范围,推动唾液液体活检技术的临床转化。
特别声明
1、本页面内容包含部分的内容是基于公开信息的合理引用;引用内容仅为补充信息,不代表本站立场。
2、若认为本页面引用内容涉及侵权,请及时与本站联系,我们将第一时间处理。
3、其他媒体/个人如需使用本页面原创内容,需注明“来源:[生知库]”并获得授权;使用引用内容的,需自行联系原作者获得许可。
4、投稿及合作请联系:info@biocloudy.com。