Genomes reveal marked differences in the adaptive evolution between orangutan species
基因组揭示了猩猩物种间适应性进化的显著差异
| 期刊: | Genome Biology | 影响因子: | 9.400 |
| 时间: | 2018 | 起止号: | 2018 Nov 15;19(1):193 |
| doi: | 10.1186/s13059-018-1562-6 | ||
文献解析
1. 领域背景与文献引入
文献英文标题:Genomes reveal marked differences in the adaptive evolution between orangutan species;发表期刊:Genome Biology;影响因子:未公开;研究领域:灵长类进化生物学、群体基因组学
灵长类适应性进化研究是进化生物学与保护生物学的交叉核心领域,其关键发展节点包括2001年人类基因组序列的完成,2010年后大猩猩、黑猩猩等大猿全基因组的陆续解析,推动了从单物种到跨物种的适应性进化机制研究。当前研究热点聚焦于结合种群动态历史与环境变化,解析灵长类应对环境压力的遗传适应基础,尤其是人类近亲大猿的适应性进化模式,为理解人类自身进化及大猿保护策略制定提供参考。然而,当前领域内仍存在核心未解决问题:非人类大猿中同属不同物种对异质环境的适应性进化分化机制尚不明确,缺乏全基因组层面的系统解析与环境关联验证。
此前针对猩猩属(Pongo)的研究多集中于分类学修订、种群数量动态及行为学观察,尚未从全基因组层面系统对比苏门答腊猩猩(Pongo abelii)与婆罗洲猩猩(P. pygmaeus)对岛屿环境差异的适应性进化遗传基础。本研究针对这一空白,利用35只覆盖猩猩属主要种群的全基因组测序数据,结合种群动态模型与环境历史数据,解析两种猩猩的适应性进化差异,揭示环境-种群动态-适应性进化的互作机制,为灵长类进化生物学及大猿保护提供重要理论依据。
2. 文献综述解析
作者对领域内现有研究的分类维度涵盖研究对象(人类vs非人类大猿)、研究时间尺度(远古适应性进化vs近期局部适应)、研究内容(种群动态历史vs适应性遗传机制)三个层面,系统梳理了灵长类适应性进化研究的进展与不足。
在人类适应性进化研究中,已明确高海拔、寒冷、饮食转变等环境压力下的遗传适应机制,涉及肤色、代谢、心血管功能等多个性状,技术方法上全基因组关联分析、群体遗传学模型已成为主流,但其研究范式难以直接迁移至非人类大猿。非人类大猿的适应性进化研究相对滞后,仅在大猩猩、黑猩猩中有部分报道,多聚焦于种群动态历史重建,对适应性遗传机制的解析较为零散,且多数研究未充分结合种群动态历史以排除中性进化的干扰,存在样本量不足、缺乏跨物种对比、未整合环境因子分析等局限性。
本研究通过整合35只猩猩的大样本全基因组数据,构建详细的种群动态模型以校正中性进化干扰,同时采用多维度正选择检测方法,首次系统对比苏门答腊与婆罗洲猩猩的适应性进化差异,并关联岛屿环境历史数据,弥补了此前研究在样本量、分析深度、环境关联方面的不足,为非人类大猿适应性进化研究提供了新的研究范式。
3. 研究思路总结与详细解析
本研究的整体框架为“种群动态历史重建→多时间尺度正选择检测→功能富集与环境关联分析→结论”,研究目标是解析苏门答腊与婆罗洲猩猩对岛屿环境差异的适应性进化遗传基础,核心科学问题是两种猩猩在不同环境压力下的适应性进化模式及关键遗传机制,技术路线形成了从数据获取到机制解析的完整闭环。
3.1 种群样本收集与基因组数据获取
实验目的:获取覆盖猩猩属主要地理种群的高质量全基因组数据,为后续种群动态与适应性进化分析提供可靠基础。
方法细节:收集35只野生或野生来源的猩猩样本,涵盖苏门答腊的东北阿拉斯、西阿拉斯两个种群,以及婆罗洲的东北婆罗洲、中/西加里曼丹两个种群,排除样本量仅为2的打巴奴里猩猩以避免统计偏差;全基因组测序数据来自三个已发表研究,测序覆盖度范围为4.8-31.1x,确保数据质量满足后续分析要求。
结果解读:通过邻接网络分析构建的遗传关系图显示,样本的遗传结构与地理分布高度一致,苏门答腊与婆罗洲猩猩形成明显分化的两大支系,种群内遗传结构与采样区域对应,验证了样本的代表性与数据可靠性。
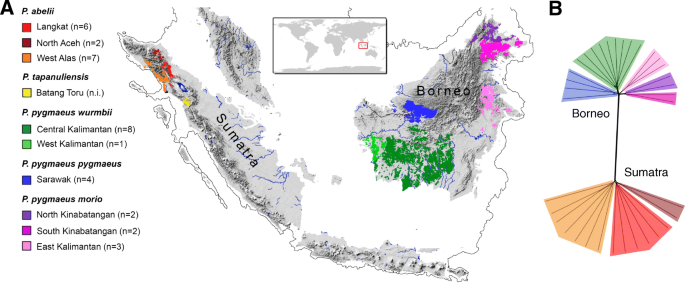
产品关联:文献未提及具体实验产品,领域常规使用Illumina系列高通量测序平台、BWA序列比对软件、GATK变异检测工具等开展全基因组测序与变异分析。
3.2 种群动态历史重建
实验目的:明确苏门答腊与婆罗洲猩猩的分化时间、有效种群大小(Ne)变化及基因流历史,为正选择检测提供种群动态背景以排除中性进化干扰。
方法细节:采用成对序列马尔可夫凝聚(PSMC)模型分析单一个体的有效种群大小随时间的变化,分组时考虑测序覆盖度以避免偏差;采用多序列马尔可夫凝聚(MSMC2)模型分析种群间的基因流,为降低相位误差影响,仅使用雄性X染色体数据;同时采用momi2模型拟合多维度位点频谱,验证PSMC与MSMC2的结果可靠性。
结果解读:PSMC分析显示,苏门答腊猩猩在中更新世有效种群大小持续增加,直至70-80 ka前出现骤降,而婆罗洲猩猩的有效种群大小则呈持续下降趋势;MSMC2分析显示两种猩猩约1 Ma前开始分化,1 Ma至400 ka间基因流完全停止,momi2模型进一步检测到约44 ka前存在少量跨岛屿基因流,与末次冰期陆桥形成的时间一致。
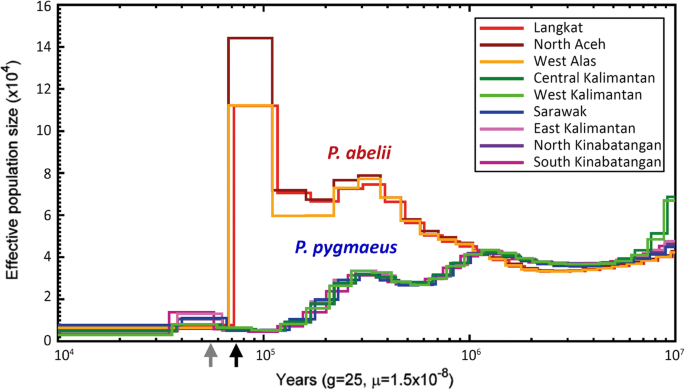
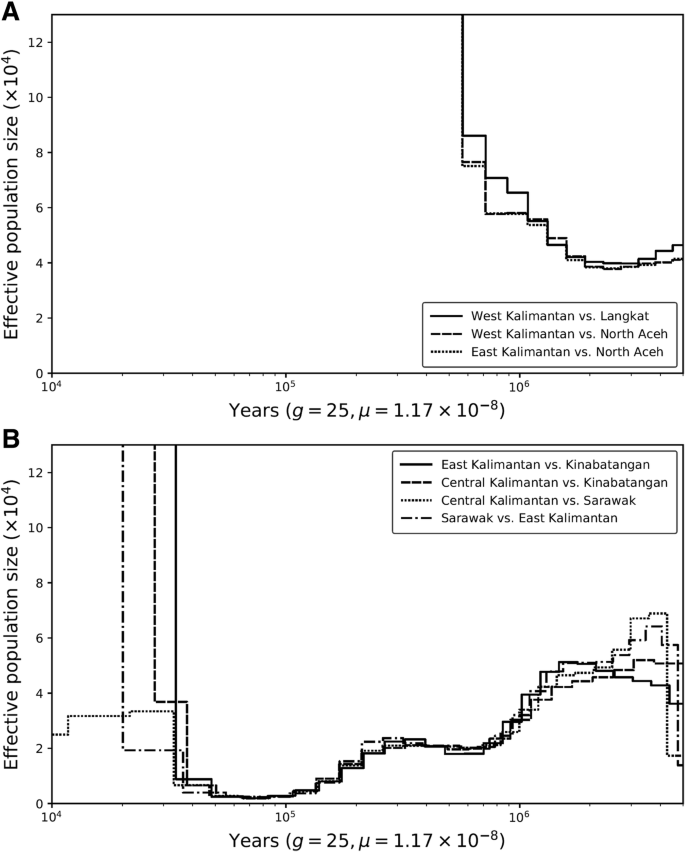
产品关联:文献未提及具体实验产品,领域常规使用PSMC、MSMC2、momi2等群体遗传学分析软件开展种群动态历史重建。
3.3 多时间尺度的正选择检测
实验目的:检测苏门答腊与婆罗洲猩猩在长期进化(物种分化后)和近期进化(种群分化后)过程中的正选择基因,筛选适应性进化的遗传标记。
方法细节:长期进化尺度采用马尔可夫密码子模型(MCM),基于人类、黑猩猩、恒河猴的外群序列,通过分支位点检验检测物种支系上的正选择基因;近期进化尺度采用单倍型积分(iHS)和复合似然比(CLR)两种互补方法,结合基于种群动态模型的中性模拟,确定显著性阈值以降低假阳性,检测基因组中的选择性清除信号。
结果解读:MCM检测显示,婆罗洲东北种群有46个基因存在正选择信号,苏门答腊北部种群有33个基因存在正选择信号;iHS检测在苏门答腊猩猩中鉴定到605个候选基因,婆罗洲猩猩中鉴定到410个候选基因;CLR检测在苏门答腊猩猩中鉴定到658个候选基因,婆罗洲猩猩中鉴定到489个候选基因;三种方法的结果均显示,两种猩猩的正选择基因功能存在显著差异。
产品关联:文献未提及具体实验产品,领域常规使用PAML(马尔可夫密码子模型分析)、rEHH(单倍型积分分析)、SweeD(复合似然比分析)等软件开展正选择检测。
3.4 正选择基因的功能富集与环境关联分析
实验目的:解析正选择基因的功能特征,关联苏门答腊与婆罗洲的环境差异,揭示适应性进化的驱动机制。
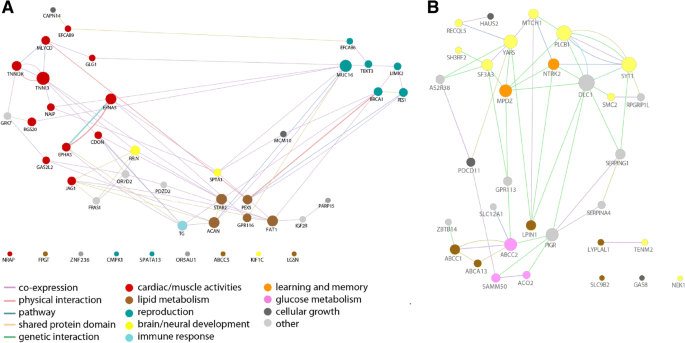
方法细节:采用GeneCards数据库进行基因功能注释,利用Cytoscape构建基因互作网络,通过g:Profiler进行基因本体(GO)富集分析;结合苏门答腊与婆罗洲的环境差异(如苏门答腊森林生产力高、食物资源稳定,婆罗洲森林生产力低、食物资源波动大),分析功能富集结果与环境压力的关联。
结果解读:婆罗洲猩猩的正选择基因显著富集于脂质代谢、心脏和肌肉活动等功能类别,与该岛屿食物资源波动大、环境严酷的特征一致,提示这些基因的正选择有助于猩猩适应能量限制的环境;苏门答腊猩猩的正选择基因显著富集于脑和神经系统发育、学习记忆、葡萄糖代谢等功能类别,与该岛屿环境稳定、种群密度高、文化行为复杂的特征一致,提示这些基因的正选择有助于猩猩发展复杂的认知与社会行为。
产品关联:文献未提及具体实验产品,领域常规使用Cytoscape、g:Profiler、GeneCards等工具开展基因功能分析。
4. Biomarker研究及发现成果解析
本研究中的Biomarker为种群特异性正选择基因,作为猩猩适应性进化的遗传标记,其筛选与验证整合了全基因组测序、多维度正选择检测、功能富集与环境关联分析的完整流程,揭示了猩猩属物种间适应性进化的核心遗传机制。
Biomarker定位:类型为种群特异性适应性进化遗传标记,筛选逻辑为“全基因组多维度正选择检测→功能注释与富集→环境关联验证”,分为长期进化(物种水平)和近期进化(种群水平)两个层面。长期进化层面的标记为物种支系上的正选择基因,近期进化层面的标记为种群内的选择性清除区域相关基因,验证逻辑通过多种正选择检测方法的交叉验证,结合种群动态模型校正中性干扰,确保结果的可靠性。
研究过程详述:Biomarker来源为35只苏门答腊与婆罗洲猩猩的全基因组测序数据,验证方法包括马尔可夫密码子模型(MCM)、单倍型积分(iHS)、复合似然比(CLR)三种正选择检测方法,特异性表现为苏门答腊与婆罗洲猩猩的正选择基因功能完全不同,无显著重叠;敏感性方面,三种方法的联合检测提高了正选择基因的检出效率,其中MCM适用于长期进化尺度,iHS和CLR适用于近期进化尺度。具体数据:婆罗洲猩猩的脂质代谢相关GO术语显著富集(P<0.05,经FDR校正),苏门答腊猩猩的脑发育相关GO术语显著富集(P<0.05,经FDR校正);MCM检测的正选择基因经似然比检验(P<0.05),iHS和CLR检测的候选基因经中性模拟确定的显著性阈值筛选(P<0.05)。
核心成果提炼:首次揭示了猩猩属内同属不同物种对岛屿环境差异的适应性进化遗传机制,苏门答腊猩猩的认知与社会行为相关基因正选择与其复杂文化行为、高种群密度的特征直接关联,婆罗洲猩猩的代谢与生理相关基因正选择与其严酷环境、食物资源波动的特征直接关联;创新性在于整合种群动态历史与环境因子解析适应性进化,为非人类大猿适应性进化研究提供了新的范式;统计学结果显示,所有功能富集分析均经FDR校正(P<0.05),正选择检测结果经严格的统计检验与中性模拟验证,确保了结论的可靠性。
特别声明
1、本页面内容包含部分的内容是基于公开信息的合理引用;引用内容仅为补充信息,不代表本站立场。
2、若认为本页面引用内容涉及侵权,请及时与本站联系,我们将第一时间处理。
3、其他媒体/个人如需使用本页面原创内容,需注明“来源:[生知库]”并获得授权;使用引用内容的,需自行联系原作者获得许可。
4、投稿及合作请联系:info@biocloudy.com。