The genomic signature of resistance to platinum-containing neoadjuvant therapy based on single-cell data
基于单细胞数据的含铂新辅助治疗耐药的基因组特征
| 期刊: | Cell and Bioscience | 影响因子: | 6.100 |
| 时间: | 2023 | 起止号: | 2023 Jun 8;13(1):103. |
| doi: | 10.1186/s13578-023-01061-z | 研究方向: | 细胞生物学 |
| 细胞类型: | 其它细胞 | ||
文献解析
1. 领域背景与文献引入
文献英文标题:The genomic signature of resistance to platinum-containing neoadjuvant therapy based on single-cell data;发表期刊:Cell Bioscience;影响因子:未公开;研究领域:肿瘤学(肺腺癌、食管鳞癌新辅助化疗耐药机制)
根据2023年全球癌症统计数据,恶性肿瘤尤其是肺癌是50岁以上男性和女性的首要癌症死亡原因,而中国2016年癌症新发病例约406.4万,死亡病例约241.35万,癌症仍是各国提高预期寿命的主要障碍。新辅助化疗(NACT)自1980年代起成为晚期肿瘤的一线治疗选择,多项随机研究和荟萃分析显示,新辅助化疗联合手术能显著改善部分晚期实体瘤患者的长期生存,但在未筛选人群中获益有限,甚至可能延误手术或导致肿瘤进展。当前新辅助靶向治疗和免疫治疗成为术前辅助治疗的新趋势,但因价格高昂、仍处于临床试验阶段、适用人群有限等问题,铂类化疗方案仍是多数癌症新辅助或辅助治疗的一线选择或核心组成部分。
现有研究存在的核心问题在于,缺乏精准筛选适合铂类新辅助化疗患者的工具,传统组织水平研究难以解析肿瘤细胞异质性对化疗敏感性的影响,导致无法有效区分获益人群与非获益人群。因此,本研究旨在基于单细胞测序数据,解析铂类新辅助化疗耐药的基因组特征,构建化疗敏感性评分及预测模型,为临床筛选铂类新辅助化疗获益患者提供依据,避免无效治疗带来的不良预后。
2. 文献综述解析
作者对领域内现有研究的分类维度主要包括新辅助化疗的治疗类型(传统铂类化疗、靶向治疗、免疫治疗)、研究技术层面(组织水平组学、单细胞水平组学)、研究应用局限(异质性忽略、精准预测模型缺失)。
现有研究的关键结论显示,新辅助化疗能提高部分晚期实体瘤患者的长期生存,但未经过人群筛选时获益有限,甚至可能带来负面预后影响;新辅助靶向和免疫治疗具有广阔应用前景,但受限于成本、临床试验进展及适用人群占比低等问题,短期内无法替代铂类化疗;铂类化疗的耐药机制涉及细胞黏附、干细胞样表型转化、泛素化调控等多个层面,但尚未完全阐明。技术方法方面,传统组织水平组学能分析肿瘤组织的整体基因表达特征,而单细胞测序技术可解析肿瘤细胞的异质性,更精准地定位肿瘤细胞内的分子变化;但现有研究多基于组织水平,无法区分肿瘤细胞与肿瘤微环境细胞的差异,且缺乏针对铂类新辅助化疗的特异性敏感性评分,已有的预测模型临床验证不足,难以直接应用于临床筛选。
本研究的创新价值在于,首次结合肺腺癌(LUAD)和食管鳞癌(ESCC)患者新辅助化疗前后的单细胞测序数据,以及肿瘤细胞系的顺铂IC50数据,构建跨癌种的新辅助化疗评分(NCS),并建立对应的预测模型,同时在细胞水平验证关键调控基因的功能,弥补了传统组织水平研究忽略肿瘤细胞异质性的不足,为精准筛选铂类新辅助化疗获益患者提供了可验证的工具。
3. 研究思路总结与详细解析
本研究的整体框架为:以“筛选铂类新辅助化疗敏感性标志物并构建预测模型”为研究目标,围绕“铂类新辅助化疗耐药的肿瘤细胞基因组特征及关键调控基因”这一核心科学问题,采用“单细胞数据差异分析→核心基因筛选→评分构建与验证→预测模型建立→细胞功能验证”的闭环技术路线,系统解析铂类新辅助化疗的敏感性调控机制。
3.1 单细胞数据处理与差异基因筛选
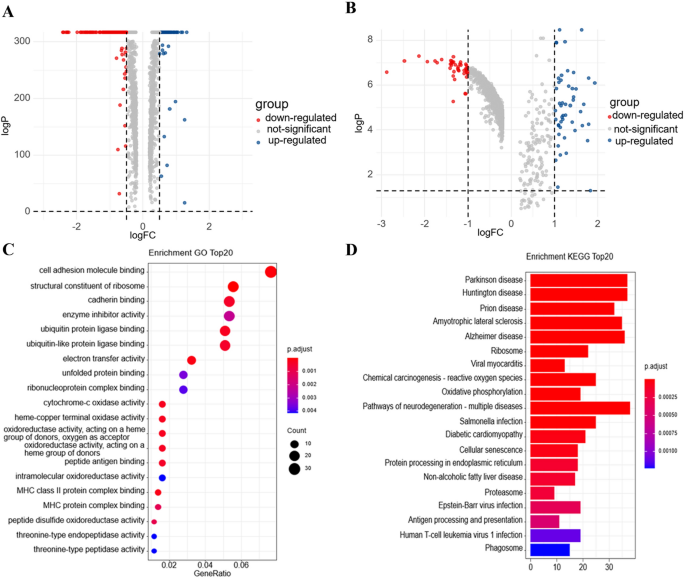
本环节的实验目的是筛选LUAD和ESCC患者新辅助化疗前后肿瘤细胞的差异表达基因,以及与顺铂耐药相关的核心基因。方法细节上,研究收集了LUAD和ESCC患者顺铂新辅助化疗前后的单细胞测序原始数据,采用Cell Ranger软件(版本3.0.0)进行数据处理,包括序列比对、过滤、条形码计数和UMI计数;以P<0.05、错误发现率(FDR)<0.05、|logFC|>1为标准筛选化疗前后肿瘤细胞的差异表达基因,同时结合前期研究中从Cancer Dependency Map(Depmap)和Cancer Cell Line Encyclopedia(CCLE)数据库获得的顺铂耐药相关基因,取交集得到共同差异基因。结果解读显示,LUAD和ESCC新辅助化疗前后的肿瘤细胞共有485个差异表达基因,基因本体(GO)功能富集分析显示这些基因主要集中于细胞黏附分子结合、酶抑制剂活性、钙黏蛋白结合等功能,京都基因与基因组百科全书(KEGG)通路富集分析显示其主要参与代谢、癌变等通路。实验所用关键产品:Cell Ranger软件(版本3.0.0)、R语言(版本3.6.1、4.0.3)。
3.2 新辅助化疗评分(NCS)构建与验证
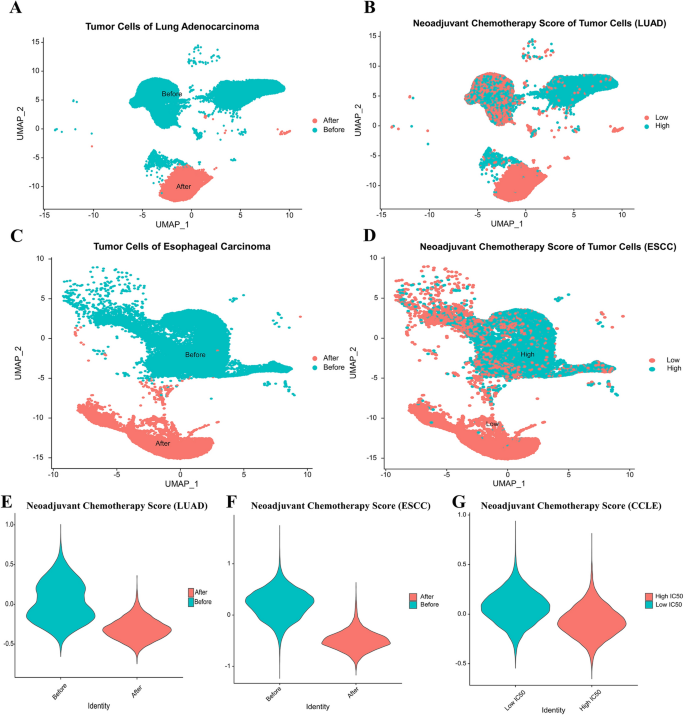
本环节的实验目的是构建基于核心基因的新辅助化疗敏感性评分,并验证其与顺铂敏感性的关联。方法细节上,研究将筛选得到的12个核心基因(CAV2、PHLDA1、DUSP23、VDAC3、DSG2、SPINT2、SPATS2L、IGFBP3、CD9、ALCAM、PRSS23、PERP)构建为新辅助化疗评分(NCS),并在LUAD和ESCC患者新辅助化疗前后的单细胞数据、CCLE数据库的细胞系数据中验证评分与顺铂敏感性的关联;以NCS均值为界将肿瘤细胞分为高低分组,进行差异基因富集分析。结果解读显示,LUAD和ESCC患者新辅助化疗前肿瘤细胞的NCS评分显著高于化疗后,CCLE数据库中顺铂敏感组(低IC50)的NCS评分显著高于耐药组(高IC50);高低NCS分组的差异基因GO富集于钙黏蛋白结合、肌动蛋白结合、肽酶调节活性等功能,KEGG富集于流体剪切应力与动脉粥样硬化、癌症中的蛋白聚糖、转录失调等通路。实验所用关键产品:R语言AddModuleScore函数、Uniform Manifold Approximation and Projection(UMAP)分析工具。
3.3 预测模型构建与生存分析
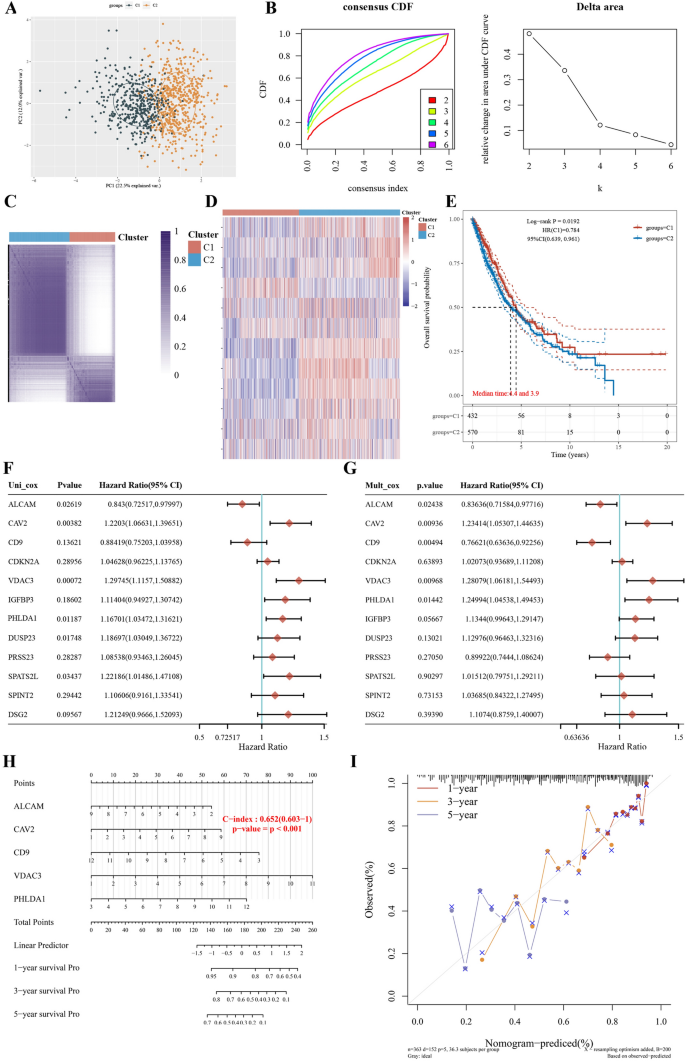
本环节的实验目的是建立NCS高低分组的预测模型,并分析核心基因与患者预后的关联。方法细节上,研究对高低NCS分组的差异基因进行最小绝对收缩和选择算子(LASSO)回归分析,筛选特征变量并通过R语言glm函数构建广义线性预测模型;基于The Cancer Genome Atlas(TCGA)和Gene Expression Omnibus(GEO)数据库,对12个核心基因进行Kaplan-Meier(K-M)生存分析,对LUAD患者进行一致性聚类分析和Cox回归,构建预后预测列线图。结果解读显示,研究筛选出22个特征变量构建预测模型,可有效区分NCS高低分组;CAV2、PHLDA1、ALCAM、CD9、IGFBP3、VDAC3与LUAD化疗患者的预后显著相关(P<0.05),其中CAV2、PHLDA1、VDAC3高表达患者的预后更差;一致性聚类分析将LUAD患者分为两个亚型,两组生存差异显著;多因素Cox回归显示ALCAM、CAV2、CD9、VDAC3、PHLDA1是LUAD患者的独立预后因素,基于这些因素构建的列线图C-index为0.652(95%CI 0.603-1),可预测患者1年、3年、5年的总生存。实验所用关键产品:siRNA(Ribobio)、Lipofectamine 8000(Beyotime)、CCK-8试剂盒(Dojindo)、EdU试剂盒(Sangon Biotech)、兔抗CAV2抗体(Abways,CY5010)、兔抗PHLDA1抗体(Abways,AY3597)、兔抗VDAC3抗体(Proteintech,55260-1-AP)、β-ACTIN抗体(Beyotime,AA128)。
3.4 细胞水平关键基因功能验证
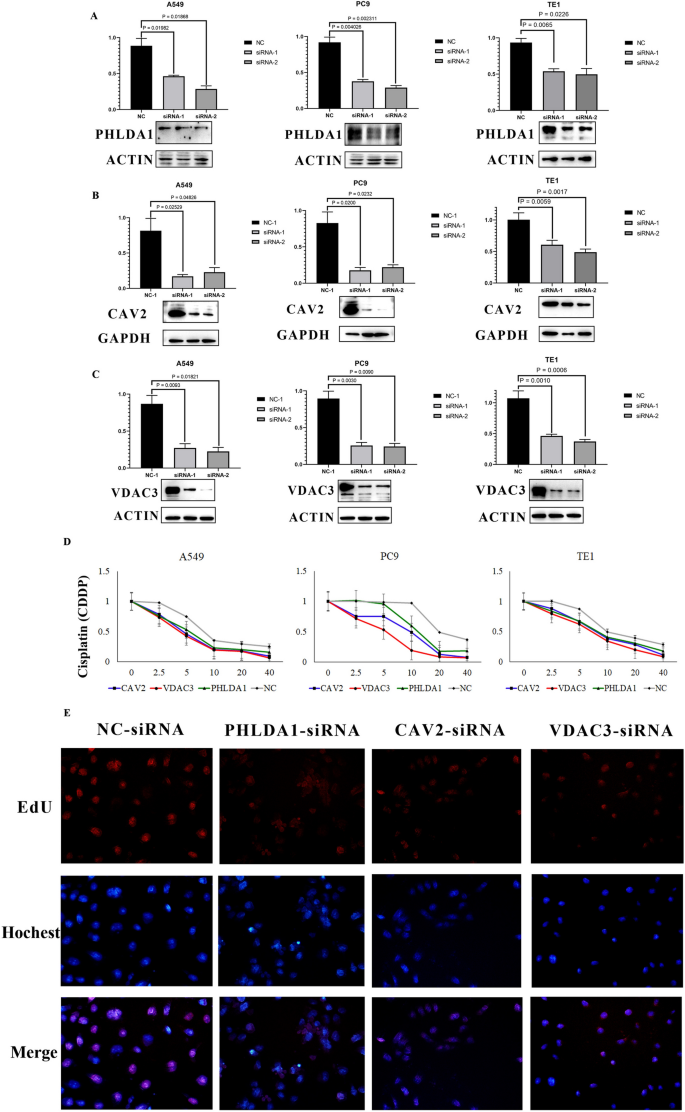
本环节的实验目的是验证CAV2、PHLDA1、VDAC3对肿瘤细胞顺铂敏感性的调控作用。方法细节上,研究在A549、PC9(LUAD)和TE1(ESCC)细胞系中,采用siRNA敲低CAV2、PHLDA1、VDAC3的表达,通过实时荧光定量PCR(qRT-PCR)和蛋白质免疫印迹(WB)验证敲低效率;采用CCK-8实验检测细胞在不同浓度顺铂处理后的活力变化,EdU实验检测细胞增殖能力变化。结果解读显示,siRNA敲低后,三个基因的mRNA和蛋白表达水平均显著降低(n=3,P<0.05);敲低CAV2、PHLDA1、VDAC3后,细胞对顺铂的敏感性显著增加,CCK-8实验显示细胞的顺铂IC50降低,EdU实验显示顺铂处理后的细胞增殖受抑制更明显(n=3,P<0.05)。实验所用关键产品:R语言glmnet包、forestplot包、rms包、K-M plotter在线工具。
4. Biomarker研究及发现成果解析
本研究涉及的Biomarker包括由12个核心基因组成的新辅助化疗评分(NCS),以及单个关键基因CAV2、PHLDA1、VDAC3。筛选与验证逻辑为:首先通过LUAD和ESCC新辅助化疗前后的单细胞数据差异分析,结合顺铂耐药细胞系的基因表达数据,筛选出共同差异基因;随后在单细胞数据和CCLE数据库中验证NCS与顺铂敏感性的关联;在TCGA和GEO数据库中验证单个基因与患者预后的关联;最后在细胞系中验证关键基因对顺铂敏感性的调控功能。
Biomarker的来源为LUAD和ESCC患者新辅助化疗前后的肿瘤单细胞数据、CCLE数据库的肿瘤细胞系数据、TCGA和GEO数据库的临床样本数据。验证方法包括单细胞数据的UMAP分析、小提琴图分析,CCLE数据库的IC50关联分析,临床数据库的K-M生存分析、Cox回归分析,以及细胞系的siRNA敲低、CCK-8、EdU实验。特异性与敏感性方面,NCS可有效区分顺铂敏感与耐药细胞系,预测模型可区分NCS高低分组;CAV2、PHLDA1、VDAC3高表达与LUAD患者的不良预后显著相关(P<0.05),敲低这些基因可显著增加细胞对顺铂的敏感性。
核心成果提炼显示,NCS评分越高,患者对顺铂新辅助化疗的敏感性越高;CAV2、PHLDA1、VDAC3是顺铂耐药的关键调控基因,其高表达与LUAD患者不良预后相关,敲低后可逆转细胞的顺铂耐药;构建的预测模型可辅助临床筛选适合顺铂新辅助化疗的患者,为精准治疗提供依据。本研究的创新性在于首次基于单细胞数据构建跨癌种的铂类新辅助化疗敏感性评分,弥补了传统组织水平研究忽略肿瘤细胞异质性的不足,为铂类新辅助化疗的获益人群筛选提供了新的工具。
特别声明
1、本页面内容包含部分的内容是基于公开信息的合理引用;引用内容仅为补充信息,不代表本站立场。
2、若认为本页面引用内容涉及侵权,请及时与本站联系,我们将第一时间处理。
3、其他媒体/个人如需使用本页面原创内容,需注明“来源:[生知库]”并获得授权;使用引用内容的,需自行联系原作者获得许可。
4、投稿及合作请联系:info@biocloudy.com。