Pharmacogenomic analysis of patient-derived tumor cells in gynecologic cancers
妇科癌症患者来源肿瘤细胞的药物基因组学分析
| 期刊: | Genome Biology | 影响因子: | 10.100 |
| 时间: | 2019 | 起止号: | 2019 Nov 26;20(1):253. |
| doi: | 10.1186/s13059-019-1848-3 | 研究方向: | 细胞生物学、肿瘤 |
| 细胞类型: | 肿瘤细胞 | ||
文献解析
1. 领域背景与文献引入
文献英文标题:Pharmacogenomic analysis of patient-derived tumor cells in gynecologic cancers;发表期刊:Genome Biology;影响因子:17.906(2019年);研究领域:妇科肿瘤精准医学。
妇科恶性肿瘤是全球女性成人死亡的主要原因之一,精准肿瘤学的核心原则是通过肿瘤分子谱分析为个体患者匹配最适宜的治疗方案。领域发展的关键节点包括2011、2013及2017年癌症基因组图谱(TCGA)研究网络分别完成卵巢癌、子宫内膜癌及宫颈癌的大规模基因组表征,揭示了驱动肿瘤发生发展的核心分子畸变,但这些分子靶向治疗的临床应用潜力仍不明确。当前研究热点聚焦于患者来源肿瘤细胞(PDC)模型的药物基因组学分析,这类模型更贴近患者肿瘤的分子特征,有望解决传统长期培养癌细胞系与临床肿瘤的分子、药理学差异问题。领域未解决的核心问题在于,现有妇科肿瘤标准治疗(手术联合铂类-紫杉烷化疗)后,约25%的患者会在6个月内出现肿瘤复发,且缺乏可及的替代治疗方案;同时针对妇科肿瘤不同亚型的个性化治疗靶点与预测生物标志物仍较为匮乏,限制了精准治疗的落地。
针对上述研究空白,本研究建立了包含139例妇科肿瘤的PDC库,整合基因组测序、转录组测序及37种分子靶向药物的敏感性分析,旨在系统揭示妇科肿瘤不同亚型的谱系特异性药物敏感性,鉴定可指导个性化治疗的分子生物标志物,为妇科肿瘤精准治疗提供新的理论依据与实践方向。
2. 文献综述解析
作者围绕“精准肿瘤学的临床转化瓶颈”“现有研究模型的局限性”“妇科肿瘤靶向治疗的挑战”三个维度对领域内研究进行分类评述,明确了传统研究的核心结论、技术局限及本研究的创新定位。
现有研究已证实精准肿瘤学的核心价值在于通过肿瘤分子谱指导治疗选择,大规模癌细胞系药物基因组分析为药物敏感性的基因组标记物鉴定提供了参考框架,但传统长期培养的癌细胞系与患者肿瘤存在显著的分子及药理学差异,导致其基因-药物图谱的临床转化价值受限。TCGA等大规模基因组研究虽已揭示卵巢、子宫及宫颈癌的核心分子畸变,但靶向这些畸变的治疗常因肿瘤基因组的复杂性及多条细胞生存通路的同时激活而失败,无法满足临床个性化治疗需求。PDC模型作为更贴近患者肿瘤的研究体系,已被证实可用于解析动态基因-药物关联,但针对妇科肿瘤不同亚型的系统PDC药物基因组学研究仍处于空白阶段,缺乏针对PARP抑制剂等热门靶向药物的特异性预测生物标志物。
与现有研究相比,本研究的核心创新在于首次建立了覆盖宫颈癌、子宫内膜癌、上皮性卵巢癌及子宫肉瘤的大规模妇科肿瘤PDC库,通过整合多组学与药物敏感性数据,不仅揭示了妇科肿瘤不同亚型的谱系特异性药物敏感性,还首次发现TP53突变可作为PARP抑制剂奥拉帕利的广谱预测生物标志物,同时鉴定出ID2转录组表达与奥拉帕利耐药的关联,填补了妇科肿瘤精准治疗靶点与生物标志物研究的关键空白,为临床个性化治疗方案的制定提供了直接依据。
3. 研究思路总结与详细解析
本研究的整体研究目标是建立具有临床相关性的妇科肿瘤PDC模型库,解析其药物基因组学特征,筛选可指导个性化治疗的分子标志物;核心科学问题聚焦于妇科肿瘤不同亚型的药物敏感性差异及潜在分子机制,以及PARP抑制剂奥拉帕利的敏感性预测生物标志物;技术路线遵循“样本收集→PDC库建立与验证→多组学测序分析→药物敏感性筛选→生物标志物鉴定与功能验证→临床意义分析”的闭环逻辑,确保研究结果的可靠性与临床转化价值。
3.1 妇科肿瘤患者来源细胞库的建立与验证
实验目的:建立保留患者肿瘤分子特征的PDC库,验证其作为妇科肿瘤药物筛选模型的可靠性与临床相关性。方法细节:研究团队收集139例妇科肿瘤手术标本,包括18例宫颈癌、29例子宫/子宫内膜癌、92例上皮性卵巢癌,将肿瘤组织在添加表皮生长因子(EGF)和碱性成纤维细胞生长因子(FGF)的无血清培养基中培养2-4周,富集肿瘤起始细胞;对129例样本进行靶向外显子测序以鉴定基因组变异,51例样本进行全转录组测序分析基因表达谱;同时建立患者来源异种移植(PDX)模型,通过组织病理学分析验证PDC的肿瘤源性。结果解读:靶向外显子测序结果显示,PDC中保留了亲本肿瘤的主要驱动基因突变,包括TP53、ERBB3、EGFR及BRAF等,转录组分析显示PDC与亲本肿瘤的基因表达谱呈强正相关;PDX模型完全重现了亲本肿瘤的组织形态与病理特征,证实该PDC库可作为反映患者肿瘤真实分子特征的药物筛选模型。产品关联:文献未提及具体实验产品,领域常规使用QIAamp DNA提取试剂盒、Illumina测序平台、ATPLite细胞活力检测试剂盒等试剂与仪器。
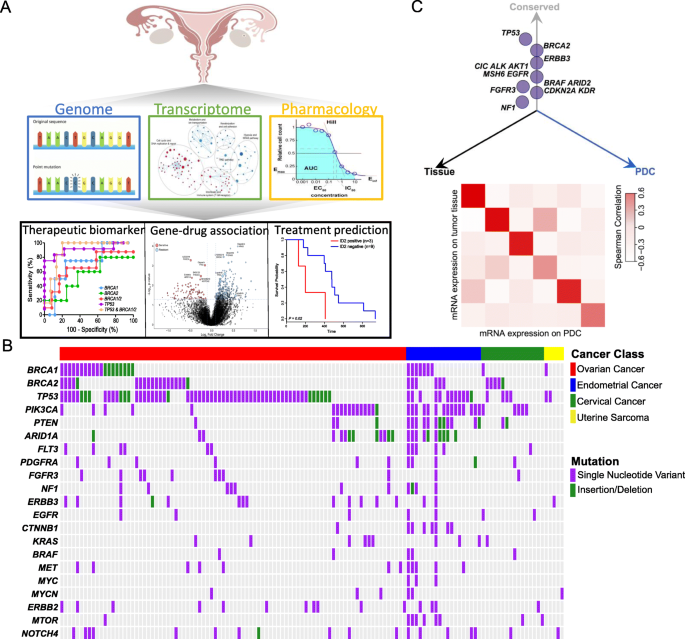
3.2 妇科肿瘤谱系特异性药物敏感性分析
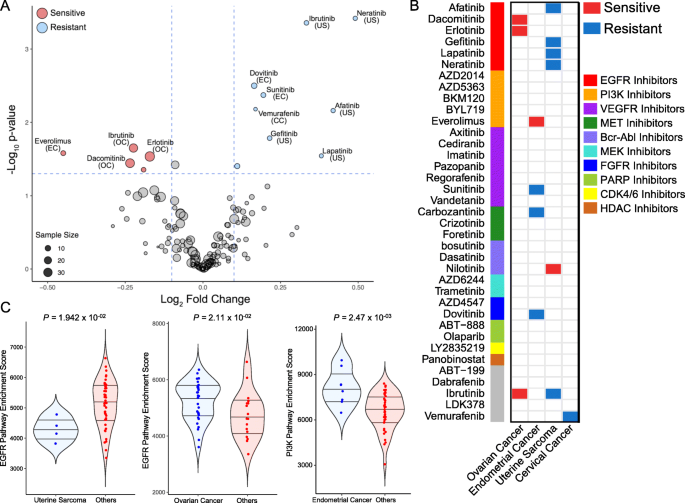
实验目的:系统分析不同妇科肿瘤亚型的药物敏感性差异,解析其背后的分子通路机制。方法细节:选取66例PDC(6例宫颈癌、10例子宫内膜癌、8例子宫肉瘤、42例上皮性卵巢癌)进行37种分子靶向药物的敏感性筛选,通过剂量反应曲线下面积(AUC)量化药物敏感性;采用Wilcoxon秩和检验比较不同肿瘤亚型的药物敏感性差异,通过基因集富集分析(GSEA)解析差异通路的激活状态。结果解读:研究发现上皮性卵巢癌对多种EGFR抑制剂(如厄洛替尼、达可替尼)表现出更高的敏感性(P值分别为2.91×10^-02、3.59×10^-02),而子宫肉瘤对这类EGFR抑制剂普遍耐药(P值分别为3.81×10^-04、6.91×10^-03);子宫内膜癌对mTOR抑制剂依维莫司的敏感性显著高于其他亚型,通路富集分析显示上皮性卵巢癌中EGFR通路激活,子宫肉瘤中EGFR通路下调,子宫内膜癌中PI3K通路富集,与药物敏感性结果完全一致。产品关联:文献未提及具体实验产品,领域常规使用Selleckchem药物库、GraphPad Prism软件进行剂量反应曲线拟合与分析。
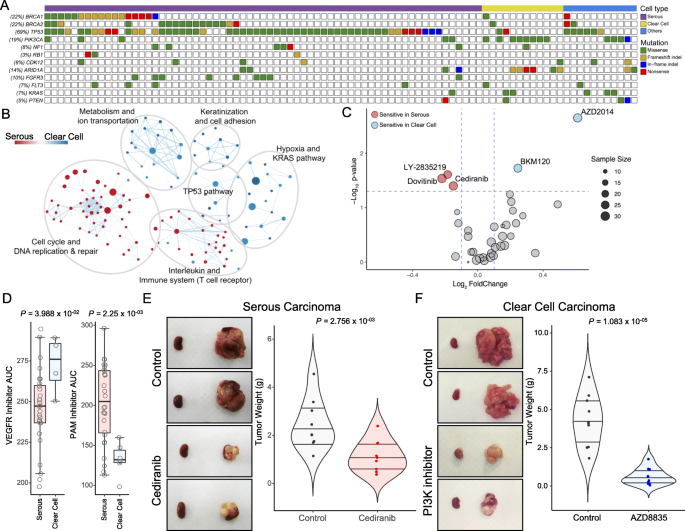
3.3 上皮性卵巢癌亚型的药物基因组学分析
实验目的:解析上皮性卵巢癌主要亚型(高级别浆液性癌HGSC、透明细胞癌)的基因组特征与药物敏感性差异,为亚型特异性治疗提供依据。方法细节:对上皮性卵巢癌PDC进行靶向外显子测序与全转录组测序,比较HGSC与透明细胞癌的基因突变频率及通路富集状态;通过Wilcoxon秩和检验分析两种亚型对37种分子靶向药物的敏感性差异,并利用PDX模型进行体内治疗效果验证。结果解读:基因组分析显示,HGSC中TP53突变率高达82%,BRCA1/2突变率分别为26%与25%,通路富集分析显示细胞周期与DNA修复相关通路显著激活;透明细胞癌中PIK3CA与ARID1A突变率分别为67%与50%,代谢、缺氧及KRAS通路激活更为显著;药物敏感性分析显示HGSC对多激酶抑制剂(如多韦替尼、西地尼布)更敏感,透明细胞癌对PI3K-AKT-mTOR(PAM)通路抑制剂更敏感,PDX模型体内实验进一步验证了西地尼布对HGSC、PI3K抑制剂对透明细胞癌的治疗有效性。产品关联:文献未提及具体实验产品,领域常规使用Gene Set Enrichment Analysis(GSEA)软件进行通路富集分析。
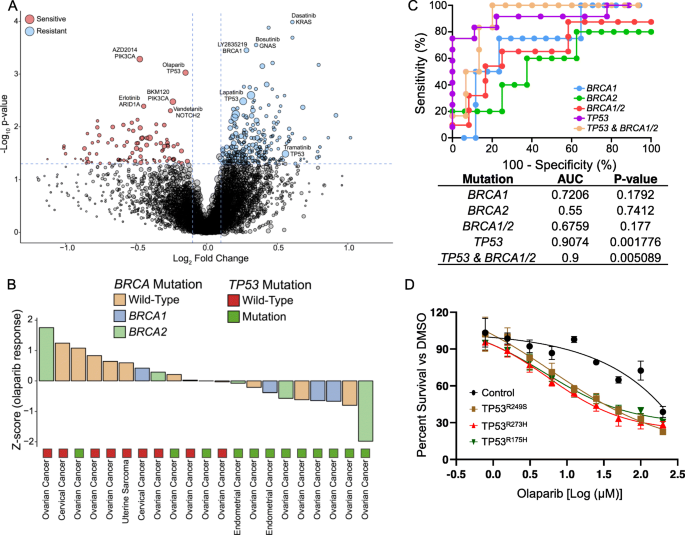
3.4 妇科肿瘤药物敏感性的基因组生物标志物鉴定
实验目的:鉴定妇科肿瘤药物敏感性的基因组生物标志物,重点解析PARP抑制剂奥拉帕利的敏感性预测因子。方法细节:通过Wilcoxon秩和检验分析单个基因突变与37种药物敏感性的关联;构建稳定表达TP53突变体(R273H、R249S、R175H)的卵巢癌细胞系,验证TP53突变对奥拉帕利敏感性的调控作用;采用受试者工作特征(ROC)曲线分析生物标志物的预测效能。结果解读:研究发现PIK3CA突变是PAM通路抑制剂敏感性的强预测因子,携带该突变的肿瘤对AZD2014(mTOR抑制剂)及BKM120(PI3K抑制剂)的敏感性显著更高(P值分别为5.20×10^-04、3.34×10^-03);TP53突变肿瘤对奥拉帕利的敏感性显著高于野生型肿瘤(P=9.39×10^-04),ROC曲线显示TP53突变联合BRCA1/2突变的预测AUC达0.9,稳定表达TP53突变体的细胞系中奥拉帕利的IC50显著降低,其中R249S突变体的log(IC50)为1.269 μM(95% CI 1.177-1.362),远低于野生型的2.155 μM(95% CI 2.055-2.259)。产品关联:文献未提及具体实验产品,领域常规使用Addgene慢病毒载体、Lipofectamine转染试剂构建稳定细胞系。
3.5 奥拉帕利敏感性的转录组生物标志物鉴定
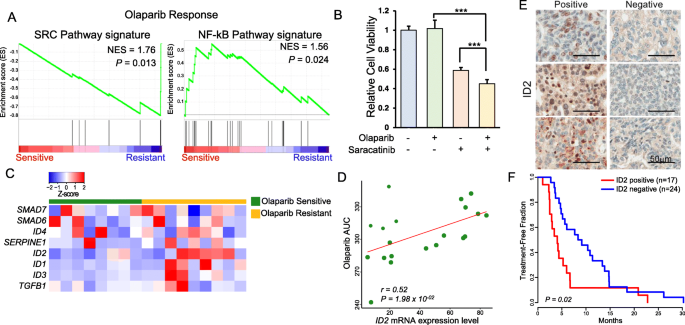
实验目的:鉴定奥拉帕利敏感性的转录组生物标志物,解析上皮性卵巢癌对奥拉帕利的耐药机制。方法细节:对上皮性卵巢癌PDC进行全转录组测序,通过基因集富集分析(GSEA)比较奥拉帕利敏感与耐药样本的通路激活差异;分析ID2基因表达与奥拉帕利耐药的相关性,并通过回顾性临床样本的免疫组化(IHC)检测与Kaplan-Meier生存分析验证其临床意义。结果解读:通路富集分析显示奥拉帕利耐药样本中SRC通路显著激活,其中ID1/2/3基因的mRNA表达在耐药样本中显著上调,尤其是ID2的转录组表达水平与奥拉帕利耐药呈显著正相关(r=0.52,P=0.01978);对41例接受奥拉帕利治疗的BRCA突变HGSC患者的生存分析显示,ID2低表达患者的无治疗生存期显著延长,中位生存期为8.73个月(95% CI 5.60-13.87),而ID2高表达患者仅为4.03个月(95% CI 2.87-6.67)(P=0.02)。产品关联:实验所用关键产品:Novus Biologicals的ID2单克隆抗体(货号NBP2-66898)。
4. Biomarker研究及发现成果
本研究鉴定了两类可指导妇科肿瘤精准治疗的生物标志物,包括基因组层面的TP53、PIK3CA及BRCA1/2突变,以及转录组层面的ID2基因表达,这些标志物覆盖了药物敏感性预测与耐药风险评估两大临床需求,具有重要的转化价值。
Biomarker定位与筛选逻辑
基因组生物标志物的筛选遵循“TCGA数据库已知驱动基因→PDC样本测序验证→药物敏感性关联分析→细胞系功能验证”的完整逻辑,其中TP53突变作为奥拉帕利敏感性的预测标志物,首次突破了BRCA突变的限制,可覆盖更广泛的妇科肿瘤患者;转录组生物标志物ID2的筛选则通过“全转录组测序差异分析→相关性验证→临床样本生存分析”的流程,明确其作为奥拉帕利耐药标志物的临床意义。
研究过程详述
TP53突变的检测来源于139例妇科肿瘤标本的靶向外显子测序,验证实验通过构建稳定表达TP53突变体的卵巢癌细胞系完成,其预测奥拉帕利敏感性的ROC曲线AUC为0.9074,特异性与敏感性均表现优异;PIK3CA突变同样通过靶向外显子测序鉴定,可预测PAM通路抑制剂的敏感性,携带该突变的肿瘤对AZD2014的敏感性显著更高(P=5.20×10^-04);ID2表达的检测基于51例样本的全转录组测序,临床验证采用免疫组化检测41例HGSC患者的肿瘤组织,相关性分析显示ID2表达与奥拉帕利耐药的相关系数为0.52(P=0.01978),生存分析进一步证实其临床价值。
核心成果提炼
本研究的核心Biomarker成果包括三个方面,一是首次证实TP53突变是妇科肿瘤对奥拉帕利敏感的广谱预测标志物,无论肿瘤组织学亚型,携带TP53突变的肿瘤均对奥拉帕利表现出更高敏感性,为PARP抑制剂的临床拓展应用提供了依据;二是明确PIK3CA突变可作为子宫内膜癌对PAM通路抑制剂敏感的特异性标志物,为该亚型患者的个性化治疗提供了靶点;三是鉴定ID2高表达为上皮性卵巢癌奥拉帕利耐药的生物标志物,低ID2表达的BRCA突变HGSC患者接受奥拉帕利治疗的无治疗生存期显著延长(中位生存期8.73个月vs 4.03个月,P=0.02,95% CI: ID2阳性2.87~6.67 vs ID2阴性5.60~13.87),为临床耐药风险评估提供了新的工具。
特别声明
1、本页面内容包含部分的内容是基于公开信息的合理引用;引用内容仅为补充信息,不代表本站立场。
2、若认为本页面引用内容涉及侵权,请及时与本站联系,我们将第一时间处理。
3、其他媒体/个人如需使用本页面原创内容,需注明“来源:[生知库]”并获得授权;使用引用内容的,需自行联系原作者获得许可。
4、投稿及合作请联系:info@biocloudy.com。