A novel semi-automatic image processing approach to determine Plasmodium falciparum parasitemia in Giemsa-stained thin blood smears
一种用于检测吉姆萨染色薄血涂片中恶性疟原虫寄生虫血症的新型半自动图像处理方法
| 期刊: | BMC Cell Biology | 影响因子: | 0.000 |
| 时间: | 2008 | 起止号: | 2008 Mar 28;9:15 |
| doi: | 10.1186/1471-2121-9-15 | 研究方向: | 微生物学 |
文献解析
1. 领域背景与文献引入
文献英文标题:A novel semi-automatic image processing approach to determine Plasmodium falciparum parasitemia in Giemsa-stained thin blood smears;发表期刊:BMC Cell Biology;影响因子:未公开;研究领域:疟疾诊断与医学图像分析
疟疾是全球范围内的重要传染性疾病,疟原虫血症(血液中疟原虫的相对含量)是临床诊断病情严重程度、评估抗疟药物疗效的核心指标。领域共识:传统的疟原虫血症检测依赖显微镜下人工计数吉氏染色薄血涂片,该方法虽为金标准,但存在耗时费力、结果易受检测人员经验影响、人为误差大等局限。随着医学图像技术发展,自动化疟原虫血症检测方法成为研究热点,但现有方法多依赖“标准样本模型”假设,仅能处理染色均匀、细胞分散的理想样本,无法应对实际检测中常见的细胞重叠、涂片染色不均、图像失焦等非标准情况,导致鲁棒性不足,难以推广至大规模筛查场景。针对这一研究空白,本研究开发了一种基于比较分析的半自动图像处理方法,通过利用不同图像与颜色通道的关联关系,放松模型假设,提升对非标准样本的检测能力,为疟疾低成本大规模筛查提供技术支撑。
2. 文献综述解析
作者按图像处理技术类型对现有疟原虫血症自动检测研究进行分类,涵盖边缘检测与细胞团分割、形态学与阈值技术、霍夫空间峰值选择、分水岭变换四大类。现有研究中,边缘检测方法对染色均匀、细胞分散的样本检测效果较好,能实现较高的检测效率,但面对细胞重叠样本时,细胞边界识别准确性显著下降;形态学与阈值技术通过图像灰度特征分割细胞,虽有一定应用前景,但对图像质量高度敏感,仅适用于符合“细胞圆形均匀”假设的样本;霍夫空间方法将红细胞检测转化为峰值选择问题,但严格依赖“红细胞为圆形均匀大小”的假设,无法适配实际样本中细胞形态的变异;分水岭变换利用局部最大值识别细胞中心,仅能处理低细胞重叠的图像,重叠率升高时会出现严重的过分割问题。这些方法的共同局限是依赖严格的样本模型假设,难以应对实际检测中样本制备和图像采集的各种误差,鲁棒性不足。本研究的创新价值在于突破了传统方法的模型限制,采用比较分析方法,通过不同图像观测和辐射表示的关联,结合统计测量与交叉验证,能够处理染色不均、细胞重叠、失焦等非标准样本,同时保持与人工计数相当的检测准确性,填补了非标准样本自动化检测的技术空白。
3. 研究思路总结与详细解析
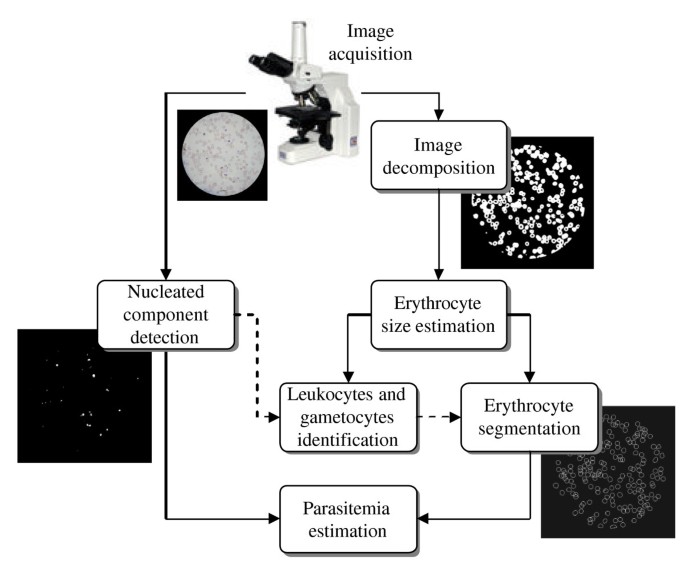
整体研究框架是构建包含六个核心步骤的半自动图像分析流程,从有核成分检测开始,经图像分解、红细胞大小估算、白细胞与配子体识别、红细胞分割,最终实现疟原虫血症的准确估算,形成“样本采集-图像分析-多维度验证”的闭环逻辑,核心科学问题是解决实际样本中非标准情况对自动化检测的干扰,技术路线以“鲁棒性优先”为原则,通过多通道关联分析替代单一模型假设。
3.1 样本制备与图像采集
实验目的是获取包含不同疟原虫感染状态、细胞重叠程度、图像质量的吉氏染色薄血涂片图像,为后续分析提供多样化的验证样本。方法细节:培养恶性疟原虫克隆,调整细胞悬液浓度制备不同重叠程度的薄血涂片,用Sigma-Aldich的吉氏染液1:5稀释染色300秒;使用Nikon YS 100光学显微镜(100×油镜+10×目镜)连接Nikon CoolPix 8400 CCD相机,以1600×1200分辨率、f/5.7光圈、1/125秒曝光时间采集图像,共获取225张随机位置的涂片图像,覆盖细胞重叠、染色不均、失焦等多种实际场景。结果解读:成功制备包含疟原虫不同生命周期阶段、不同细胞密度的样本,为方法的鲁棒性验证提供了全面的数据基础。实验所用关键产品:Sigma-Aldich的吉氏染液、Nikon YS 100光学显微镜、Nikon CoolPix 8400 CCD相机。
3.2 有核成分检测
实验目的是准确识别图像中的疟原虫、白细胞等有核成分,为后续红细胞分割和感染判断奠定基础。方法细节:利用蓝色与绿色通道的强度差突出有核成分,采用Zack阈值算法结合半径为2的圆盘形态学开运算去除噪声,通过图像强度分布的偏度验证判断样本中是否存在有核成分(偏度<1.2时判定存在)。结果解读:该方法有效区分有核成分与红细胞,在225张样本图像中稳定检测出有核区域,避免了单一颜色通道检测的局限性,减少了假阳性结果。
文献未提及具体实验产品,领域常规使用数字图像处理软件(如MATLAB)完成分析。
3.3 图像分解
实验目的是将图像中的背景与细胞等固体成分分离,消除非均匀光照和光学污染的影响。方法细节:将样本灰度图像与相同条件下采集的空白载玻片灰度图像做差,通过两次Zack阈值算法分割背景与固体成分,结合欧拉数检测并填充红细胞中心因过曝光产生的空洞。结果解读:成功补偿了非均匀光照和光学污染的影响,准确分离出细胞区域,为后续细胞分割提供了清晰的图像基础。文献未提及具体实验产品,领域常规使用MATLAB等图像处理工具实现。
3.4 红细胞大小估算与白细胞/配子体识别
实验目的是确定红细胞的尺寸范围,排除白细胞、疟原虫配子体等大细胞对红细胞分割的干扰。方法细节:通过用户交互标记单个红细胞,基于95%置信区间确定红细胞尺寸范围;利用有核成分区域与红细胞平均面积的差异(大于平均面积+2倍标准差)识别白细胞和配子体并去除。结果解读:准确划定了红细胞的尺寸范围,有效排除了大细胞成分的干扰,提升了后续红细胞分割的准确性。文献未提及具体实验产品,领域常规使用人工交互标注工具完成。
3.5 红细胞分割
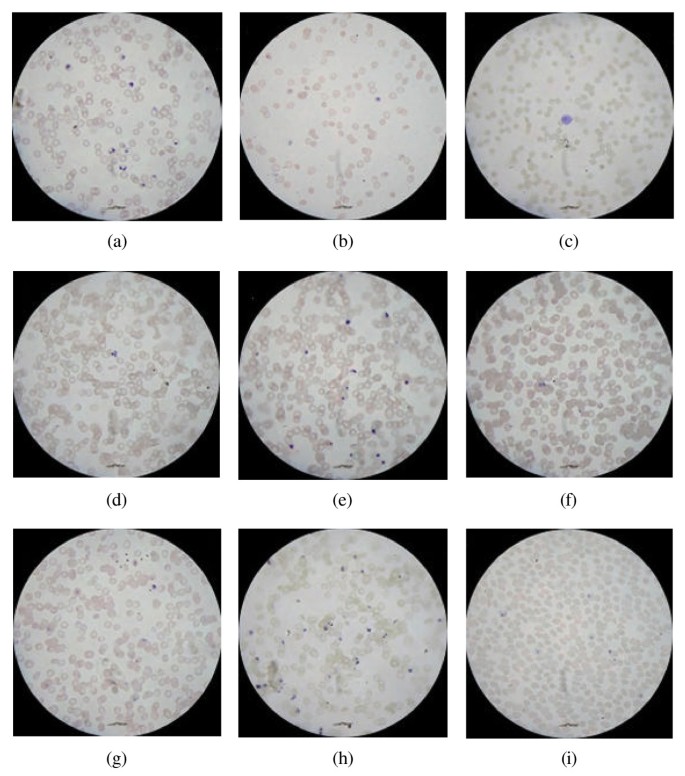
实验目的是实现单个红细胞及重叠红细胞团的准确分割,解决实际样本中细胞重叠的核心问题。方法细节:对单个红细胞进行欧氏距离变换记录峰值,对红细胞团通过迭代检测区域最大值实现分割,采用F值(精确率与召回率的加权调和平均)评估分割性能。结果解读:对于聚焦良好、染色均匀的样本,即使细胞重叠率达50%仍可实现有效分割,9组测试图像的F值普遍超过92%,仅在重度重叠(如Image 2(f))时性能略有下降,证明方法对细胞重叠的鲁棒性优于现有技术。
文献未提及具体实验产品,领域常规使用MATLAB的图像处理工具箱完成分割算法实现。
3.6 疟原虫血症估算与验证
实验目的是验证自动检测方法的准确性与鲁棒性,对比人工计数结果评估性能。方法细节:选取9张涵盖细胞重叠、染色不均、失焦等多种实际问题的测试图像,由四位具有4-12年经验的疟原虫学家手动计数,将自动检测结果与手动计数的中位数对比,计算相关性、误差率;同时用约氏疟原虫样本测试方法的通用性。结果解读:自动检测的疟原虫血症平均绝对误差为0.73±0.54%(n=9,P<0.05),与手动计数的相关性达0.97;约氏疟原虫样本的相关性为0.99,证明方法具有跨疟原虫种类的通用性。
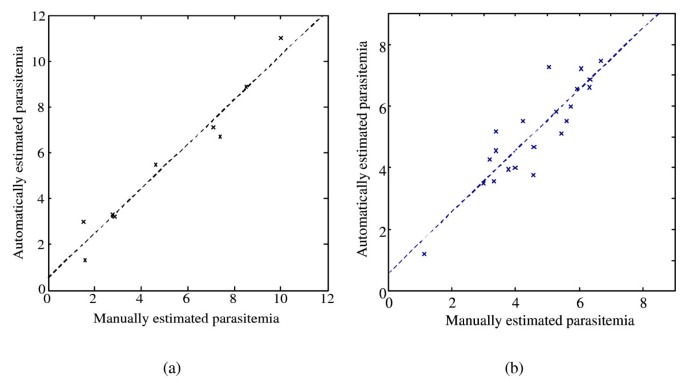
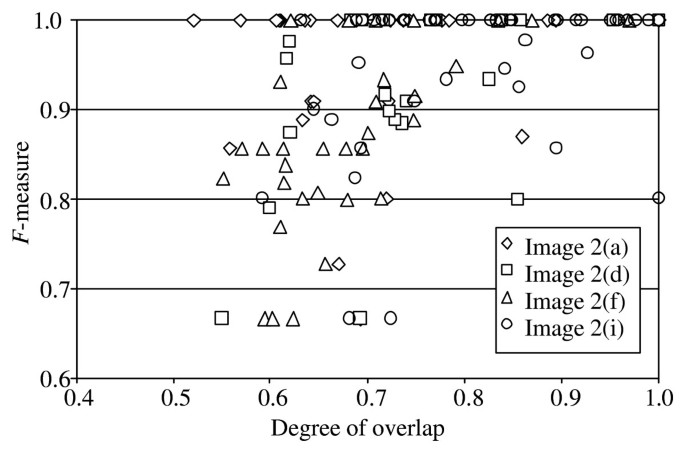
文献未提及具体实验产品,领域常规使用统计分析软件(如SPSS、MATLAB)完成数据统计。
4. Biomarker研究及发现成果
Biomarker定位
本文以疟原虫感染红细胞的图像特征(包括颜色通道差异、细胞形态、重叠程度等)作为检测Biomarker,筛选与验证逻辑为“多样化样本采集-人工标注金标准-自动检测算法开发-多维度性能验证”,通过与专业人员手动计数的金标准对比完成验证,形成从图像特征提取到疟原虫血症估算的完整检测链条。
研究过程详述
Biomarker来源于225张吉氏染色薄血涂片图像,覆盖不同疟原虫血症水平、细胞重叠程度、图像质量,包含恶性疟原虫、约氏疟原虫两种疟原虫样本;验证方法采用与四位疟原虫学家手动计数的中位数对比,同时用F值评估红细胞分割的精确率与召回率,用Pearson相关性分析评估疟原虫血症估算的准确性;检测的鲁棒性数据显示,聚焦良好、染色均匀的样本可容忍高达50%的细胞重叠,F值维持在92%以上,与手动计数的相关性达0.97,证明Biomarker的检测具有较高的稳定性。
核心成果提炼
本研究首次开发出基于比较分析的半自动化疟原虫血症检测方法,无需严格的样本模型假设,可处理多种非标准样本,自动检测的平均绝对误差小于1%(n=9,P<0.05),与人工计数的相关性达0.97;该方法可推广至不同疟原虫种类,约氏疟原虫样本的相关性达0.99,为疟疾低成本大规模筛查提供了可行的技术方案。此外,研究建立的细胞重叠程度与检测性能的关联模型,可为样本制备质量控制提供参考依据。
特别声明
1、本页面内容包含部分的内容是基于公开信息的合理引用;引用内容仅为补充信息,不代表本站立场。
2、若认为本页面引用内容涉及侵权,请及时与本站联系,我们将第一时间处理。
3、其他媒体/个人如需使用本页面原创内容,需注明“来源:[生知库]”并获得授权;使用引用内容的,需自行联系原作者获得许可。
4、投稿及合作请联系:info@biocloudy.com。