1. 领域背景与文献引入
文献英文标题:Accurate detection of early-stage lung cancer using a panel of circulating cell-free DNA methylation biomarkers;发表期刊:Biomarker Research;影响因子:未公开;研究领域:肺癌早期诊断(DNA甲基化生物标志物)
肺癌是全球癌症死亡的首要原因,2020年全球新增220万例肺癌患者,死亡180万例(占所有癌症死亡的18.0%)。早期诊断是改善肺癌预后的关键:Ⅰ期肺癌患者5年生存率可达68%-92%,但Ⅳ期患者仅约10%。目前临床常用的早期筛查方法存在明显局限:低剂量CT虽能发现肺结节,但假阳性率高(约96%),易导致过度诊断和不必要的有创检查;传统血清肿瘤标志物如细胞角蛋白19片段(CYFRA21-1)、癌胚抗原(CEA)等对早期肺癌的敏感性不足(多低于60%),难以满足精准诊断需求。
领域共识:DNA甲基化是一种重要的表观遗传修饰,肿瘤细胞中常存在“全基因组低甲基化(激活原癌基因)+ 抑癌基因启动子高甲基化(抑制基因表达)”的异常模式。已有研究发现肺癌中存在APC、p16(INK4a)、RASSF1A等基因的异常甲基化,且部分甲基化标志物可在循环游离DNA(cfDNA)中检测到,具备非侵入性诊断潜力。但现有研究多基于小样本或单一标志物,缺乏系统的多队列验证,且未聚焦早期肺癌的诊断性能。
在此背景下,本研究针对“现有肺癌早期诊断方法敏感性/特异性不足,缺乏高性价比非侵入性生物标志物”的核心问题,通过筛选肺癌特异性DNA甲基化差异区域(DMRs),构建多标志物诊断模型,旨在为早期肺癌的精准检测提供新策略。
2. 文献综述解析
作者对现有研究的分类围绕“肺癌早期诊断的局限”与“DNA甲基化标志物的进展”展开:
- 现有方法的局限:低剂量CT依赖影像学特征判别肺结节良恶性,假阳性率高;传统血清标志物敏感性低,无法区分早期肺癌与良性疾病。
- 甲基化标志物的进展:已有研究报道肺癌中存在多个基因的异常甲基化,但多为单一标志物研究,样本量小且缺乏临床验证;部分研究尝试检测血浆cfDNA甲基化,但未系统评估其对早期肺癌的诊断价值。
本研究的创新价值在于:①采用“前瞻性样本收集+回顾性盲法评估”设计,减少实验偏倚;②通过靶向测序分析9307个肺癌相关DMRs,系统筛选差异区域;③利用mRMR算法优化标志物panel,避免过拟合;④同时在组织(金标准)和血浆(非侵入性)中验证模型性能,为临床转化提供可靠证据。
3. 研究思路总结与详细解析
本研究核心目标是“筛选肺癌特异性甲基化标志物,构建非侵入性早期诊断模型”;技术路线为“临床队列构建→组织甲基化测序→DMRs筛选→模型构建→组织/血浆验证”的闭环。
3.1 临床队列构建与样本收集
实验目的是建立包含肺癌、良性疾病及健康对照的队列,为标志物筛选提供样本基础。
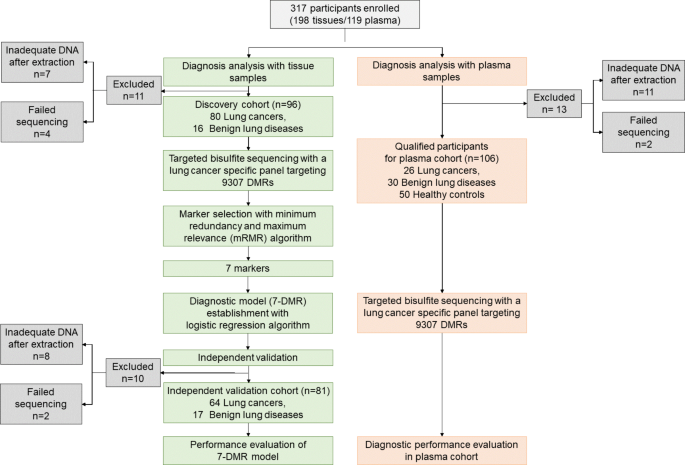
方法细节:2020-2021年招募317例受试者(健康对照50例、肺癌患者及良性肺疾病患者267例),采集术前1-3天的外周血(10mL)和术后FFPE组织样本;排除DNA提取不足(n=15)或测序失败(n=6)的样本,最终纳入198例组织样本(96例发现队列:80肺癌、16良性;81例验证队列:64肺癌、17良性)和106例血浆样本(26肺癌、30良性、50健康)。
结果解读:队列人口学特征(年龄、性别、吸烟史)无统计学差异(P>0.05),88.2%的肺癌患者为早期(0/I期),符合“早期诊断”的研究目标。
产品关联:文献未提及具体产品,领域常规使用Qiagen QIAamp DNA FFPE Tissue Kit提取组织DNA、QIAamp Circulating Nucleic Acid Kit提取血浆cfDNA。
3.2 靶向亚硫酸氢盐测序与差异甲基化分析
实验目的是比较肺癌与良性组织的甲基化谱,筛选差异DMRs。
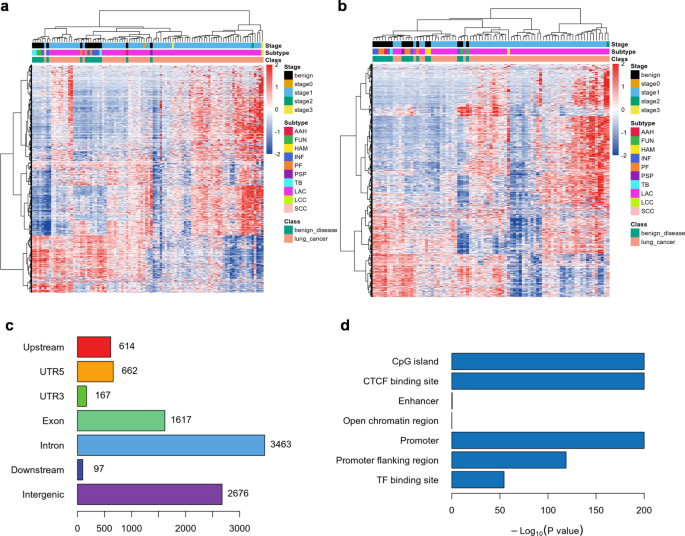
方法细节:使用定制化panel(覆盖9307个肺癌相关DMRs)对组织样本进行靶向亚硫酸氢盐测序;通过R包DSS分析差异甲基化位点(DMCs,FDR<0.05、delta>0.05),合并相邻DMCs为DMRs(至少3个CpG、间距≤100bp);利用ANNOVAR注释DMRs对应的蛋白编码基因。
结果解读:共鉴定6604个高甲基化DMRs(对应2614个基因)和2703个低甲基化DMRs(对应1228个基因);异常甲基化区域主要位于内含子、基因间区及外显子,富集于CpG岛、启动子等调控区域(符合肿瘤甲基化特征);KEGG通路分析显示差异基因参与“肌动蛋白细胞骨架调节”“非小细胞肺癌”等肺癌相关通路。
产品关联:领域常规使用Zymo Research EpiTect Bisulfite Kit进行亚硫酸氢盐转化,Illumina NovaSeq平台测序。
3.3 甲基化标志物筛选与生物信息学验证
实验目的是从差异DMRs中筛选具有诊断价值的核心panel。
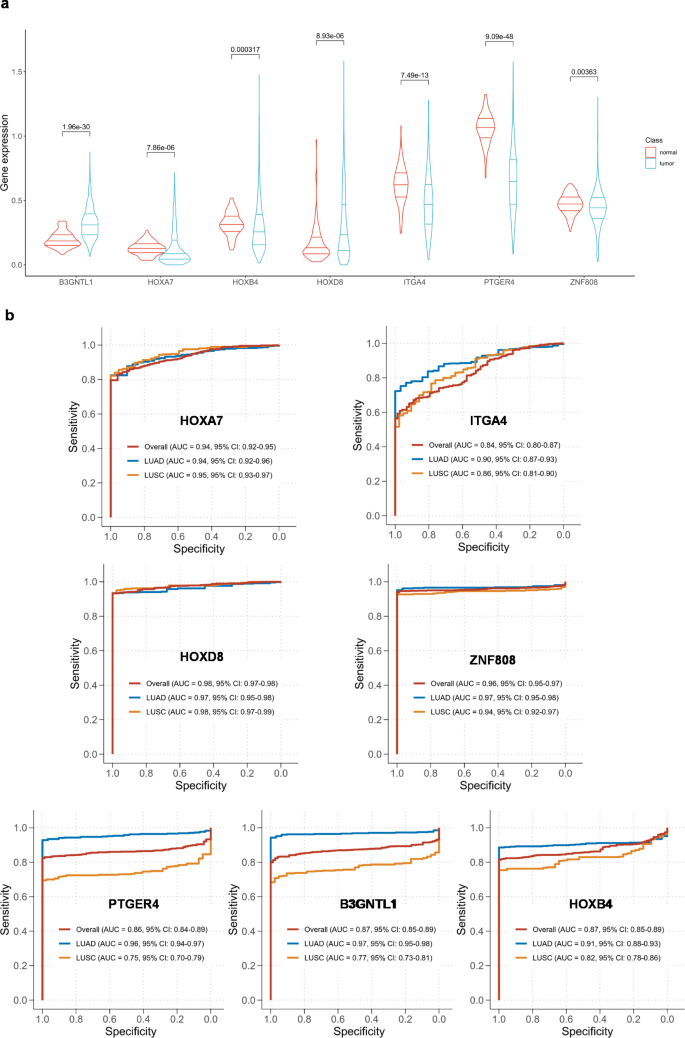
方法细节:①过滤“分析重复样本中变异系数>30%”的DMRs(保证重复性);②使用mRMR算法(平衡相关性与独立性)筛选1-10个特征,通过五折交叉验证(重复10次)选择“AUC最大且数量最少”的7个DMRs;③利用TCGA数据库(肺腺癌535例、肺鳞癌502例,对应正常组织59例、49例)验证标志物相关基因的表达差异。
结果解读:筛选出的7个DMRs对应HOXB4、HOXA7、HOXD8、ITGA4、ZNF808、PTGER4、B3GNTL1基因;TCGA数据显示,B3GNTL1、HOXD8在肺癌中表达显著上调(P<0.01),其余5个基因显著下调(P<0.01),提示DMRs可能通过调控基因表达参与肺癌发生。
产品关联:mRMR算法使用Python开源工具(https://github.com/smazzanti/mrmr),基因表达数据来自TCGA数据库。
3.4 组织样本中诊断模型构建与验证
实验目的是基于7个DMRs构建组织诊断模型,并验证性能。
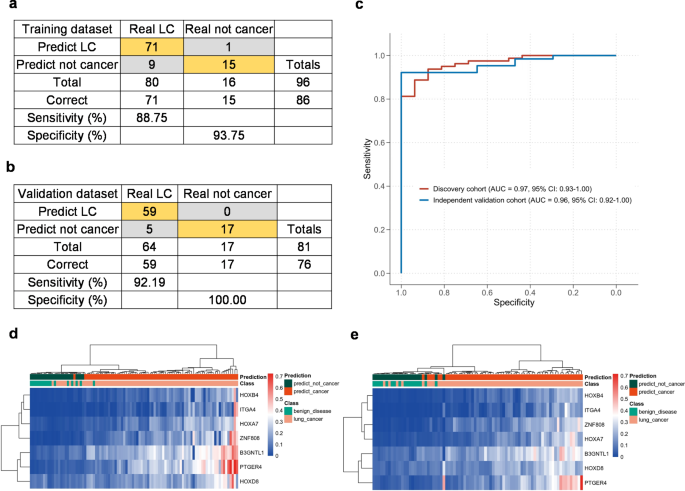
方法细节:以发现队列(80肺癌、16良性)为训练集,用逻辑回归构建“7-DMR模型”;以独立验证队列(64肺癌、17良性)为测试集,评估AUC、敏感性、特异性等指标;通过无监督层次聚类验证标志物的区分能力。
结果解读:发现队列AUC为0.97(95%CI:0.93-1.00),敏感性0.89(n=80,95%CI:0.82-0.95),特异性0.94(n=16,95%CI:0.89-0.99);验证队列AUC为0.96(95%CI:0.92-1.00),敏感性0.92(n=64,95%CI:0.86-0.98),特异性1.00(n=17,95%CI:1.00-1.00);无监督聚类可清晰区分肺癌与良性样本。
产品关联:逻辑回归模型使用Python scikit-learn包构建。
3.5 血浆样本中诊断模型性能评估
实验目的是验证模型的非侵入性诊断性能。
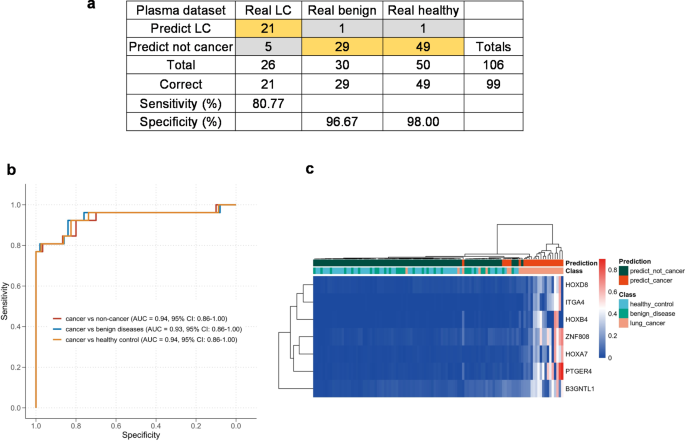
方法细节:合并组织发现+验证队列的甲基化数据重新训练模型,应用于106例血浆样本(26肺癌、30良性、50健康),评估“肺癌vs良性”“肺癌vs健康”“肺癌vs非癌(良性+健康)”的性能;通过无监督聚类验证区分能力。
结果解读:血浆样本中,模型对“肺癌vs非癌”的AUC为0.94(95%CI:0.86-1.00),敏感性0.81(n=26,95%CI:0.73-0.88),特异性0.98(n=80,95%CI:0.95-1.00);无监督聚类可区分肺癌、良性与健康样本。
产品关联:血浆cfDNA甲基化测序方法与组织一致。
4. Biomarker研究及发现成果解析
Biomarker定位
本研究的生物标志物为循环游离DNA中的7个DNA甲基化差异区域(DMRs),对应HOXB4、HOXA7、HOXD8、ITGA4、ZNF808、PTGER4、B3GNTL1基因。筛选与验证逻辑为“组织差异分析→重复性过滤→mRMR筛选→TCGA验证→组织/血浆模型验证”的完整链条。
研究过程详述
- Biomarker来源:肺癌及良性肺疾病的FFPE组织、肺癌/良性/健康对照的血浆cfDNA。
- 验证方法:靶向亚硫酸氢盐测序(检测甲基化水平)、TCGA基因表达分析(验证功能关联)、逻辑回归模型(评估诊断性能)。
- 特异性与敏感性:组织验证队列中,肺癌敏感性0.92(n=64),良性特异性1.00(n=17);血浆样本中,肺癌敏感性0.81(n=26),非癌特异性0.98(n=80)。
核心成果提炼
- 诊断性能优异:组织模型AUC达0.96,血浆模型AUC达0.94,远超传统血清标志物(如CEA的AUC约0.7)。
- 非侵入性优势:通过血浆cfDNA检测,避免有创组织活检,适用于早期筛查。
- 功能相关性:TCGA数据证实标志物相关基因在肺癌中表达异常,提示DMRs可能通过调控基因表达参与肺癌发生。
- 创新性:首次系统筛选并验证了包含7个DMRs的早期肺癌诊断panel,填补了“高敏感性非侵入性甲基化标志物”的研究空白。
局限性与展望
本研究样本量较小(尤其是血浆肺癌病例仅26例),未来需扩大多中心样本验证模型通用性;未探究DMRs调控肺癌的分子机制,需进一步开展功能实验(如基因敲除/过表达)验证其作用通路。
综上,本研究构建的7-DMR甲基化panel为早期肺癌的非侵入性诊断提供了新方案,具备潜在的临床转化价值。
