1. 领域背景与文献引入
文献英文标题:Retrospective genomic analysis of sorghum adaptation to temperate-zone grain production;发表期刊:Genome Biology;影响因子:未公开;研究领域:作物基因组学/高粱遗传育种。
谷物作为人类核心主食,经历了数千年的驯化与定向改良:从野生禾本科植物驯化为栽培种后,又持续被选育以提升产量、均匀性及新环境适应性。领域共识:绿色革命时期,通过调控小麦、水稻的赤霉素通路获得半矮化品种,大幅提升了收获指数与抗倒伏能力,成为现代高投入农业的核心技术突破之一。高粱作为全球第五大禾谷类作物,起源于非洲热带地区,为适应温带机械化谷物生产,需选育光周期不敏感(早熟)与矮化的品种,已知至少4个主要矮化位点(Dw1-Dw4)和6个成熟位点(Ma1-Ma6)参与调控,其中Ma1、Ma3、Dw3已被克隆,但Dw1、Dw2尚未完成克隆,且此前针对高粱转换(SCP)项目的全基因组层面适应性机制研究仍存在空白,无法系统解析驯化过程中基因组渗入的关键区域及亚群特异性差异,因此亟需开展全基因组研究以明确温带适应的遗传基础,为高粱及相关禾本科作物的跨区域改良提供理论支撑。
2. 文献综述解析
本文献综述部分以谷物驯化与适应性改良的时间线为核心分类维度,系统梳理了从野生种驯化到现代品种选育的关键研究进展,重点聚焦高粱温带适应的遗传调控研究现状与未解决问题。
现有研究已明确谷物驯化过程中人类选择的核心方向,包括产量提升、环境适应性增强等,绿色革命中赤霉素通路的调控机制为禾本科作物矮化改良提供了范式。针对高粱温带适应,已通过经典遗传学定位了多个控制光周期敏感性与矮化的主效位点,其中Ma1编码PRR37蛋白、Ma3编码光敏色素B、Dw3编码生长素转运蛋白,这些位点的功能验证为高粱遗传改良提供了靶点,但现有研究仍存在局限性,一是未对SCP项目开展全基因组层面的渗入位点系统分析,无法明确除已知主效位点外的其他适应性区域;二是缺乏不同高粱亚群间的适应性位点差异研究,难以满足多样化遗传背景下的育种需求;三是Dw1、Dw2等未克隆位点的功能及调控机制尚不清晰。本研究的创新价值在于首次采用基因型测序(GBS)技术对1160份高粱转换系(SC)及其热带亲本(EP)材料进行全基因组分析,通过渗入位点定位、关联分析与亚群特异性研究,系统解析了高粱温带适应的遗传基础,填补了全基因组层面研究的空白。
3. 研究思路总结与详细解析
本研究以解析高粱适应温带谷物生产的基因组遗传基础为核心目标,围绕SCP项目中基因组渗入的关键区域及功能这一科学问题,构建了“GBS全基因组分型→渗入位点频率分析→表型关联与群体分化验证→亚群特异性位点解析”的闭环技术路线,通过多维度分析明确了温带适应的核心基因组区域及亚群差异。
3.1 实验材料与GBS全基因组分型
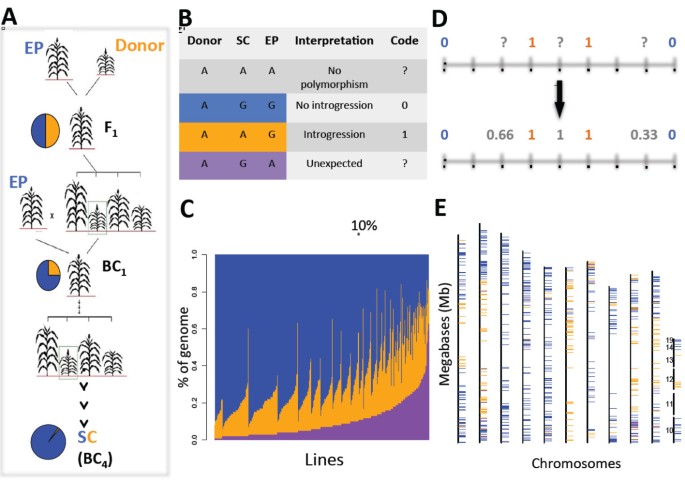
实验目的:获取高粱SC与EP材料的全基因组SNP数据,为后续渗入位点分析提供基础。方法细节:选取580对SC与EP材料,采用改良CTAB法从黄化幼苗中提取基因组DNA,使用PstI-HF与BfaI/HinP1I双酶切构建GBS文库,连接带条形码的接头后进行PCR扩增,通过Illumina HiSeq2000平台进行单端测序,利用TASSEL GBS流程进行SNP分型,对低质量数据与异常样本进行过滤,最终保留390对SC-EP材料与46062个SNP。结果解读:双酶切组合使每个样本的SNP检测数量提升近一倍,过滤后数据集的杂合基因型占比仅0.3%,缺失数据从66%降至23%,确保了后续分析的可靠性。产品关联:实验所用关键产品:Invitrogen的PicoGreen定量试剂、Beckman Coulter的AmpureXP Beads、Agilent的Bioanalyzer 2100与DNA1000 Kit、New England Biolabs的PhusionHF Master Mix、Illumina HiSeq2000测序平台。
3.2 基因组渗入位点频率分析
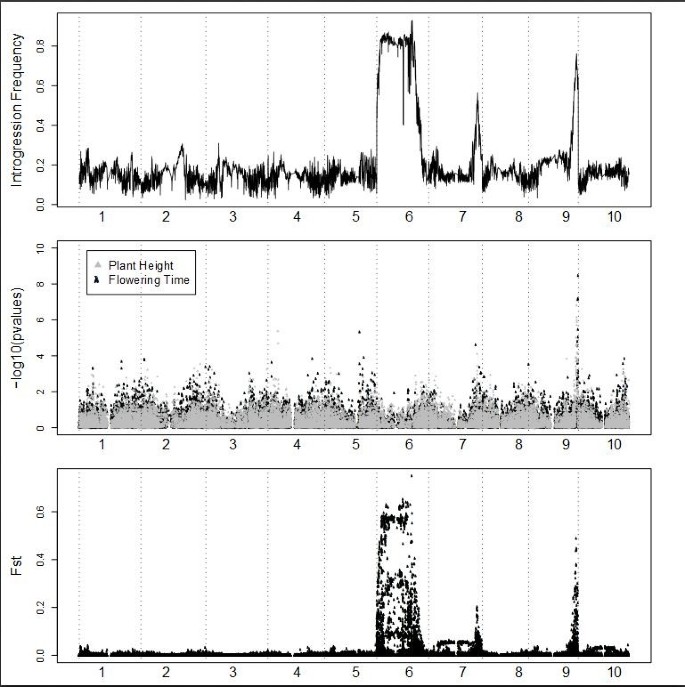
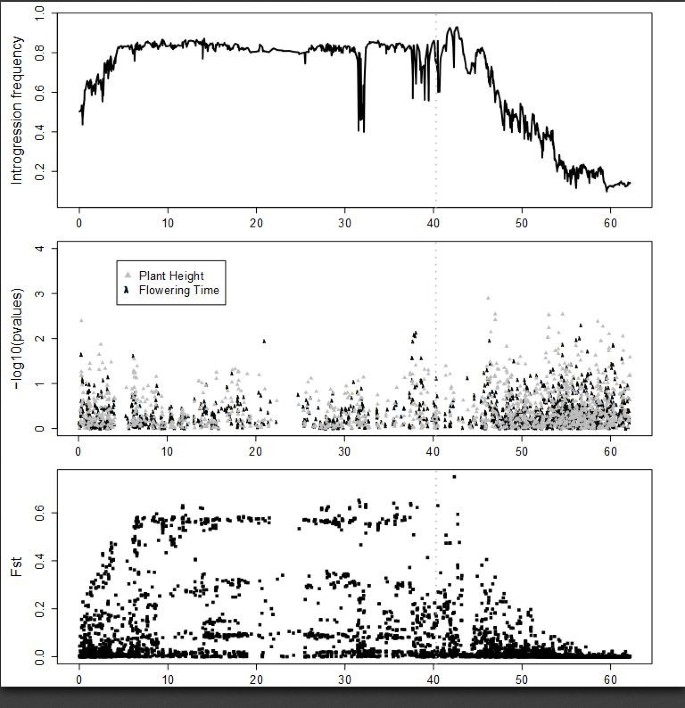
实验目的:定位SCP项目中受选择的核心基因组渗入区域。方法细节:基于SC与EP、供体材料的基因型差异,定义渗入位点(SC与供体基因型一致),采用加权平均法填充缺失数据,计算每个SNP位点的渗入频率,与无选择情况下的理论频率(约3%)进行比较。结果解读:全基因组范围内检测到多个渗入频率高于4%的区域,其中6号、7号、9号染色体上存在三个显著的渗入频率峰值,表明这些区域是温带适应的必需位点,与理论频率的差异证实了这些区域受到强烈的人工选择。
3.3 表型关联与群体分化验证
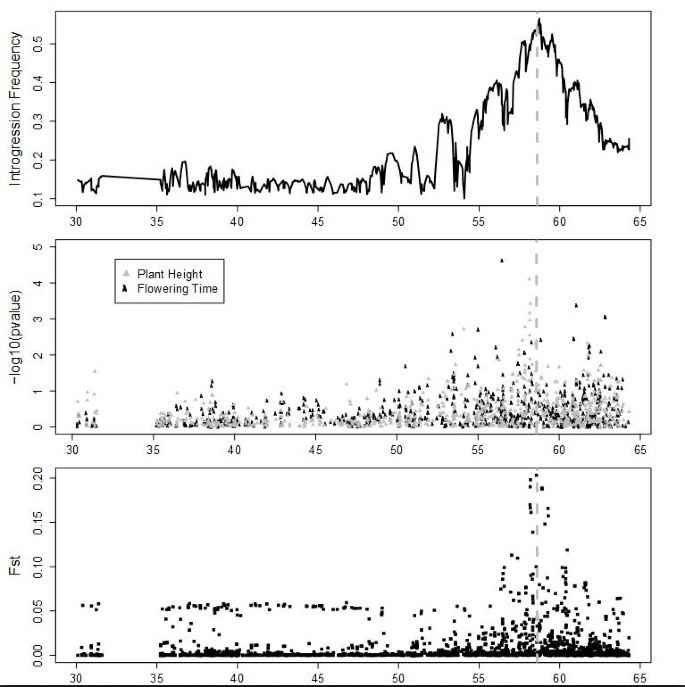
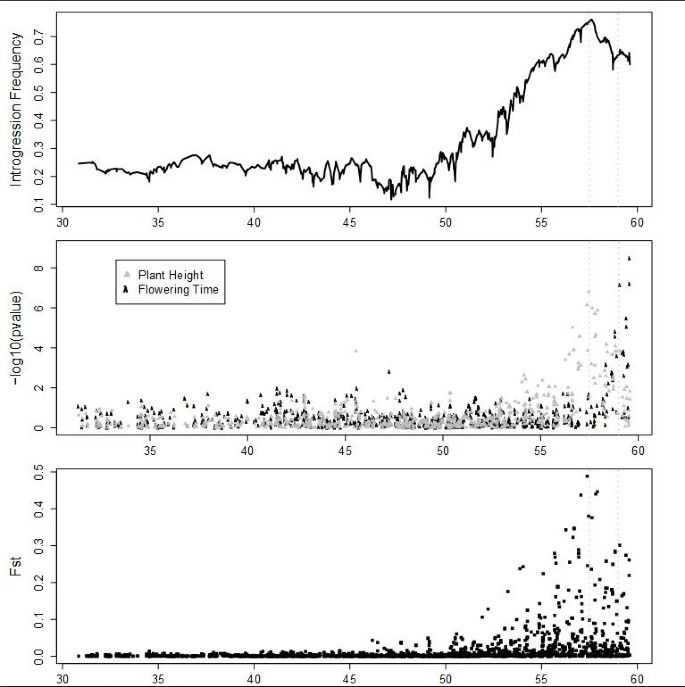
实验目的:验证渗入区域的功能关联性,明确其调控的表型性状。方法细节:对580份SC材料的株高与开花时间进行表型调查,采用全基因组关联分析(GWAS)分析表型与SNP的关联,同时计算SC与EP群体间的Fst值以验证群体分化区域。结果解读:GWAS分析显示9号染色体Dw1区域与株高显著关联(符合统计学显著性水平),且该区域可进一步划分为独立的株高与开花时间数量性状位点(QTL);7号染色体Dw3区域的渗入频率与Fst峰值一致,但表型关联信号较弱;6号染色体整体渗入频率与Fst值较高,但无显著表型关联,推测该区域的功能变异已被供体单倍型替代。
3.4 亚群特异性渗入位点分析
实验目的:解析不同高粱亚群间温带适应的遗传差异。方法细节:基于EP材料的主成分分析(PCA)将样本分为caudatum(C,n=137)、durra(D,n=131)、guinea/kafir(GK,n=122)三个亚群,分别计算各亚群的渗入频率,通过置换检验评估亚群间的差异显著性。结果解读:各亚群的渗入位点存在显著差异,例如GK亚群在6号染色体1Mb区域存在特异性渗入峰值,Dw1、Dw3区域的渗入频率也因亚群而异,部分亚群特异性区域与开花时间关联,表明这些位点是亚群特异性的温带适应靶点。
4. Biomarker研究及发现成果
本研究中涉及的Biomarker为调控高粱温带适应的基因组区域(包括主效渗入位点与亚群特异性位点),通过“GBS分型→渗入频率筛选→功能验证→亚群分析”的完整逻辑链进行定位与验证。
Biomarker的来源为SC与EP材料的全基因组SNP位点,验证方法包括渗入频率统计、GWAS关联分析、群体分化(Fst)分析及亚群特异性检验。核心主效Biomarker包括6号染色体Ma1-Dw2区域、7号染色体Dw3区域、9号染色体Dw1区域,这些区域的渗入频率显著高于理论值(>4%,n=390),其中Dw1区域的株高关联信号具有统计学显著性(P<0.05,文献未明确具体P值);亚群特异性Biomarker如GK亚群6号染色体1Mb区域,其渗入频率在该亚群中显著高于其他亚群(置换检验P<0.05)。核心成果方面,首次明确高粱温带适应仅需少数基因组区域,每个区域包含多个连锁的株高与开花时间位点,Dw1区域可拆分为独立的株高与开花时间QTL;6号染色体因连锁不平衡导致大片段渗入,损失了大量功能多样性,对温带高粱育种构成限制;亚群特异性位点的存在表明不同遗传背景下的适应机制存在差异。这些成果为高粱及相关禾本科作物的跨区域适应性改良提供了精准的基因组靶点,有望加速作物在新生产系统中的应用。
