1. 领域背景与文献引入
文献英文标题:Phylogeographic variation in recombination rates within a global clone of methicillin-resistant Staphylococcus aureus;发表期刊:Genome Biology;影响因子:未公开;研究领域:细菌分子流行病学、耐甲氧西林金黄色葡萄球菌(MRSA)进化与系统地理学。
细菌病原体的微进化与系统地理学研究是感染病精准防控的核心基础,其发展历程经历了从低分辨率分型到全基因组解析的关键突破。早期依赖的多位点序列分型(MLST)技术虽在致病菌种群结构解析中取得成功,但仅覆盖不足1%的基因组,无法揭示近期克隆的微进化细节。下一代测序(NGS)技术的问世为全基因组水平解析细菌传播路径与进化机制提供了高分辨率工具,已应用于致病菌局部分散、医院内传播及宿主内长期定植的分子动态研究。耐甲氧西林金黄色葡萄球菌(MRSA)是全球最具威胁的医院获得性致病菌之一,ST239是其广泛传播的高毒力克隆谱系,此前研究多单独聚焦其全球传播格局或重组进化机制,缺乏将系统地理格局与重组率变异相结合的综合分析,无法揭示同一克隆内不同地理亚群的进化动态差异。因此,本研究旨在通过扩展NGS数据集,结合贝叶斯重组检测方法,系统解析ST239克隆内重组率的系统地理变异及其驱动因素,为耐药菌的进化防控提供理论依据。
2. 文献综述解析
本文综述部分以细菌病原体微进化研究的技术发展与研究侧重点为分类维度,梳理了MLST、NGS在系统地理学与分子进化研究中的应用,以及重组在细菌进化中的核心作用,明确了现有研究的局限与本研究的创新定位。
现有研究中,MLST技术作为流行病学监测与种群结构解析的经典方法,在致病菌分型与溯源中发挥了重要作用,但受限于基因组覆盖度,无法解析近期克隆的微进化细节;NGS技术的应用则实现了全基因组单核苷酸多态性(SNP)的高分辨率检测,已用于解析致病菌在数月至数年尺度的分化、医院内传播及宿主内定植的分子变化,但多数研究仅聚焦于系统地理传播或分子进化的单一维度。例如,Harris等的研究揭示了ST239克隆的全球传播路径,但未深入分析重组对其进化的影响;Croucher等解析了肺炎链球菌的重组机制,但未结合流行病学背景探讨重组率的地理变异。现有技术的优势在于NGS提供的全基因组数据能实现高分辨率进化分析,贝叶斯方法可精准检测重组事件;局限性则在于缺乏将系统地理格局与重组率变异相结合的研究,对同一克隆内不同地理亚群的重组差异及驱动因素的认识不足。
本研究的创新点在于首次将系统地理学框架与分子进化分析相结合,针对全球传播的单一细菌克隆(ST239),同时解析核心基因组与可移动遗传元件(MGE)的重组率地理变异,填补了现有研究中“系统地理-分子进化”脱节的空白,为理解细菌克隆的全球进化动态提供了新的研究范式。
3. 研究思路总结与详细解析
本研究的总体目标是揭示MRSA ST239全球克隆内重组率的系统地理变异及其驱动因素,核心科学问题为同一克隆不同地理亚群重组率差异的形成机制,技术路线遵循“数据集构建→重组检测→系统地理分群→重组率比较→驱动因素探讨”的闭环逻辑,综合运用NGS测序、贝叶斯重组分析、系统进化建模等多种方法。
3.1 全基因组数据集构建与SNP分析
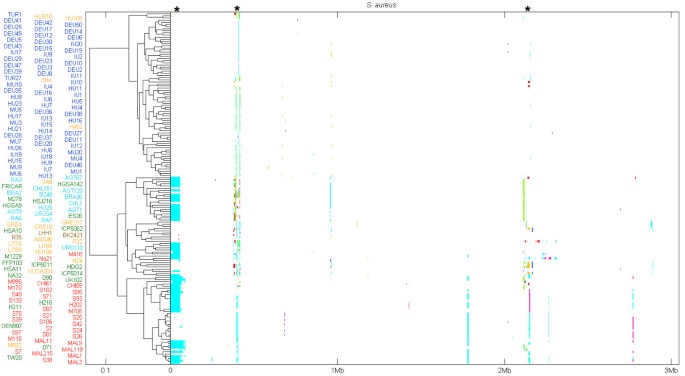
实验目的是构建包含全球多地区的ST239全基因组数据集,为后续系统地理与重组分析提供基础数据支撑。方法细节:在Harris等的62株ST239分离株基础上,新增102株分离株(其中31株来自全球收集,71株来自土耳其4家代表性医院),最终形成165株的研究队列;以ST239参考基因组TW20为模板,采用SMALT软件进行reads比对,鉴定高质量SNP位点。结果解读:共获得16172个高质量SNP,覆盖核心基因组与非核心可移动遗传元件(MGE)区域;重组事件主要集中在MGE区域,核心基因组重组率相对较低,这与此前MLST研究的结果一致。文献未提及具体实验产品,领域常规使用Illumina测序平台、SMALT序列比对软件、BRATNextGen重组检测工具等。
3.2 重组事件检测与基因组功能分区分析
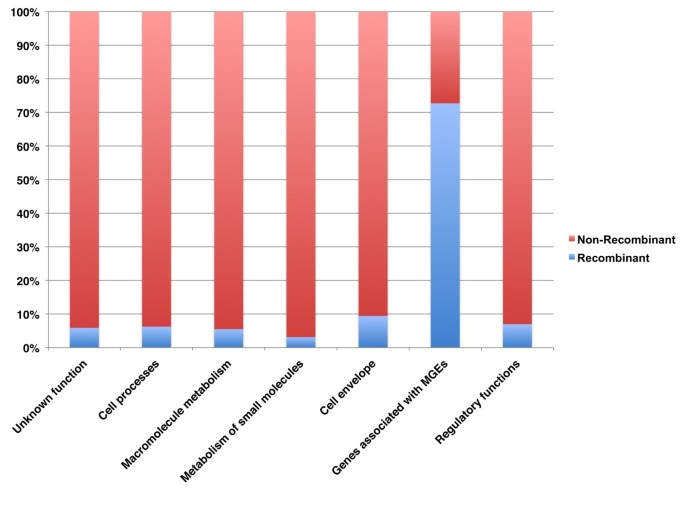
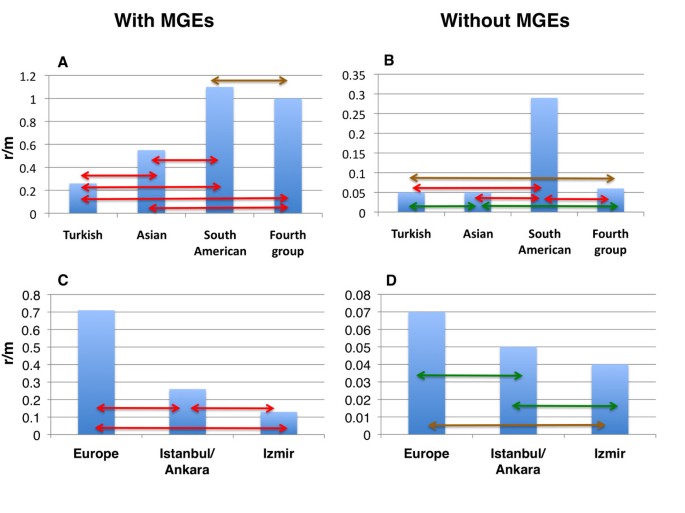
实验目的是定位基因组中受重组影响的区域与功能基因,比较核心基因组与MGE的重组特征差异。方法细节:采用BRATNextGen贝叶斯方法检测重组事件,筛选包含至少100bp重组片段的基因,按Riley功能分类统计不同功能类别基因的重组比例;通过将SNP分为重组来源与突变来源,计算重组与突变的核苷酸变化比值(r/m)以量化重组对基因组多样化的贡献。结果解读:共441个基因(占参考基因组的15.3%)受重组影响,其中MGE相关基因的重组比例超过70%,核心基因组中细胞包膜相关基因的重组率最高(3%-10%);整体基因组的r/m比值为1.13,排除MGE后降至0.11,提示MGE是重组的主要发生区域,核心基因组重组率较低但功能上存在差异,细胞包膜基因可能受到更高的多样化选择压力。
3.3 系统地理格局解析与种群分群
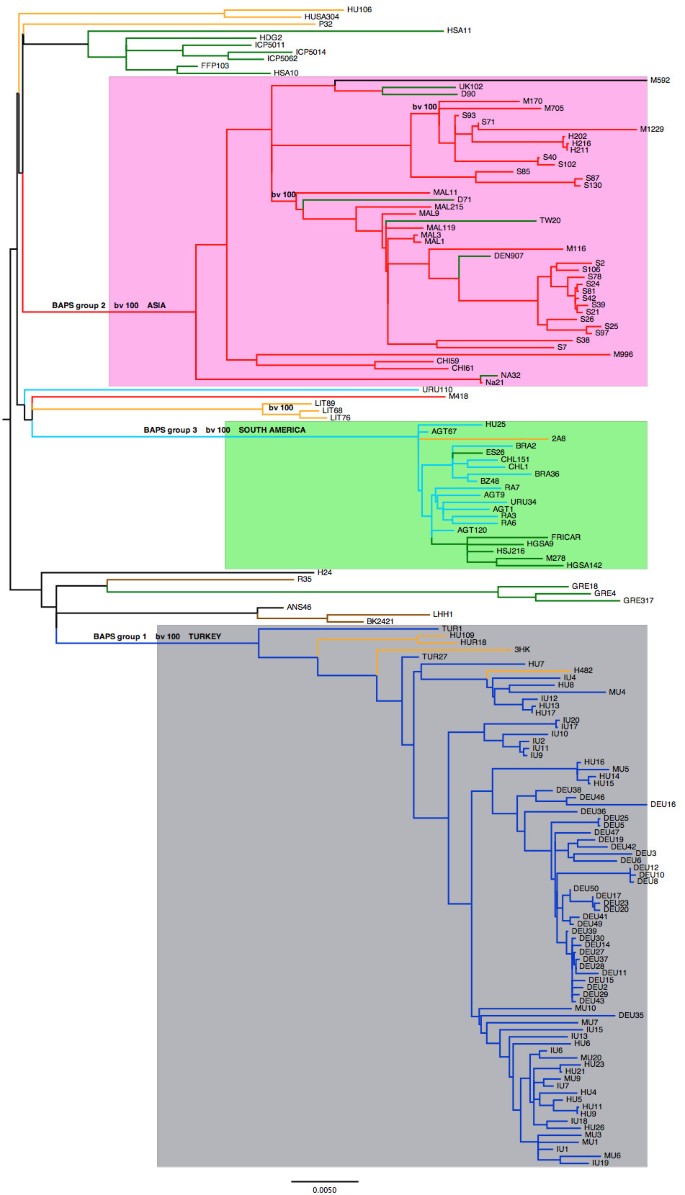
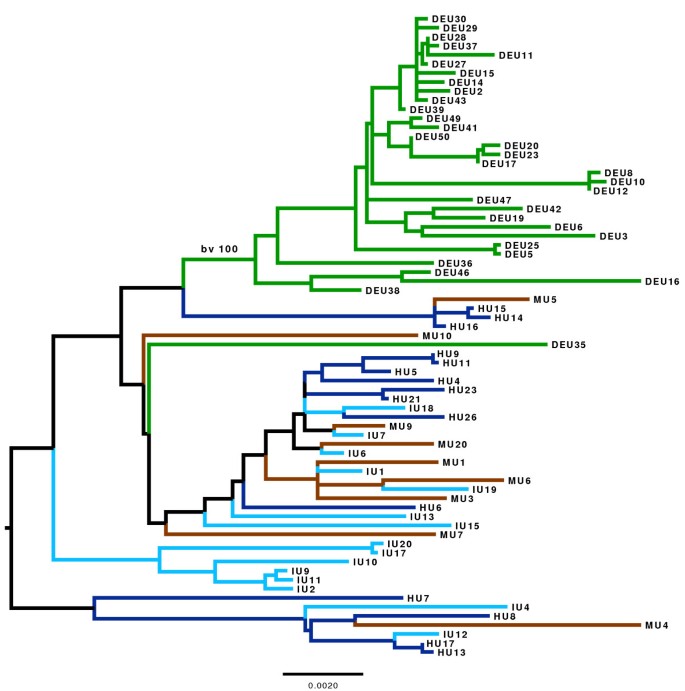
实验目的是明确ST239克隆的全球系统地理结构与种群分化时间,为重组率的亚群比较提供框架。方法细节:排除重组区域的SNP后构建最大似然进化树,采用贝叶斯种群结构分析(BAPS)进行种群分群,通过BEAST软件构建校准进化树以估算种群亚群的起源时间;针对土耳其国内分离株单独构建进化树,分析医院间的传播动态。结果解读:全球ST239种群分为3个单系亚群(土耳其、南美、亚洲)和1个多系群(欧美),土耳其亚群起源于东欧的单一引入事件,国内伊兹密尔分离株形成独立聚类,提示医院间传播存在差异(安卡拉与伊斯坦布尔间传播频繁,伊兹密尔相对隔离);BEAST分析显示ST239于1965年起源于欧洲,土耳其与亚洲亚群起源于1982年左右,南美亚群起源于1992年。
3.4 亚群重组率比较与驱动因素探讨
实验目的是比较不同地理亚群的重组率差异,解析其潜在驱动因素。方法细节:计算各BAPS亚群的r/m比值,采用卡方检验比较亚群间重组率的统计学差异;分析土耳其国内两次奠基者事件(东欧→安卡拉/伊斯坦布尔、安卡拉/伊斯坦布尔→伊兹密尔)中的r/m变化趋势。结果解读:含MGE时,南美亚群r/m比值最高,亚洲亚群中等,土耳其亚群最低,各亚群间比较除第四亚群与南美亚群外均为P<0.0001(n=165);排除MGE后,南美亚群r/m仍显著高于其他亚群(P<0.0001,n=165),第四亚群与土耳其亚群比较P=0.015(n=165);土耳其国内奠基者事件中r/m逐渐降低。推测:驱动因素包括种群大小与起源时间(新建立的种群多样性低导致重组检测率低)、宿主流动导致的传播动态(隔离种群基因交流少)、基因组变化(如限制修饰系统)影响重组倾向。
4. Biomarker研究及发现成果
本研究以MRSA ST239克隆内的重组事件与重组率作为进化分子标志物,通过全基因组分析揭示了其系统地理变异特征,为理解细菌克隆的进化动态提供了新的分子指标。
Biomarker定位:本文聚焦的分子标志物为ST239基因组中的重组事件及重组率(r/m比值),属于进化层面的分子标志物,筛选与验证逻辑为:基于165株全基因组SNP数据,采用BRATNextGen贝叶斯方法检测重组片段,结合系统地理分群分析不同亚群间的重组率差异,通过统计学检验验证差异的显著性。
研究过程详述:该标志物的来源为165株全球不同地区ST239分离株的全基因组SNP数据,验证方法包括重组事件检测(BRATNextGen,bootstrap验证P<0.05)、系统进化分析(最大似然树、BAPS分群,bootstrap支持率最高为100%)、统计学检验(卡方检验比较亚群r/m差异);特异性方面,不同地理亚群的重组率特征具有显著差异,如土耳其亚群r/m显著低于南美亚群(P<0.0001,n=165),敏感性方面,重组事件检测可覆盖基因组中受重组影响的15.3%基因,其中MGE区域重组检测敏感性更高。
核心成果提炼:首次发现全球传播的单一细菌克隆内重组率存在显著系统地理变异,该变异可作为反映克隆进化动态的分子标志物;南美亚群重组率最高(含MGE时r/m与土耳其亚群比较P<0.0001,n=165),土耳其亚群最低,提示种群隔离程度与重组率负相关;核心基因组中细胞包膜基因重组率更高,提示其受到多样化选择的作用;重组率差异的驱动因素包括种群起源时间、宿主流动导致的传播动态、种群隔离程度,为耐药菌的进化防控提供了理论依据。本研究未涉及临床诊断或预后相关的传统Biomarker,但其揭示的重组率地理变异特征可用于追踪耐药菌克隆的进化与传播路径。
