1. 领域背景与文献引入
文献英文标题:scSTEM: clustering pseudotime ordered single-cell data;发表期刊:Genome Biology;影响因子:未公开;研究领域:单细胞基因组学、基因表达模式分析
单细胞RNA测序(scRNA-seq)技术自2009年首次报道以来,已成为解析细胞异质性、重构细胞发育与分化轨迹的核心手段,关键技术突破包括2014年Monocle系列轨迹推断方法的提出、2018年Slingshot等轨迹工具的优化,推动了细胞命运轨迹解析的快速发展。当前研究热点聚焦于细胞命运决定的分子机制、动态基因表达网络构建,但领域内仍存在核心未解决问题:现有基因聚类方法大多未利用轨迹的动态时间信息,且伪时间排序数据存在路径重叠度高、有效时间点少的特性,传统聚类方法难以适配,导致轨迹路径上的基因动态表达模式解析不足,限制了对细胞命运分支机制的深入理解。
针对“伪时间排序单细胞数据的基因聚类方法缺失”这一研究空白,本研究开发了scSTEM工具,通过扩展经典的STEM时间序列聚类算法,结合单细胞轨迹推断技术与基因表达汇总策略,实现了轨迹路径特异性的基因聚类与跨路径比较,为解析细胞命运决定的分子机制提供了新的分析范式,具有重要的学术价值与应用前景。
2. 文献综述解析
作者按单细胞数据分析的不同环节,将现有研究分为细胞分群与轨迹建模、基因聚类两类,重点评述了现有基因聚类方法在伪时间数据应用中的局限性,明确了本研究的创新方向。
现有研究中,细胞分群与轨迹建模方法如Monocle 3、Slingshot等已能有效重构细胞发育的伪时间路径,实现细胞命运轨迹的可视化,但针对基因层面的分析方法仍存在不足。已有的基因聚类方法如scLM、GPseudoClust主要聚焦于同一细胞类型内的基因聚类,未利用时间序列或轨迹的动态表达信息,无法解析路径特异性的基因表达模式;同时,这些方法在处理伪时间数据时,未考虑路径重叠、有效时间点少的特性,导致聚类结果的生物学相关性不足。此外,传统时间序列聚类方法如STEM仅适用于bulk数据,无法直接适配单细胞数据的异质性与dropout问题。
本研究的创新价值在于,首次将STEM算法扩展到单细胞伪时间排序数据,通过整合轨迹推断方法与基因表达汇总策略,解决了伪时间数据路径重叠、有效时间点少的聚类难题;同时,新增了跨路径聚类比较功能,能够解析细胞命运分支的分子差异,弥补了现有方法的核心不足,为单细胞轨迹的基因层面分析提供了全新工具。
3. 研究思路总结与详细解析
本研究的核心目标是开发适配伪时间排序scRNA-seq数据的基因聚类工具scSTEM,解决伪时间数据基因聚类的技术难题;核心科学问题包括如何将轨迹动态信息融入基因聚类、如何应对伪时间数据的路径重叠与有效时间点少的问题;技术路线遵循“工具构建→多数据集验证→功能拓展→性能比较”的闭环逻辑,通过整合轨迹推断、基因表达汇总、STEM聚类与结果比较,实现了完整的分析流程。
3.1 scSTEM工具框架构建与核心流程设计
实验目的:构建能够处理伪时间排序scRNA-seq数据的基因聚类工具,明确核心分析流程与技术参数。
方法细节:整合dynverse包支持的19种轨迹推断方法(如Monocle 3、Slingshot、PAGA等),设计三种基因表达汇总指标(平均表达、熵减评分、表达变化率)以适配不同生物学场景,扩展STEM算法使其支持单细胞数据的基因聚类,并开发可视化GUI界面;流程包括轨迹构建、细胞路径选择、基因表达汇总、STEM聚类、功能富集分析与跨路径比较五个核心步骤。
结果解读:成功构建scSTEM工具的完整分析流程(如图1),能够将伪时间轨迹路径转换为简化的时间序列数据,有效降低单细胞数据的噪声与dropout影响;每个路径的聚类结果包含基因聚类列表、GO富集分析结果与表达模式图谱,为后续生物学解析提供了全面信息。
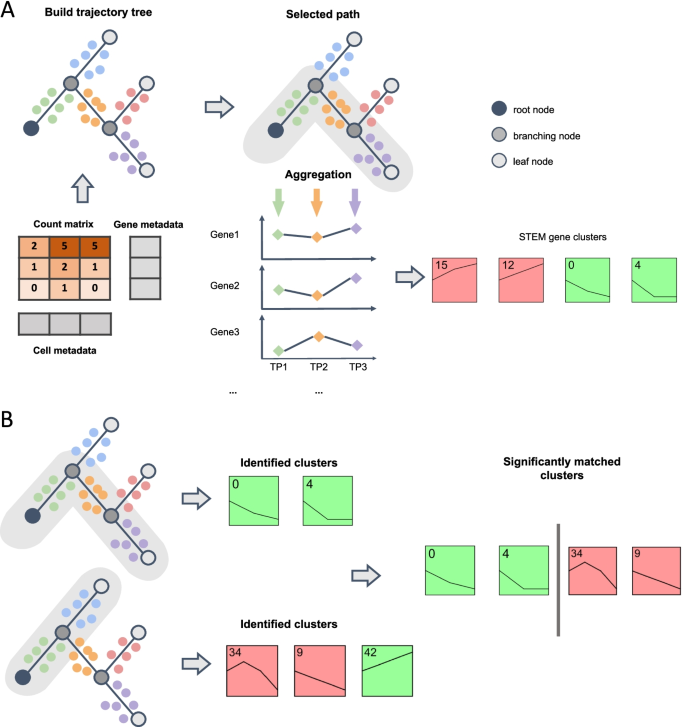
产品关联:文献未提及具体实验产品,领域常规使用R语言生物信息学包(如dynverse、Seurat、Monocle 3等)及STEM算法工具。
3.2 多数据集验证工具的生物学有效性
实验目的:验证scSTEM在不同生物学场景下的基因聚类性能与功能解析能力。
方法细节:选取三个具有代表性的scRNA-seq数据集:人类胎儿免疫细胞数据集(n=103766,18个时间点)、小鼠胚胎血细胞数据集(n=42262,5个时间点)、小鼠胚胎神经嵴细胞数据集(n=22283,5个时间点);针对每个数据集,选择细胞类型特异性标记基因或高可变基因作为输入,分别使用不同轨迹推断方法与基因汇总指标进行scSTEM分析,结合GO富集分析解析聚类的生物学功能。
结果解读:在人类胎儿免疫细胞数据中,scSTEM成功识别出与NK细胞毒性、T细胞活化相关的基因聚类(如图2),每个路径包含1-5个显著聚类,基因数量为35~301个;在小鼠胚胎血细胞数据中,区分出免疫应答相关基因(表达上调)与细胞发育相关基因(表达下调)的聚类(如图3),揭示了终端细胞命运固定时发育程序的抑制与免疫功能的激活;在小鼠胚胎神经嵴细胞数据中,发现同一功能模块(神经元发育)的基因在不同路径呈现上调或下调的差异表达模式(如图4),提示功能模块的表达调控可驱动不同细胞命运。
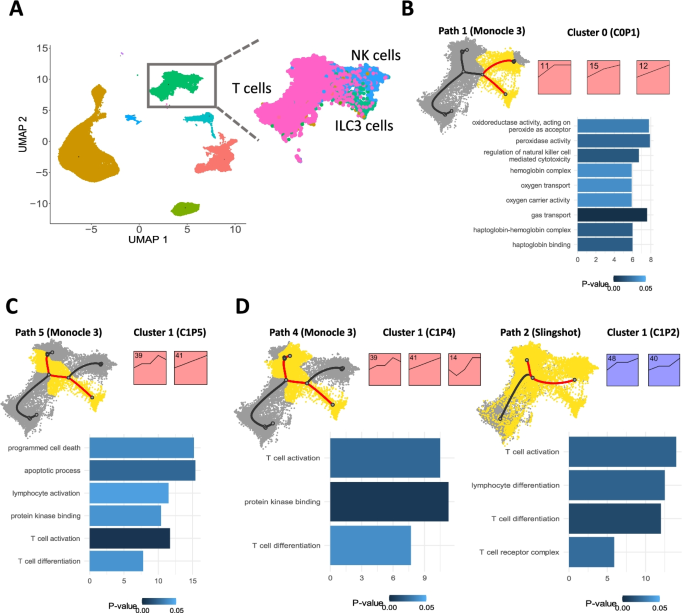
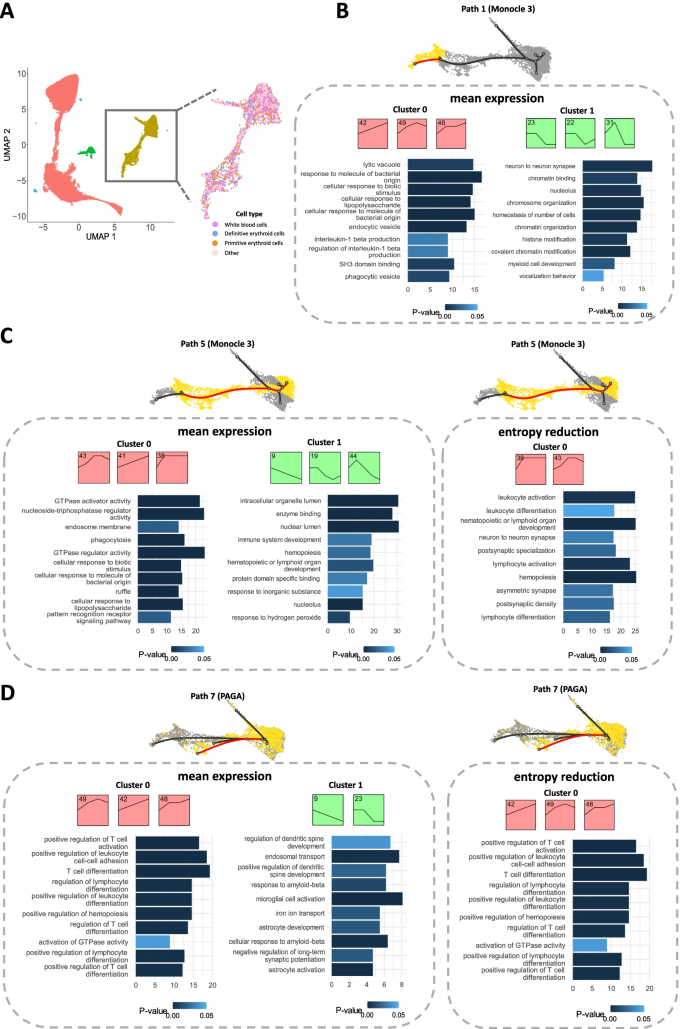
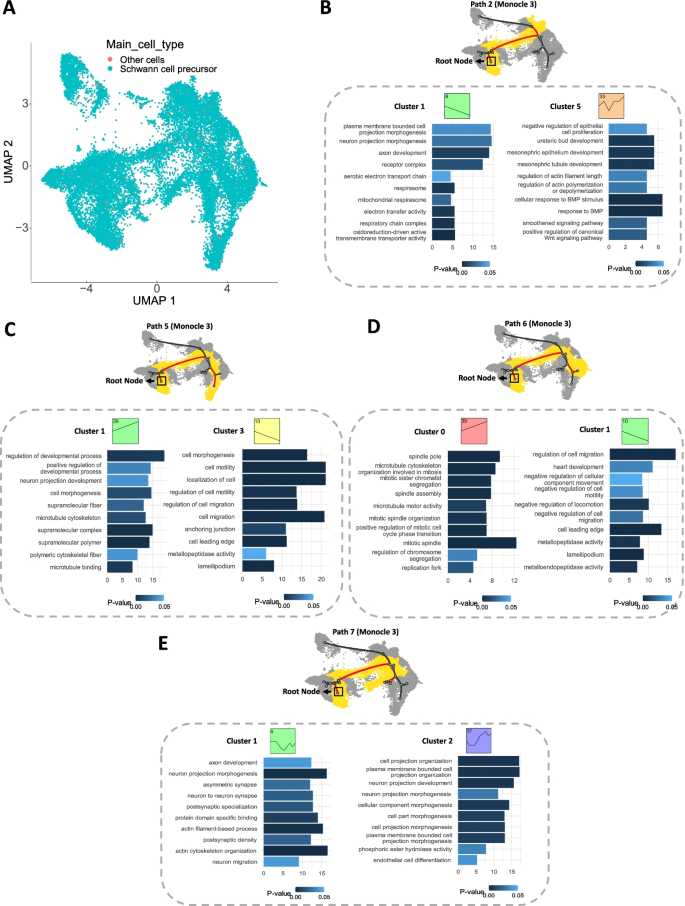
产品关联:文献未提及具体实验产品,领域常规使用单细胞测序数据分析平台及GO功能富集分析工具。
3.3 未知细胞群的功能注释能力验证
实验目的:验证scSTEM对未注释细胞群的功能解析能力,解决单细胞分析中细胞类型注释缺失的问题。
方法细节:选取人类胎儿免疫细胞数据中未注释的STC2_TLX1细胞群,使用Monocle 3轨迹推断方法与平均表达汇总指标进行scSTEM分析,通过GO富集分析推断该细胞群的潜在功能。
结果解读:scSTEM识别到一个显著聚类(Cluster 0),其基因表达呈持续下降趋势;GO富集分析显示该聚类与“内源性抗原的加工与呈递”相关(校正P值=0.004),结合文献报道,提示该细胞群可能为间充质前体细胞或干细胞,具有抗原呈递功能,为未知细胞群的注释提供了分子依据。
产品关联:文献未提及具体实验产品,领域常规使用GO数据库等基因功能注释资源。
3.4 跨轨迹路径的基因聚类比较分析
实验目的:验证scSTEM比较不同轨迹路径基因表达模式差异的能力,解析细胞命运分支的分子机制。
方法细节:在人类胎儿免疫细胞数据中,选取NK细胞路径与T细胞路径的聚类结果,使用超几何检验分析聚类间的基因重叠情况,结合PanglaoDB数据库的NK细胞标记基因进行验证,比较不同路径中标记基因的表达模式。
结果解读:发现NK细胞路径的Cluster 0(C0P2)与T细胞路径的Cluster 2(C2P7、C2P6)存在显著基因重叠;C0P2中包含14个NK细胞标记基因(超几何检验P<0.001),基因表达持续上调,而C2P7中仅包含4个标记基因(P<0.001),且仅在路径早期表达上调,C2P6中无NK细胞标记基因(如图5),揭示了NK细胞与T细胞命运决定的核心基因表达差异,为细胞命运调控机制解析提供了关键线索。
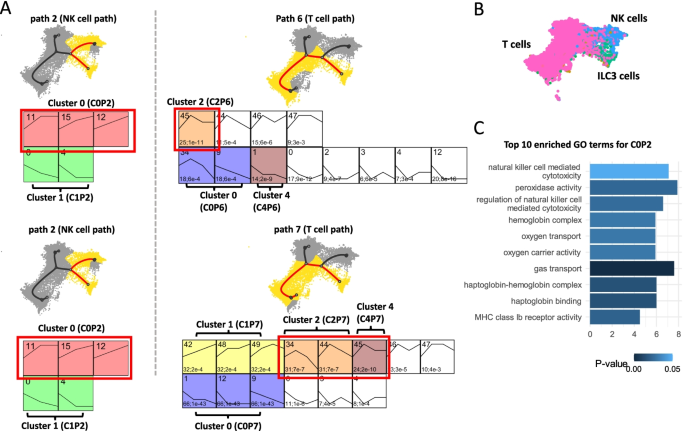
产品关联:文献未提及具体实验产品,领域常规使用细胞标记基因数据库(如PanglaoDB)及统计检验方法。
3.5 与现有方法的性能比较
实验目的:比较scSTEM与现有单细胞基因聚类、差异表达分析方法的性能,验证工具的优越性。
方法细节:选取人类胎儿免疫细胞数据的NK细胞路径(n=4058,3000个基因),比较scSTEM与scHOT、tradeSeq(聚类方法)、Monocle 3、tradeSeq(差异表达方法)的结果,以NK基因比率(NK功能基因数/聚类/差异基因数)为核心评价指标,同时比较计算效率。
结果解读:scSTEM的NK基因比率最高(5.98%),显著高于其他方法(scHOT为0%,Monocle 3差异分析为3.39%,tradeSeq差异分析为3.72%,tradeSeq聚类为0%);计算效率方面,scSTEM耗时60秒,仅次于Monocle 3的16秒,远快于tradeSeq(>10000秒)与scHOT(>40000秒);此外,scSTEM仅生成2个显著聚类,结果更简洁,易于生物学解释,综合性能优于现有方法。
产品关联:文献未提及具体实验产品,领域常规使用生物信息学性能评价指标与统计方法。
4. Biomarker研究及发现成果解析
本研究中涉及的Biomarker为路径特异性的功能基因模块,包括NK细胞毒性相关基因群、T细胞活化相关基因群、免疫应答相关基因群等,这些基因模块可作为细胞命运状态与功能的分子标志物,通过伪时间轨迹聚类、功能富集与标记基因验证的完整逻辑链进行筛选与验证。
Biomarker定位:本研究中的Biomarker属于功能基因模块类型,筛选逻辑遵循“伪时间轨迹路径选择→基因表达汇总→STEM聚类→GO富集分析→标记基因验证”的完整链条,通过轨迹特异性的基因聚类,识别与细胞命运功能相关的基因集合;验证逻辑包括多数据集重复验证、跨方法比较与公共数据库验证,确保Biomarker的生物学可靠性。
研究过程详述:Biomarker来源于三个不同的scRNA-seq数据集的细胞转录组数据,验证方法包括GO富集分析、超几何检验与标记基因数据库比对;特异性与敏感性数据方面,NK细胞路径的Cluster 0(C0P2)中NK细胞标记基因富集的超几何检验P<0.001,GO富集分析的校正P值=0.004;小鼠胚胎血细胞数据中免疫应答相关聚类的GO富集结果显示白细胞介素相关、吞噬作用相关术语显著富集(文献未明确具体P值);小鼠胚胎神经嵴细胞数据中神经元发育相关聚类的表达模式在不同路径呈现特异性差异。
核心成果提炼:这些功能基因模块作为Biomarker,能够有效表征细胞命运的功能状态,例如NK细胞路径的基因模块可作为NK细胞活化与功能执行的分子标志物,其与T细胞路径的表达差异揭示了细胞命运分支的核心机制;创新性在于首次通过伪时间轨迹的基因聚类,识别了路径特异性的功能Biomarker,为细胞命运决定的分子机制解析提供了新的视角;统计学结果包括超几何检验P<0.001、GO富集校正P=0.004,样本量覆盖从22283到103766个细胞,确保了结果的可靠性。
