1. 领域背景与文献引入
文献英文标题:The combinatorial approach of laser-captured microdissection and reverse transcription quantitative polymerase chain reaction accurately determines HER2 status in breast cancer;发表期刊:Biomark Res;影响因子:未公开;研究领域:乳腺癌精准诊断与生物标志物研究
领域共识:人表皮生长因子受体(HER)家族包括HER1(EGFR)、HER2、HER3、HER4,参与细胞增殖、分化与存活调控,其功能异常与肺癌、乳腺癌等多种肿瘤的发生发展密切相关。其中HER2是乳腺癌领域的核心靶向治疗标志物,约20%的乳腺癌患者存在HER2基因扩增与蛋白过表达,这类患者的肿瘤侵袭性更强、转移风险更高,同时对曲妥珠单抗、帕妥珠单抗等HER2靶向治疗药物敏感。临床中HER2检测的金标准为免疫组化(IHC)和荧光原位杂交(FISH),但这两种方法存在标准化程度低、实验室操作技术变异大、结果判读主观性强等核心问题,可能导致部分患者错失靶向治疗机会或接受不必要的治疗。现有研究尝试用逆转录定量PCR(RT-qPCR)检测HER2 mRNA表达,但因多采用全肿瘤组织RNA,受基质细胞等非肿瘤成分干扰,假阴性率较高,精准性未得到临床认可。基于此,本研究旨在验证激光捕获显微切割(LCM)富集癌细胞后结合RT-qPCR检测HER2状态的准确性,为临床提供更精准、可标准化的HER2检测方法。
2. 文献综述解析
本文综述围绕HER2检测的临床需求与现有技术局限性展开,作者按检测技术类型分类评述了HER2检测方法的研究现状,明确了现有方法的瓶颈与研究空白。
首先,作者系统梳理了HER家族的生物学功能与临床意义,指出HER2作为乳腺癌靶向治疗标志物的核心地位,以及精准检测对患者分层治疗的必要性。其次,针对现有临床检测方法,作者总结了IHC与FISH的优势与不足:IHC操作简便但为半定量检测,结果判读依赖病理医师经验,存在主观偏差;FISH定量准确性更高,但操作复杂、成本高,且受样本处理条件影响较大。对于RT-qPCR方法,作者回顾了既往研究的矛盾结果,指出既往研究因未排除非肿瘤细胞干扰,导致RT-qPCR与金标准方法的一致性较低,假阴性率高是限制其临床应用的关键问题。最后,作者提出本研究的创新方向:通过LCM富集纯癌细胞样本,消除基质细胞干扰,验证RT-qPCR检测HER2的准确性,同时探索HER3、HER4作为补充生物标志物的潜在价值,弥补现有研究在样本纯度控制与多标志物分析方面的不足。
3. 研究思路总结与详细解析
本研究的核心目标是验证LCM结合RT-qPCR检测乳腺癌HER2状态的准确性,核心科学问题是如何消除非肿瘤细胞干扰以提高RT-qPCR检测HER2的精准性,技术路线遵循“样本分组→多方法平行检测→结果一致性分析→补充标志物探索”的逻辑闭环,通过对比全肿瘤组织与LCM富集样本的RT-qPCR结果,明确LCM的必要性,并分析HER家族其他成员的表达特征。
3.1 样本制备与分组
实验目的是获取标准化的福尔马林固定石蜡包埋(FFPE)乳腺导管癌样本,明确HER2状态的金标准分组。方法细节:选取30例FFPE乳腺导管癌样本,先通过IHC与FISH确定HER2状态,其中10例为HER2阳性,20例为HER2阴性(n=30)。使用Leica RM 2255切片机制备5μm厚FFPE切片,用于LCM操作;切片经苏木精-伊红(HE)快速染色后,在Leica DM6000B显微镜下通过CryLaS FTSS 355-50激光捕获系统富集约10000个癌细胞,同时保留全肿瘤组织样本用于对比。结果解读:成功完成30例样本的LCM富集与全肿瘤组织样本制备,为后续检测提供了纯癌细胞与混合细胞两种样本类型。实验所用关键产品:Leica RM 2255切片机、Leica FrameSlides(PET-Membrane 1.4 μm)、Leica DM6000B显微镜、CryLaS FTSS 355-50激光捕获系统。
3.2 三种HER2检测方法的实验操作
实验目的是通过IHC、FISH与RT-qPCR三种方法平行检测HER2状态,为结果对比提供数据基础。方法细节:IHC采用Dako Autostainer Universal Staining System,使用兔多克隆HER2抗体(Dako,A0485),按标准流程进行脱蜡、抗原修复、染色与显色;FISH采用Abbott的Vysis TOP2A/HER2/CEP 17 FISH探针试剂盒,调整预处理条件为80℃柠檬酸盐缓冲液处理70分钟,按ASCO/CAP指南判读结果;RT-qPCR方面,分别从全肿瘤组织与LCM富集癌细胞中提取RNA(Qiagen RNeasy FFPE试剂盒),经Roche Transcriptor First Strand cDNA Synthesis Kit反转录为cDNA,采用Life Technologies的TaqMan基因表达探针检测HER2 mRNA,以EEF1A1为内参,采用比较Cq法计算相对表达量。结果解读:IHC与FISH结果一致,成功将30例样本分为HER2阳性与阴性两组;RT-qPCR完成两种样本类型的HER2 mRNA定量检测,获得相对表达数据。实验所用关键产品:Dako Autostainer Universal Staining System、Dako HER2抗体(A0485)、Abbott Vysis TOP2A/HER2/CEP 17 FISH Probe Kit、Qiagen RNeasy FFPE试剂盒、Roche Transcriptor First Strand cDNA Synthesis Kit、Life Technologies TaqMan Gene Expression Assays、Qiagen Qiagility自动移液系统、Qiagen Rotor-Gene Q PCR仪。
3.3 检测结果一致性分析
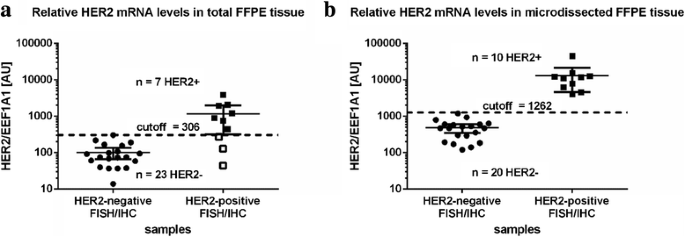
实验目的是对比不同样本类型的RT-qPCR结果与金标准的一致性,验证LCM对检测准确性的提升作用。方法细节:采用Budczies等开发的Cutoff Finder算法确定HER2 mRNA表达的临界值,将RT-qPCR结果分为阳性与阴性,分别对比全肿瘤组织与LCM富集样本的RT-qPCR结果与IHC/FISH金标准的一致性,采用Mann-Whitney检验分析组间差异。结果解读:全肿瘤组织的RT-qPCR结果中,10例HER2阳性样本仅7例被正确识别,假阴性率为30%(n=10);而LCM富集癌细胞的RT-qPCR结果与IHC/FISH完全一致,所有HER2阳性样本的mRNA相对表达量显著高于阴性样本(P<0.0001,n=30),证明LCM可有效消除非肿瘤细胞干扰,提高RT-qPCR检测的准确性。对应结果图:
3.4 HER家族其他成员表达分析
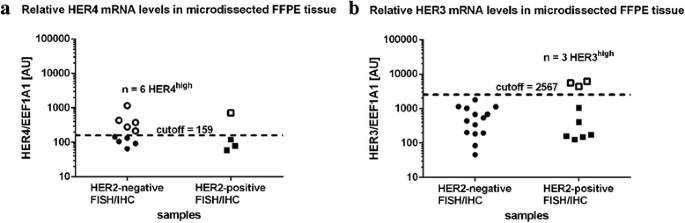
实验目的是探索HER3、HER4作为补充生物标志物的潜在价值,细化乳腺导管癌的分子分型。方法细节:采用RT-qPCR检测30例LCM富集样本中HER1(EGFR)、HER3、HER4的mRNA表达,同样以EEF1A1为内参,采用Cutoff Finder算法划分表达高低组,分析其与HER2状态的关联。结果解读:HER1仅在10%的样本中低表达;HER4在约50%的样本中表达,高低表达组差异显著(P<0.001,n=30),且与HER2状态无显著关联;HER3在90%的HER2阳性样本与70%的HER2阴性样本中表达,其中HER2阳性样本中存在部分HER3高表达的亚群,提示HER3可作为HER2阳性乳腺癌的补充标志物。对应结果图:
4. Biomarker研究及发现成果解析
本文围绕HER2核心生物标志物展开,同时探索了HER3、HER4作为补充标志物的价值,通过LCM富集样本的RT-qPCR检测,实现了HER2状态的精准判定,并揭示了HER家族成员的表达异质性。
Biomarker定位:核心生物标志物为HER2 mRNA,筛选与验证逻辑为“金标准方法(IHC/FISH)分组→全肿瘤组织RT-qPCR初筛→LCM富集样本RT-qPCR验证”,通过消除非肿瘤细胞干扰,确保RT-qPCR结果的准确性;HER3、HER4为潜在补充生物标志物,基于HER家族的协同作用,探索其对乳腺导管癌分型的价值。研究过程详述:HER2的样本来源为FFPE乳腺导管癌组织,验证方法为RT-qPCR,LCM富集癌细胞后,RT-qPCR检测的特异性与敏感性均为100%(n=30),与IHC/FISH金标准完全一致;HER3的样本来源同样为LCM富集癌细胞,验证方法为RT-qPCR,其高表达亚群主要存在于HER2阳性样本中;HER4在50%的样本中表达,高低表达组的差异具有统计学意义(P<0.001,n=30),但与HER2状态无显著关联。核心成果提炼:LCM结合RT-qPCR可作为精准检测HER2状态的方法,弥补了现有RT-qPCR方法的假阴性问题;HER3作为HER2阳性乳腺癌的补充标志物,可能与靶向治疗反应或预后相关(推测:HER3高表达的HER2阳性乳腺癌可能对HER2/HER3双靶向治疗更敏感,需进一步临床验证);HER4的临床意义尚未明确,需更大样本量研究探索其与乳腺癌预后或治疗反应的关联。
