1. 领域背景与文献引入
文献英文标题:Simple but powerful interactive data analysis in R with R/LinkedCharts;发表期刊:Genome Biology;影响因子:未公开;研究领域:生物信息学-交互式数据可视化。
生物信息学领域伴随组学技术的快速发展,数据量与复杂度呈指数级增长,传统静态数据可视化已无法满足研究者多维度、深层次探索数据的需求。交互式可视化技术自20世纪70年代起步,目前已广泛应用于科研、营销、新闻等多个领域,其核心优势在于允许用户自主选择数据观察视角,提升数据探索效率与研究结果的可信度。当前生物信息学领域的交互式可视化工具可分为两大类别:一类是针对特定数据类型的专用工具,涵盖代谢图谱可视化、基因组组装可视化、单细胞RNA测序数据分析、QTL数据可视化等方向,这类工具能够精准适配特定数据的结构与分析需求,但仅能应用于单一数据类型,通用性不足;另一类是通用可视化框架,低层级框架如D3.js、Vega-Lite具备极高的灵活性,可实现复杂的交互式设计,但需要开发者掌握JavaScript编程技能;高层级R/Python框架如Shiny、plotly、Bokeh等虽降低了编程门槛,但在图表链接功能上存在显著不足,复杂的事件处理仍需依赖JavaScript代码,这与生物信息学家主要使用R语言的工作习惯不匹配,导致这类工具的实际应用效率受限。现有工具的核心缺口凸显了开发一款基于R语言、支持原生R事件处理的通用交互式可视化工具的必要性,本文正是针对这一问题,开发了R/LinkedCharts包。
2. 文献综述解析
作者将领域内现有交互式可视化研究分为专用工具与通用框架两大类别,系统梳理了各类工具的优势与局限性,明确了R生态中通用交互式可视化工具的核心缺口。
针对特定数据类型的专用交互式工具,能够为代谢图谱、基因组组装、单细胞RNA测序数据等特定数据提供定制化的交互功能,精准适配数据结构与分析需求,但这类工具的局限性十分明显,仅能应用于单一数据类型,无法满足跨类型数据的通用可视化需求。通用可视化框架则分为低层级与高层级两类,低层级框架如D3.js、Vega-Lite具备极高的灵活性,可实现复杂的交互式设计,但需要开发者掌握JavaScript编程技能,学习成本较高;高层级框架如Shiny、plotly、Bokeh等虽面向R/Python用户,降低了编程门槛,但在图表链接功能上存在显著不足,多数工具仅支持简单的交互操作,复杂的图表联动与事件处理仍需依赖JavaScript代码,这与生物信息学家主要使用R语言的工作习惯不匹配,导致这类工具的实际应用效率受限。通过对比现有研究的局限性,本文的创新价值得以凸显:R/LinkedCharts首次在R语言环境中实现了基于原生R事件处理的通用交互式图表链接功能,无需开发者编写JavaScript代码即可完成多图表联动、数据回溯等复杂交互式分析,填补了R生态中通用交互式可视化工具的核心缺口,为生物信息学家提供了一款适配其工作流的高效工具。
3. 研究思路总结与详细解析
本文的研究目标是开发一款简单易用、支持图表链接的R语言交互式可视化包,核心科学问题是如何在R环境中实现无需依赖JavaScript的交互式图表链接与事件处理,技术路线采用“底层核心构建-跨语言通信桥梁开发-R包封装-多场景验证”的闭环逻辑,最终完成R/LinkedCharts工具的开发与功能验证。
3.1 工具核心架构设计与实现
实验目的是构建R语言与JavaScript前端的高效通信桥梁,实现原生R代码对交互式事件的处理能力。方法细节:以D3.js为基础构建linked-charts.js核心库,负责前端交互式图表的渲染;通过jrc包搭建R与JavaScript的通信层,基于httpuv包实现WebSocket双向通信,确保R代码与前端事件的实时交互;开发R包rlc(即R/LinkedCharts),封装所有核心功能,为用户提供简洁的R函数接口。结果解读:成功实现了R代码与JavaScript前端的无缝通信,用户可在R中编写事件处理函数,无需编写JavaScript代码即可完成多图表联动,例如点击散点图中的数据点可实时触发另一图表的内容更新;工具核心架构具备良好的扩展性,支持后续添加新的图表类型与交互功能。产品关联:文献未提及具体实验产品,领域常规使用R语言环境、D3.js JavaScript库、httpuv、jrc等R包。
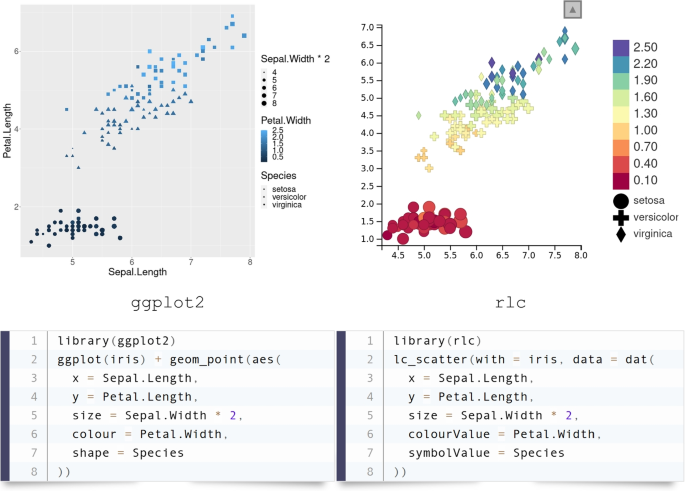
3.2 基础功能与语法兼容性验证
实验目的是验证R/LinkedCharts的易用性与R生态系统的兼容性,降低用户的学习成本。方法细节:对比R/LinkedCharts与广泛使用的ggplot2包的语法结构,测试工具支持的15种核心图表类型(包括散点图、热图、柱状图、蜂群图等)的渲染效果;验证工具与HTML5页面的集成能力,测试静态元素添加、布局定制等功能。结果解读:R/LinkedCharts的语法与ggplot2高度相似,用户仅需少量学习即可快速上手,例如散点图的绘制函数lc_scatter与ggplot2的ggplot+geom_point逻辑一致;工具支持多种图表类型,可满足不同场景的可视化需求;同时可无缝集成到HTML5页面中,用户可通过HTML定制应用的布局与装饰元素,提升应用的展示效果。
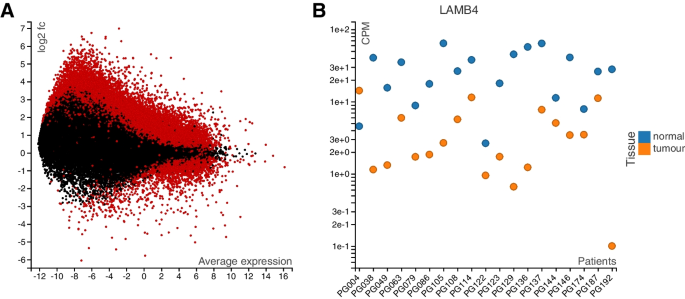
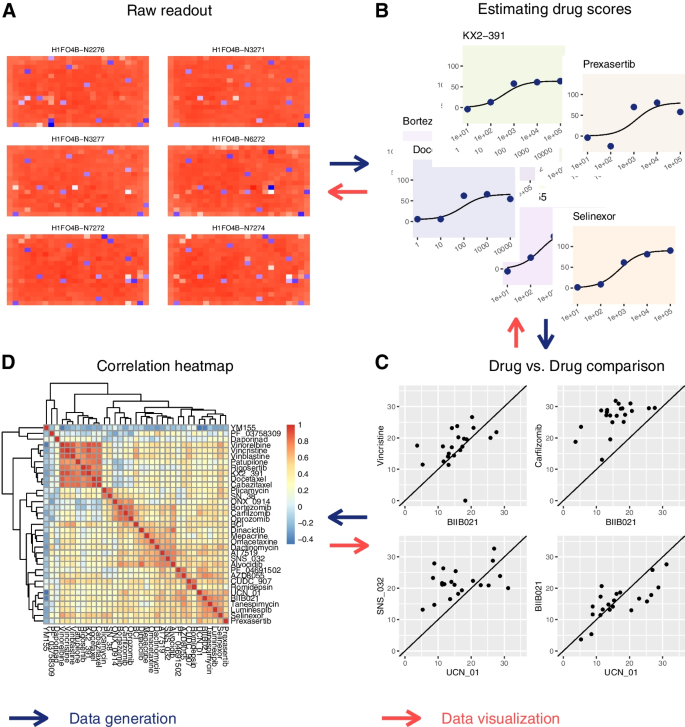
3.3 多场景功能验证与应用
实验目的是验证R/LinkedCharts在不同生物信息学数据分析场景中的实用性与灵活性。方法细节:设计多个典型应用场景,包括差异基因表达分析的图表联动、药物筛选分析 pipeline 的回溯验证、质量控制阈值优化、探索性数据分析、多用户协作分析、复杂GUI开发等;分别使用口腔癌基因表达数据、药物筛选细胞活力数据、SARS-CoV-2 LAMP检测数据等进行测试。结果解读:在差异基因表达分析场景中,点击MA图中的差异基因点,可实时查看该基因在所有样本中的表达细节,帮助研究者快速验证差异基因的可靠性;在药物筛选pipeline回溯场景中,可从最终的药物相关性热图逐层回溯至原始微孔板数据,便于排查数据异常与分析错误;工具支持多用户同时访问,可通过网络共享交互式应用,满足团队协作需求;还可构建复杂的图形用户界面,如SARS-CoV-2 LAMP检测结果的手动审核界面,提升临床检测的质量控制效率。
4. Biomarker研究及发现成果
本文为生物信息学工具开发类研究,未涉及生物标志物(Biomarker)的筛选、验证与功能研究相关内容,核心成果为成功开发了R/LinkedCharts交互式可视化包,填补了R生态中通用交互式可视化工具的核心缺口。
R/LinkedCharts的核心创新与价值体现在三个方面:一是首次在R语言环境中实现了基于原生R事件处理的通用交互式图表链接功能,无需依赖JavaScript即可完成复杂的多图表联动与事件响应,适配生物信息学家的工作习惯;二是语法与广泛使用的ggplot2包高度兼容,显著降低了用户的学习成本,便于快速集成到现有数据分析工作流中;三是支持多用户协作访问与HTML5页面集成,可满足从探索性数据分析到研究成果展示的全流程需求。该工具已开源发布于CRAN,可通过标准R包安装流程获取,为生物信息学家的交互式数据分析提供了高效、灵活的解决方案。
