1. 领域背景与文献引入
文献英文标题:Strong functional patterns in the evolution of eukaryotic genomes revealed by the reconstruction of ancestral protein domain repertoires;发表期刊:Genome Biology;影响因子:未公开;研究领域:真核生物基因组进化、蛋白质域功能演化。
真核生物基因组进化领域长期存在“基因数目悖论”——物种形态复杂度与蛋白编码基因数目无显著线性相关性,例如人类基因组约含20500个蛋白编码基因,而形态相对简单的秀丽隐杆线虫约含19000个,果蝇仅约14000个。为解释这一悖论,学界提出了非编码RNA调控、可变剪接、转录调控复杂度提升、蛋白质域组合多样性等多种假说,但针对蛋白质域(功能最小结构与演化单位)的全尺度演化动态及其对功能组的影响研究仍存在空白。传统观点认为真核生物最后共同祖先(LECA)结构简单,通过基因或蛋白质域的逐步积累形成复杂生物,但近年研究显示LECA可能已具备接近现代真核生物的内膜系统与细胞分裂机制,基因丢失在演化中的作用逐渐受到重视,但缺乏跨类群的祖先蛋白质域组重建分析以量化其动态规律。本研究正是针对这一领域空白,通过重建关键演化节点的祖先蛋白质域组,系统揭示真核生物演化中蛋白质域的得失动态及功能偏向,为“基因数目悖论”提供蛋白质域层面的新解释,填补功能组演化规律的认知缺口。
2. 文献综述解析
作者对领域内现有研究的分类维度包括:真核生物共同祖先(LECA)的结构复杂度假说(简单起源vs复杂起源)、“基因数目悖论”的解释方向(非编码区调控、转录调控网络、蛋白质域结构)、基因丢失在演化中的作用(特定类群分析vs全尺度跨类群分析)。
支持LECA复杂起源的研究表明,其已具备内膜系统、细胞分裂调控机制等现代真核生物的核心特征,为真核生物演化的“减少演化”假说提供了初步证据;针对“基因数目悖论”的解释中,非编码RNA调控、可变剪接增加蛋白质多样性等假说得到部分实验验证,但从蛋白质域层面解析演化动态的研究相对较少;基因丢失的研究多聚焦于线虫等特定类群,缺乏覆盖主要真核生物超类群的全尺度分析,且未系统关联蛋白质域得失与功能组变化的规律。现有研究的局限性在于,未通过祖先蛋白质域组的系统重建来量化域的得失平衡,也未明确功能域得失的偏向性对物种形态复杂度的调控机制。本研究的创新价值在于,首次对114个真核生物基因组的蛋白质域进行全尺度分析,结合Dollo简约法重建关键演化节点的祖先域组,系统揭示了真核生物演化中蛋白质域得失的功能偏向性,尤其是动物演化过程中调控类域显著增加、代谢类域大量丢失的核心规律,为“基因数目悖论”提供了蛋白质域层面的全新解释视角。
3. 研究思路总结与详细解析
本研究的目标是揭示真核生物基因组蛋白质域的演化动态及功能偏向性,核心科学问题为真核生物演化中蛋白质域得失的平衡规律、功能偏向及其与物种形态复杂度的关联,技术路线遵循“现有基因组蛋白质域分析→祖先域组重建→功能组富集分析→演化规律验证与拓展”的闭环逻辑。
3.1 全尺度真核生物蛋白质域数据集构建
实验目的:构建覆盖主要真核生物类群的蛋白质域组成数据集,为后续演化分析提供基础数据支撑。
方法细节:收集114个真核生物基因组的预测蛋白序列,涵盖后鞭毛生物(38个动物、1个领鞭毛虫、34个真菌)、变形虫、古虫等5个真核生物超类群;使用HMMER 3.0b2软件结合Pfam 24.0数据库的隐马尔可夫模型,以Pfam提供的“gathering”阈值筛选蛋白质域,同时去除病毒、转座子来源的域及重叠域以保证数据准确性。
结果解读:不同物种的蛋白质域数目存在差异,从自由生活的纤毛虫Paramecium tetraurelia的约2000个到人类的约4240个,但物种形态复杂度与蛋白质域数目无严格正相关,例如形态简单的多细胞动物Trichoplax adhaerens的蛋白质域数目(约3140个)高于部分形态更复杂的物种,再次验证了“基因数目悖论”在蛋白质域层面的体现。
文献未提及具体实验产品,领域常规使用HMMER蛋白质域分析软件、Pfam蛋白质域数据库。
3.2 关键演化节点祖先蛋白质域组重建
实验目的:推断真核生物关键演化节点(如LECA、Urbilateria,即原口动物与后口动物的共同祖先)的蛋白质域组成,量化演化过程中蛋白质域的得失动态。
方法细节:采用Dollo简约法(假设每个蛋白质域仅能在演化中获得一次,以最小化丢失事件为原则),结合已发表的真核生物演化树拓扑结构,重建各祖先节点的蛋白质域组;分别计算各演化分支的蛋白质域获得与丢失数目,对比不同类群的演化模式差异。
结果解读:真核生物最后共同祖先(LECA)的蛋白质域组约含4400个域,数目大于所有现存真核生物物种,表明真核生物演化整体以蛋白质域丢失为主;仅在动物起源及脊椎动物起源的分支中,蛋白质域获得数目显著超过丢失数目;后口动物与原口动物起源分支伴随大量蛋白质域丢失,其中后口动物分支约丢失366个域、获得11个域,原口动物分支约丢失252个域、获得16个域。
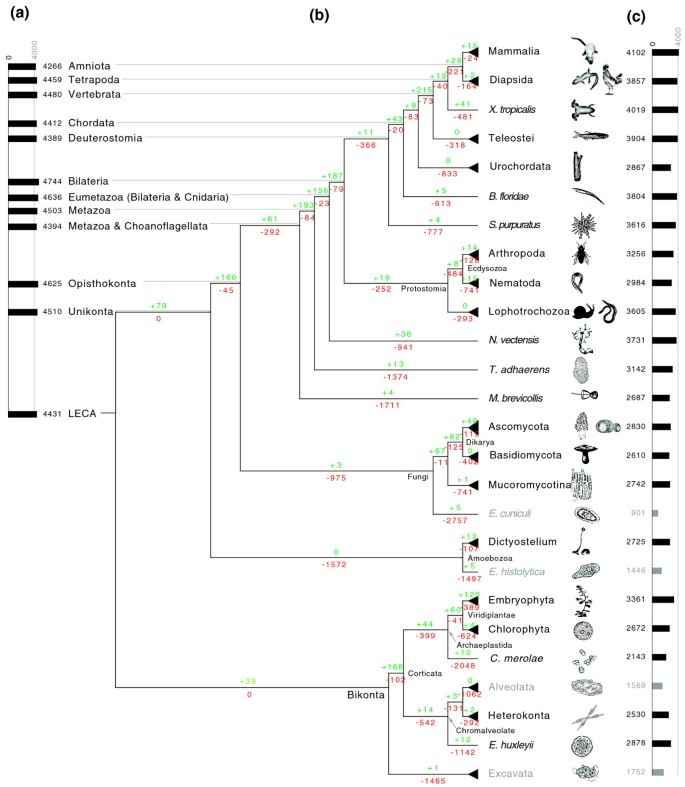
文献未提及具体实验产品,领域常规使用基于Dollo简约法的祖先序列重建工具(如forester软件)。
3.3 蛋白质域的功能组富集与偏向性分析
实验目的:解析演化过程中获得与丢失蛋白质域的功能偏向性,揭示功能组的演化规律。
方法细节:通过Pfam到基因本体(GO)的映射关系,构建各现存物种及祖先域组的功能谱;使用Ontologizer 2.0软件结合Topology-Elim算法,对各演化分支获得与丢失的蛋白质域进行GO功能富集分析,对比不同类群的功能变化趋势。
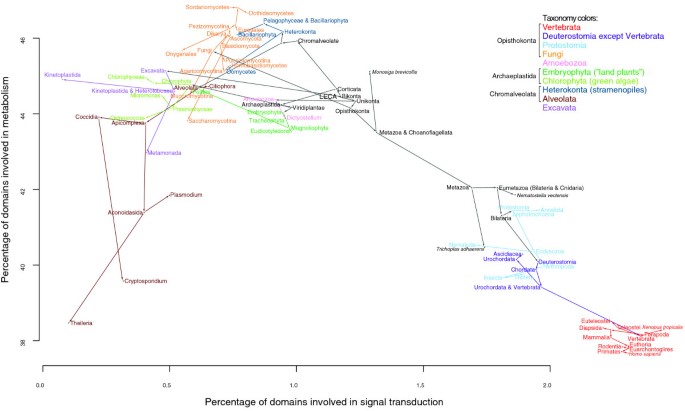
结果解读:动物演化过程中,获得的蛋白质域主要富集于DNA依赖的转录调控、细胞-基质黏附、细胞凋亡、信号转导等调控类功能,丢失的蛋白质域主要富集于氨基酸生物合成、碳水化合物代谢等代谢类功能;其他真核生物类群中,调控类域与代谢类域均以丢失为主,但调控类域的丢失程度显著低于代谢类域,例如开花植物演化中,调控类域每分支平均丢失5.6个,代谢类域每分支平均丢失18.8个。
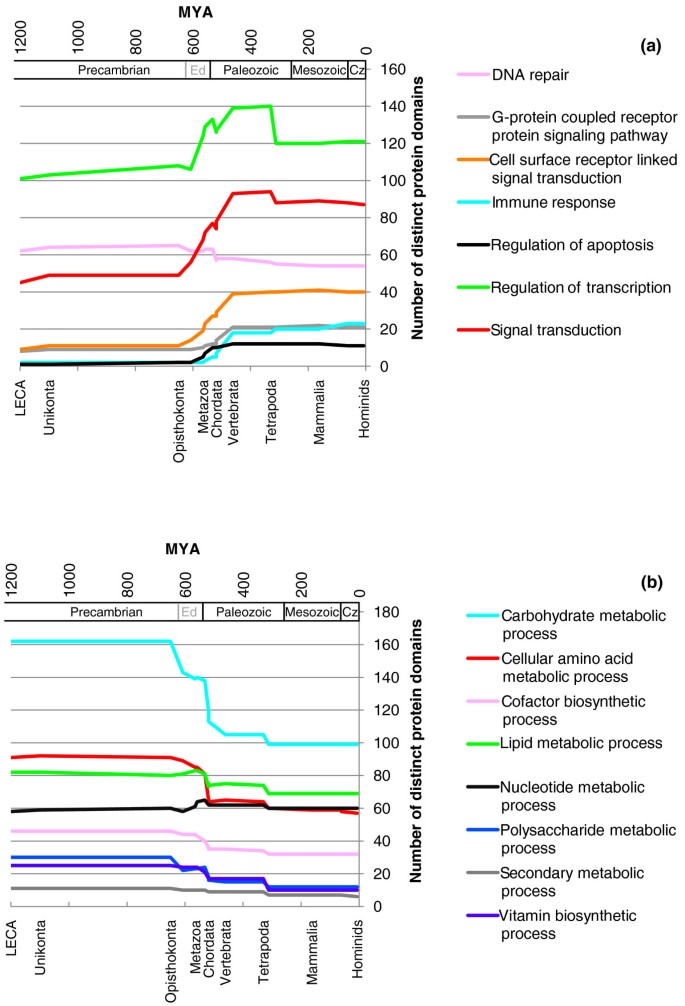
文献未提及具体实验产品,领域常规使用GO数据库、Ontologizer功能富集分析软件。
3.4 演化规律的稳健性验证与拓展分析
实验目的:验证功能组演化规律的稳健性,探讨动物演化中代谢功能丢失的补偿机制。
方法细节:采用不同的演化树拓扑结构(如体腔动物假说、冠群模型)重复祖先蛋白质域组重建分析,验证核心结论的稳健性;分析人类基因组与肠道共生菌(Bacteroides thetaiotaomicron和Eubacterium rectale)的蛋白质域组叠加后的功能谱,探讨代谢功能丢失的补偿机制。
结果解读:不同演化树模型下,动物演化中调控类域增加、代谢类域丢失的核心趋势保持一致,表明结论具有较强的稳健性;人类基因组与两种肠道共生菌的蛋白质域组叠加后,代谢类域的功能谱与LECA高度相似,提示共生微生物可能补偿了动物演化过程中丢失的代谢功能。
文献未提及具体实验产品,领域常规使用微生物基因组数据库、共生组功能分析工具。
4. Biomarker研究及发现成果解析
本研究中的Biomarker为真核生物不同演化分支中获得或丢失的特征性蛋白质功能域,其筛选逻辑为“全基因组蛋白质域分析→祖先域组重建→功能富集分析→特征功能域鉴定”,验证逻辑包括不同演化树模型的稳健性验证、共生组补偿机制的功能验证,完整覆盖了从发现到验证的全链条。
这些特征性功能域Biomarker来源于114个真核生物基因组的蛋白质域数据及重建的7个关键演化节点的祖先域组;验证方法包括基于Dollo简约法的祖先域组推断、GO功能富集分析、不同演化树拓扑结构的重复验证;特异性方面,动物起源分支中获得的调控类域(如转录因子域、G蛋白偶联受体信号转导域)具有显著的类群特异性,而丢失的代谢类域(如氨基酸生物合成域)在其他真核生物类群中普遍保留;敏感性方面,通过功能谱聚类分析,不同真核生物类群的功能域谱与演化树拓扑结构高度一致,表明特征功能域能准确反映物种的演化关系。
本研究鉴定的特征功能域Biomarker揭示了真核生物演化的核心功能偏向——整体以蛋白质域丢失为主,动物演化过程中调控复杂度显著增加、代谢能力逐步降低;首次提出共生微生物补偿动物代谢功能丢失的假说,为真核生物演化中功能组的变化机制提供了全新视角;通过不同演化树模型、不同阈值的重复分析,核心结论的稳健性得到验证,虽未明确提供具体P值,但多次独立分析的一致性支持结论的统计学可靠性。此外,特征功能域Biomarker为真核生物演化关系的解析提供了新的分子标记,可应用于未知类群的演化地位推断。
