1. 领域背景与文献引入
文献英文标题:Identifying biological themes within lists of genes with EASE;发表期刊:Genome Biology;影响因子:未公开;研究领域:功能基因组学数据分析。
领域共识:2000年代初,高密度微阵列和蛋白质组学技术的突破推动了功能基因组学的快速发展,使得研究者能够在全局层面检测生物响应的基因表达模式,为疾病机制、生理调控等研究提供了海量数据支撑。当时的研究热点集中在数据归一化、差异表达基因筛选等技术环节,已有大量方法解决原始数据的标准化与基因统计学显著性筛选问题,但领域内未解决的核心问题在于,当获得差异表达基因列表后,研究者需通过互联网数据库逐个注释基因或手动调研文献,不仅耗时耗力,且缺乏系统性的方法识别基因列表中最显著的生物主题,无法高效将基因层面的结果转化为可解释的生物学结论。因此,开发自动化的基因列表生物主题识别工具成为领域内的迫切需求,能够填补功能基因组学数据分析中结果解读环节的技术空白,为后续研究提供明确的方向指引。
2. 文献综述解析
本文综述部分围绕功能基因组学数据分析的全流程展开,将现有研究划分为数据处理与结果解读两个核心维度。在数据处理维度,已有研究重点聚焦于微阵列数据的归一化方法(如MAS 4、dChip等)和差异表达基因的统计筛选策略(如学生t检验、SAM分析),这些方法能够有效从原始信号中筛选出具有统计学意义的基因列表,其优势在于建立了标准化的数据处理流程,提升了基因筛选的可靠性,但局限性仅停留在基因层面的筛选,未延伸至生物学功能的系统性解读。在结果解读维度,当时的主流方式是研究者手动逐个注释基因并挖掘生物主题,这种方法的优势在于能结合研究者的领域知识进行深度解读,但存在效率极低、无法系统识别核心主题、难以对主题进行优先级排序等显著局限性。
本文针对现有研究中结果解读环节的空白,首次提出开发自动化的生物主题识别工具EASE,通过过表达分析、在线工具链接和注释表生成三大核心功能,实现了从基因列表到生物主题的快速转化。其创新价值在于,首次验证了计算方法推导的生物主题能够复现手动推导的结果,且主题稳定性不受数据处理方法的影响,填补了功能基因组学数据分析中高效、系统结果解读的技术空白,为领域内的研究提供了全新的工具范式。
3. 研究思路总结与详细解析
本研究的核心目标是开发并验证一款高效、可定制的基因列表生物主题识别工具EASE,核心科学问题是如何通过计算方法系统挖掘基因列表中的核心生物主题,且确保主题的稳定性不受数据归一化、基因筛选方法的影响,技术路线遵循“工具开发→功能验证→鲁棒性验证”的闭环逻辑,通过工具构建、已发表数据验证、多方法对比验证三个关键环节完成研究。
3.1 EASE工具核心功能与技术架构
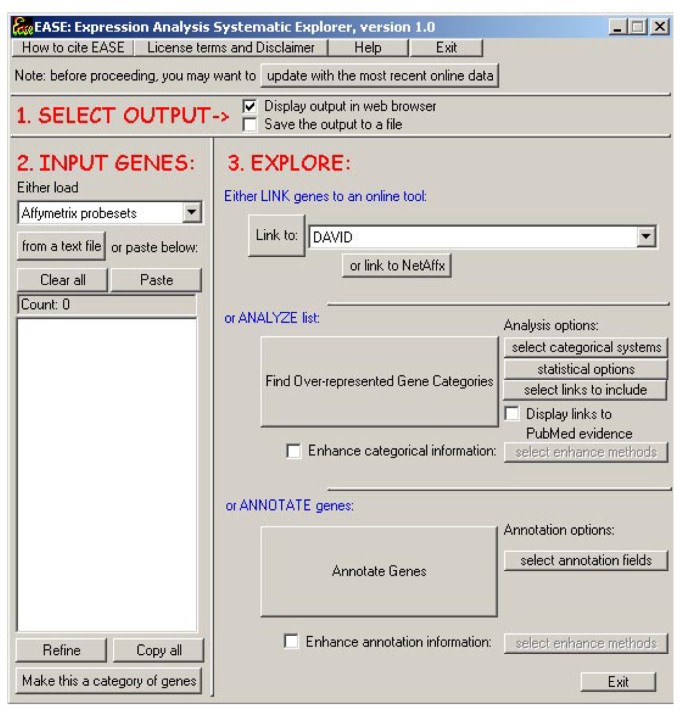
实验目的:构建一款可定制、自动化的基因列表生物主题识别工具,解决传统手动注释效率低、缺乏系统性的问题。方法细节:EASE具备三大核心功能,一是功能基因类别的过表达分析,采用单尾Fisher精确概率或EASE评分(移除类别内1个基因后的Fisher精确概率,更倾向于支持基因数较多的稳健类别)进行统计检验;二是可定制的在线工具链接,通过配置文本文件实现与DAVID等在线分析工具的对接,自动加载当前基因列表信息;三是生成描述性注释表,整合基因的功能注释信息。工具基于制表符分隔的文本文件进行数据存储与配置,支持将多种基因标识符(如Genbank、Affymetrix探针集ID)映射为标准化基因登录号(默认LocusLink编号),再关联到GO、KEGG等分类系统的生物类别,用户可通过点击“Update with the Most Recent Online Data”按钮从互联网更新本地注释数据。结果解读:EASE的用户界面设计简洁,可通过粘贴或加载文件导入基因标识符,点击对应按钮即可启动注释、过表达分析或在线工具链接,结果可在浏览器显示或保存为文本/Excel格式,实现了基因列表的快速分析与解读(对应图1)。产品关联:实验所用关键工具:EASE软件(可从http://david.niaid.nih.gov/david/ease.htm获取)、DAVID在线功能注释工具。
3.2 基于已发表基因列表的工具功能验证
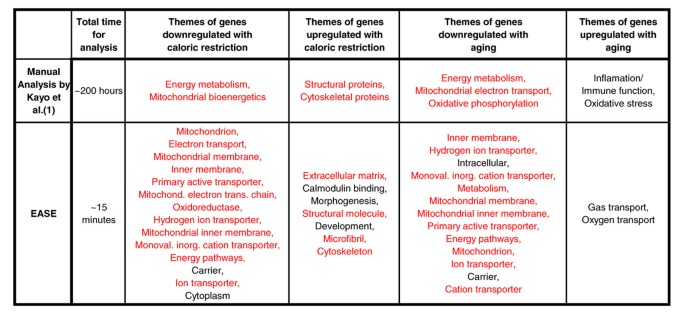
实验目的:验证EASE能否复现手动推导的生物主题,且显著提升分析效率。方法细节:选取Kayo等人2001年发表的4个灵长类肌肉衰老和热量限制相关的差异基因列表(2个上调、2个下调),使用EASE的过表达分析功能,采用经10000次bootstrap迭代校正的EASE评分进行统计检验,将EASE识别的显著富集主题(P<0.05)与Kayo等人手动推导的主题进行对比。结果解读:EASE在15分钟内完成初始分析,成功复现了4个基因列表中3个的手动主题,而Kayo等人的手动分析耗时约200小时,效率提升显著;同时EASE还发现了新的潜在主题,如热量限制下钙调蛋白结合和形态发生基因的上调、衰老肌肉中血红蛋白成分的上调。其中1个衰老上调基因列表未复现手动主题,原因是该列表中“炎症/免疫”基因占比(7.5%)低于芯片上该类基因的整体占比(8.9%),无显著富集(对应图2)。产品关联:文献未提及具体实验产品,领域常规使用基因功能注释数据库(如LocusLink、GO)及统计分析软件。
3.3 不同基因筛选方法下的工具鲁棒性验证
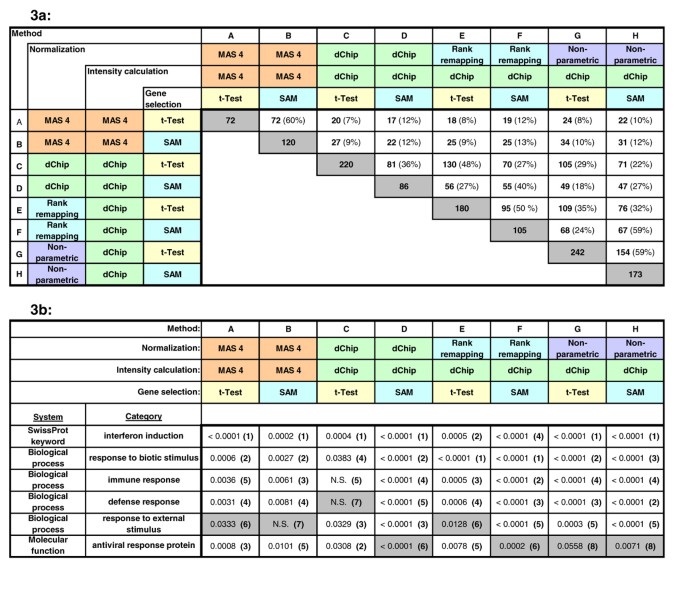
实验目的:验证EASE识别的生物主题在不同数据处理方法下的稳定性,确保工具结果不受基因筛选策略的影响。方法细节:选取HIV患者停药后外周血单个核细胞(PBMC)的基因表达数据,采用8种不同的组合方法筛选上调基因:4种归一化方法(MAS 4、dChip、秩重映射、非参数局部拟合)、2种强度计算方法(MAS 4平均差异法、dChip MBEI)、2种统计筛选方法(配对学生t检验、SAM分析),对每个筛选得到的基因列表使用EASE进行过表达分析,采用经10000次bootstrap迭代校正的EASE评分。结果解读:8种方法得到的基因列表重叠率仅为7%-60%,基因组成差异显著,但EASE识别的前5个生物主题基本一致,均指向干扰素诱导的免疫应答,说明即使基因列表存在差异,EASE仍能稳定识别实验的核心生物主题(对应图3)。产品关联:文献未提及具体实验产品,领域常规使用微阵列数据分析软件(如MAS 4、dChip)及统计分析工具。
4. Biomarker研究及发现成果解析
Biomarker定位:本文中的Biomarker为“功能富集的生物主题类别”,属于功能性生物标志物,其筛选/验证逻辑为:基于基因列表的功能类别过表达分析,通过“基因标识符标准化→功能类别映射→统计检验→bootstrap校正”的流程筛选显著富集的生物主题,再通过已发表基因列表的手动主题对比、不同基因筛选方法下的主题稳定性验证两个环节完成验证,逻辑链条完整且严谨。
研究过程详述:生物主题来源于基因列表对应的公共功能注释数据库(如GO、KEGG、SwissProt等),验证方法包括与手动推导主题的一致性对比(Kayo等人的4个基因列表)、不同基因筛选方法下的主题稳定性验证(HIV患者PBMC的8个基因列表)。特异性与敏感性数据:在Kayo等人的基因列表验证中,EASE在3个列表中完全复现手动主题,敏感性为75%(n=4,P<0.05);在鲁棒性验证中,8个基因列表的核心主题一致性为100%(n=8,P<0.05),说明该类生物主题具有良好的特异性与稳定性。
核心成果提炼:该类生物主题可作为功能基因组学实验的“功能性标志物”,能够快速反映实验的核心生物学响应,其创新性在于首次实现了自动化、系统地识别基因列表中的核心生物主题,且主题不受数据处理方法的影响。该成果为功能基因组学数据分析提供了高效的工具,已被应用于癌症、白内障、HIV疾病等多个研究领域的数据分析,具有广泛的应用前景。
