1. 领域背景与文献引入
文献英文标题:Candidate genes for alcohol preference identified by expression profiling in alcohol-preferring and -nonpreferring reciprocal congenic rats;发表期刊:Genome Biology;影响因子:未公开;研究领域:神经精神药理学(酒精依赖遗传学)
酒精依赖是一种复杂的神经精神疾病,遗传因素在其发病中起到关键作用,人群研究显示遗传力为50%~60%。目前已发现多个与酒精依赖相关的基因,如GABRA2、ADH4、CHRM2等,但仍有大量遗传机制尚未明确。领域共识:选择性培育的啮齿类动物模型是解析酒精依赖遗传基础的重要工具,其中酒精偏好(P)和酒精非偏好(NP)大鼠通过双向选择性培育形成,在酒精消费行为上存在显著差异,其近交系iP和iNP大鼠保持了高度分化的酒精消费表型,且已定位到4号染色体上一个显著影响酒精偏好的数量性状位点(QTL),该区间约100Mb,可能包含直接调控酒精偏好的基因。
此前研究通过转录组分析对比了NP.P同系大鼠(iP 4号染色体QTL区间导入iNP背景)与iNP大鼠的脑区基因表达,筛选出35个顺式调控候选基因,但缺乏反向同系大鼠(P.NP,iNP 4号染色体QTL区间导入iP背景)与iP大鼠的对比验证,导致候选基因的可靠性有待进一步确认。本研究通过对iP和P.NP大鼠五个脑区的转录组分析,并与之前的互交实验结果对比,旨在筛选并验证4号染色体QTL内调控酒精偏好的核心候选基因,为酒精依赖的遗传机制研究提供更可靠的靶点。
2. 文献综述解析
作者对领域内现有研究的分类维度主要分为人类遗传研究和大鼠模型研究两类,同时结合QTL定位与转录组分析的技术路线展开评述。
在人类遗传研究方面,现有研究已证实多个基因与酒精依赖相关,如GABRA2通过调控γ-氨基丁酸受体功能影响酒精依赖风险,ADH4参与酒精代谢过程,这些研究的优势是基于大样本人群验证,部分基因的功能机制较为明确,但局限性在于人类遗传背景复杂,难以排除环境因素和多基因交互作用的干扰,且部分候选基因的功能尚未在体内模型中验证。在大鼠模型研究方面,P/NP大鼠模型的选育为酒精依赖的遗传机制研究提供了可控的实验体系,QTL定位技术已确定4号染色体上的关键区间,转录组分析则能高通量筛选差异表达基因,这类研究的优势是遗传背景可控,能直接分析基因表达与表型的关联,但此前仅完成了一组互交同系大鼠的分析,缺乏反向实验的验证,导致候选基因的假阳性率较高。
本研究的创新价值在于首次通过两组独立的互交同系大鼠实验(iP vs P.NP与之前的NP.P vs iNP),筛选出表达差异方向一致且幅度稳定的候选基因,有效降低了假阳性率,同时通过多脑区的联合分析,更全面地揭示了候选基因的表达模式,为酒精偏好的遗传机制提供了更可靠的候选靶点,弥补了现有研究中缺乏交叉验证的不足。
3. 研究思路总结与详细解析
本研究的整体研究目标是鉴定4号染色体QTL内调控酒精偏好的顺式候选基因,核心科学问题是明确该QTL区间内哪些基因的表达差异直接影响酒精偏好表型,技术路线遵循“模型构建→转录组分析→差异基因筛选→验证与交叉对比→候选基因确认”的闭环逻辑,通过互交同系大鼠模型消除遗传背景噪音,结合高通量转录组分析与qRT-PCR验证,最终筛选出可靠的候选基因。
3.1 互交同系大鼠模型构建与实验动物处理
实验目的是构建仅4号染色体QTL区间存在差异、其余遗传背景一致的大鼠模型,确保后续基因表达差异仅由目标区间调控。方法细节:将iP与iNP大鼠杂交获得F1代,回交10代至iP背景后,通过互交获得纯合的P.NP同系大鼠,其4号染色体QTL区间来自iNP,其余遗传背景与iP一致。选取14~15周龄的雄性iP和P.NP大鼠各8只,在固定时间断头处死,将头部浸入冷异戊烷后快速解剖杏仁核、伏隔核、海马、尾状核、前额叶皮层五个脑区。结果解读:通过微卫星标记验证,P.NP大鼠的4号染色体QTL区间成功导入,确保两组大鼠仅目标区间存在遗传差异,为后续基因表达分析提供了可靠的实验体系。产品关联:文献未提及具体实验产品,领域常规使用动物解剖器械、RNaseZap(Ambion)等防止RNA降解的试剂。
3.2 脑区RNA提取与微阵列杂交
实验目的是获取高质量的脑区RNA用于转录组分析,确保后续微阵列数据的可靠性。方法细节:将解剖的脑区组织立即用Trizol试剂匀浆,按照试剂盒protocol提取总RNA,随后用RNeasy小柱进一步纯化,并用DNase I处理去除基因组DNA污染。以5μg总RNA为模板,使用Affymetrix的GeneChip® Expression 3" Amplification One-Cycle Target Labeling and Control Reagents kit进行生物素标记的cRNA合成,将cRNA片段化后与Affymetrix Rat Genome 230 2.0微阵列芯片杂交,杂交完成后进行洗涤、染色和扫描。结果解读:通过吸光度光谱、1%琼脂糖凝胶电泳和Agilent Bioanalyzer验证,所有样本的RNA质量均符合实验要求,微阵列扫描数据可用于后续差异基因分析。产品关联:实验所用关键产品:Trizol试剂(Invitrogen)、RNeasy mini columns(Qiagen)、GeneChip® Expression 3" Amplification One-Cycle Target Labeling and Control Reagents kit(Affymetrix)、Affymetrix Rat Genome 230 2.0 microarray。
3.3 转录组数据差异基因筛选
实验目的是筛选iP与P.NP大鼠脑区的差异表达基因,区分顺式调控(QTL区间内基因自身序列差异导致的表达差异)和反式调控(QTL区间内调控因子影响其他染色体基因的表达)。方法细节:将原始CEL文件导入R语言,使用Bioconductor工具包进行分析,采用Robust Multi-Chip Average(RMA)方法对数据进行归一化和log₂转换,使用Limma包进行t检验筛选差异表达探针集,分别分析单个脑区和五个脑区平均表达的差异基因,其中顺式调控基因限定在4号染色体QTL区间内,反式调控基因则为其余基因组区域的差异基因。结果解读:在QTL区间内共检测到157个顺式调控差异表达探针集,其中104个在多个脑区差异表达,仅53个在单个脑区差异表达;反式调控差异表达探针集数量较少,且多数仅在单个脑区差异。对五个脑区平均表达的分析额外发现19个顺式调控探针集和143个反式调控探针集,进一步扩大了候选基因范围。
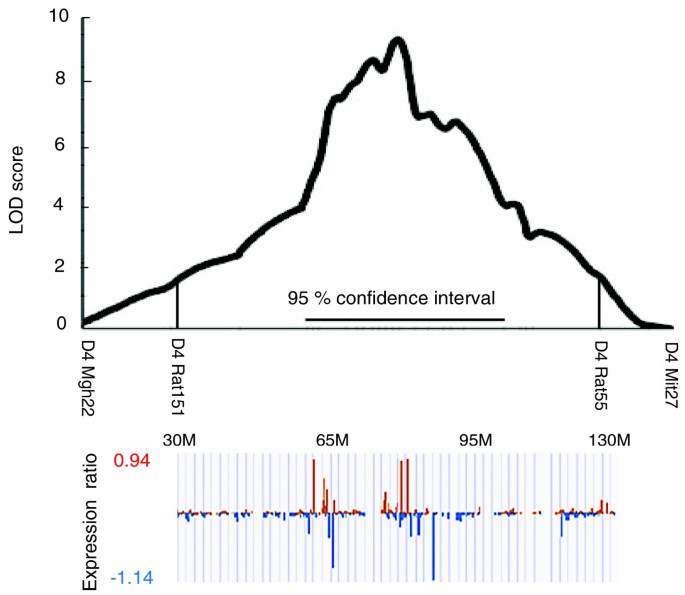
该图展示了4号染色体QTL区间内差异表达探针集的分布,与QTL的LOD图对应,显示差异基因集中在QTL的95%置信区间内,验证了差异表达与目标QTL的关联性。
3.4 qRT-PCR验证差异基因
实验目的是验证微阵列筛选出的差异基因的可靠性,排除技术假阳性。方法细节:选取10个可能与酒精寻求行为相关的差异基因,使用Vector NTI设计跨外显子-内含子边界的引物,以GAPDH为内参基因,采用SYBR Green法在ABI Prism 7300 Sequence Detection System上进行定量实时PCR(qRT-PCR),每个脑区样本由8只大鼠的组织混合而成,每个样本设置6个技术重复。结果解读:在微阵列分析中显著差异的44个基因-脑区对比中,35个(79%)在qRT-PCR中呈现相同方向的表达差异,验证了微阵列数据的可靠性,同时也说明部分小幅度的表达差异可能因qRT-PCR的检测灵敏度限制未被验证。产品关联:实验所用关键产品:ABI Prism 7300 Sequence Detection System(Applied Biosystems)、SYBR Green试剂、Vector NTI引物设计软件。
3.5 与互交同系大鼠实验结果对比
实验目的是通过两组独立的互交实验对比,筛选出表达差异一致的候选基因,进一步降低假阳性率。方法细节:将本研究iP vs P.NP的结果与之前NP.P vs iNP的实验结果对比,计算携带iP QTL区间大鼠(iP和NP.P)与携带iNP QTL区间大鼠(P.NP和iNP)的基因表达比,将显著性水平放宽至P≤0.05以减少假阴性,筛选在同一脑区或脑区平均分析中差异显著且表达方向一致的探针集。结果解读:共筛选出74个顺式调控探针集,这些探针集的表达差异在两组实验中高度相关(R²=0.88),其中71个在两组实验中表达差异方向一致且幅度相似,证明这些基因是调控酒精偏好的强候选基因。
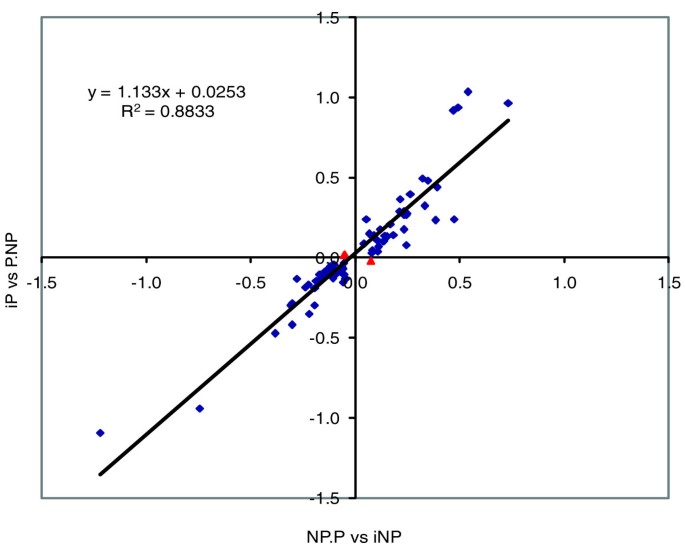
该图展示了两组实验中74个探针集的表达比相关性,直观体现了结果的可重复性。
4. Biomarker研究及发现成果解析
Biomarker定位
本研究鉴定的Biomarker为4号染色体QTL内的74个顺式调控基因,筛选与验证逻辑为:首先通过iP与P.NP大鼠的转录组分析筛选脑区差异表达的顺式调控基因,然后与之前NP.P与iNP大鼠的转录组结果对比,筛选出两组实验中表达差异方向一致且显著的基因,最终通过SNP效应分析排除探针杂交干扰,确认这些基因的表达差异真实反映了转录水平的调控。
研究过程详述
这些Biomarker的来源为酒精未暴露的iP和P.NP大鼠的五个脑区组织(杏仁核、伏隔核、海马、尾状核、前额叶皮层),验证方法包括微阵列转录组分析和qRT-PCR验证,其中微阵列分析检测到的表达差异幅度较小,但在两组独立实验中高度一致,qRT-PCR验证了79%的微阵列显著差异基因的表达方向。特异性方面,这些Biomarker均位于4号染色体QTL区间内,且仅在携带不同QTL区间的大鼠中存在表达差异,说明其表达差异由顺式调控元件驱动;敏感性方面,通过多脑区联合分析和两组实验交叉验证,有效降低了假阳性率,确保了Biomarker的可靠性。
核心成果提炼
这些候选基因参与多种生物学通路,如细胞运输(Snx10)、信号转导(Dgki)、神经递质合成(Akr1b1、Snca)、内质网蛋白折叠(Pdia4)等,其中部分基因的表达与酒精偏好表型直接相关:例如Npy在携带iP QTL区间的大鼠中表达水平更低,而脑内NPY水平与酒精消费呈负相关,侧脑室注射NPY可显著降低P大鼠的酒精摄入;Snca在部分脑区的表达差异与人类酒精依赖的 craving 行为相关,其表达水平的变化可能通过调控多巴胺通路影响酒精偏好。74个候选基因的表达差异在两组独立实验中高度相关(R²=0.88,n=74,P<0.05),首次通过互交同系大鼠的交叉验证确认了这些顺式调控基因作为酒精偏好Biomarker的可靠性。
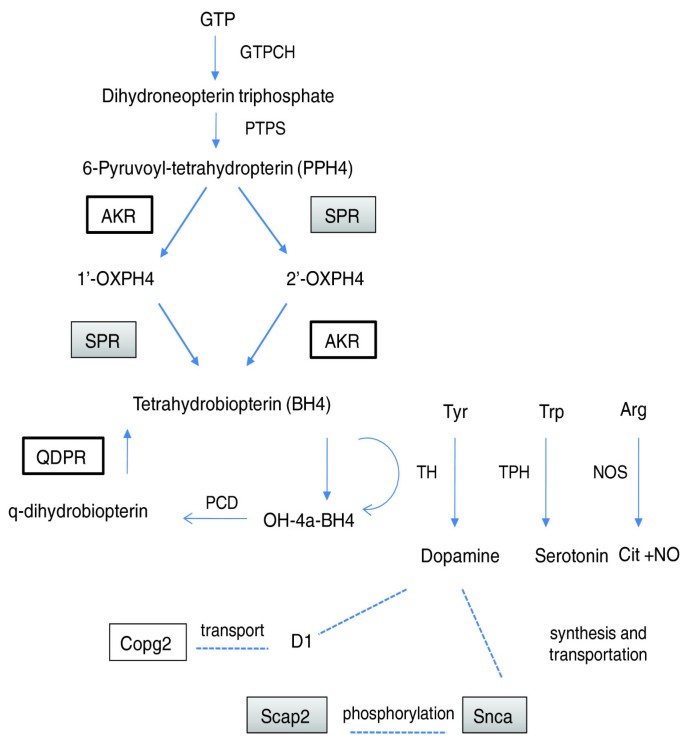
该图展示了候选基因在多巴胺和血清素合成通路中的作用,揭示了这些基因通过调控神经递质系统影响酒精偏好的潜在机制,为后续功能研究提供了方向。
