1. 领域背景与文献引入
文献英文标题:Revealing the full biosphere structure and versatile metabolic functions in the deepest ocean sediment of the Challenger Deep;发表期刊:Genome Biology;影响因子:17.906(2021年);研究领域:深海极端环境微生物学、生物地球化学循环。
深渊带(水深6000米以下)是地球表面最极端的生境之一,具有60-110MPa的高静水压力、近冰点温度、完全黑暗、低营养供给及地形隔离等特征,1950年代起研究人员开始采用培养法探索深渊微生物,2000年后16S rRNA基因测序技术的应用大幅扩展了对深渊微生物群落组成的认知,发现变形菌门、绿弯菌门、放线菌门等是深渊环境的优势类群,微生物丰度与沉积有机质的输入密切相关。但现有研究仍存在诸多局限:基于16S rRNA基因的分析仅能揭示群落分类组成,无法解析微生物的代谢功能;传统培养法仅能分离少数可培养类群,难以反映群落的真实多样性;此前针对挑战者深渊沉积物的研究缺乏深度宏基因组学的系统分析,对真核微生物、病毒组分的结构与功能了解几乎空白,也未明确深渊微生物参与生物地球化学循环的具体机制。针对这些研究空白,本研究采用深度宏基因组学结合大规模微生物培养的策略,系统解析挑战者深渊沉积物的完整生物圈结构与代谢功能,为极端环境微生物的适应性机制及深海生物地球化学循环研究提供新的视角。
2. 文献综述解析
作者对领域内现有研究的分类维度主要包括技术方法(传统培养法、16S rRNA基因测序法、宏基因组学)和研究对象(原核微生物、真核微生物、病毒)两个层面。现有研究的关键结论显示,深渊环境并非生命禁区,反而存在丰富的微生物群落,其组成与环境因子(如有机质输入、静水压力)密切相关;技术方法方面,16S rRNA基因测序法能快速、低成本地分析微生物群落的分类组成,传统培养法可获得纯培养物用于后续功能验证,但两种方法均存在明显局限性:16S rRNA基因测序无法获取微生物的功能信息,传统培养法仅能分离约0.1%-1%的环境微生物,且此前的宏基因组研究存在样本覆盖度低、数据量不足的问题,难以捕捉低丰度微生物及真核、病毒组分。
通过对比现有研究的未解决问题,本研究的创新价值凸显:首次采用深度宏基因组学方法解析挑战者深渊沉积物的完整生物圈结构,构建了178个宏基因组组装基因组(MAGs),其中16个门为首次在深渊沉积物中报道;首次系统分析了深渊真核真菌的代谢功能,发现其参与硝酸盐、硫酸盐还原及硫化氢氧化的新机制;首次揭示了深渊病毒的新进化分支及调控宿主氮、硫代谢的辅助代谢基因;结合大规模培养技术获得了1070株细菌和19株真菌分离株,其中19株为潜在新种,填补了深渊可培养微生物资源的空白。
3. 研究思路总结与详细解析
本研究的整体目标是解析挑战者深渊沉积物微生物组的分类结构、代谢功能及环境适应性,核心科学问题聚焦于深渊微生物如何通过独特的代谢机制适应极端环境,并参与深海碳、氮、硫等元素的生物地球化学循环,技术路线遵循“样本采集-多组学分析-功能解析-培养验证”的闭环逻辑,通过深度宏基因组学与大规模培养技术的结合,实现对深渊生物圈的全面解析。
3.1 样本采集与地球化学特征分析
本环节的核心目标是获取挑战者深渊的沉积物样本并明确其环境背景特征。研究人员使用深渊着陆器从马里亚纳海沟挑战者深渊(142°21.7806′E,11°25.8493′N,水深10840米)采集沉积物岩芯,将其分为0-5cm(表层)、5-10cm(中层)、10-14cm(深层)三个深度段,分别测定总有机碳(TOC)、总氮(TN)、碳氮同位素组成及孔隙水营养离子浓度。结果显示,沉积物TOC含量为0.49-0.55wt%,TN含量为0.05-0.06wt%,δ13C值为-21.41至-21.53‰,δ15N值为5.42至6.69‰,符合挑战者深渊沉积物的有机质特征;孔隙水中NH4+、PO43-、NO2-浓度随沉积物深度增加而升高,NO3-浓度则随深度降低,表明沉积物存在明显的氧化还原梯度。文献未提及具体实验产品,领域常规使用元素分析仪、同位素质谱仪、离子色谱仪等设备完成相关测定。
3.2 深度宏基因组测序与组装
本环节旨在获得高覆盖度的宏基因组数据以捕捉低丰度微生物。研究人员从每个深度段的沉积物样本中提取总DNA,构建多个独立的Illumina测序文库,每个文库平均获得22.6Gb序列数据,总计获得248.65Gb原始测序数据;经过质量控制后,使用MEGAHIT软件对所有样本的清洁数据进行共组装,最终得到总长度为6.65Gb的宏基因组,包含约621万个contigs,N50长度约为1.14kb。实验所用关键产品:MoBio PowerSoil DNA Isolation Kit、Covaris S2 DNA破碎仪、NEXTflex™ DNA Sequencing Kit、Illumina Hiseq Xten测序平台。
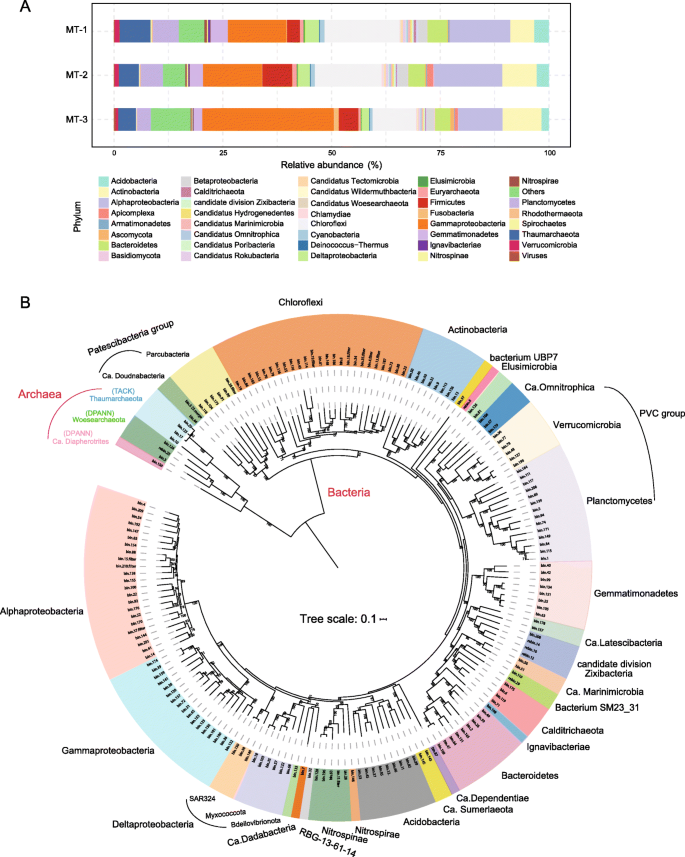
3.3 宏基因组组装基因组(MAGs)构建与系统发育分析
本环节的核心目标是从宏基因组中重构微生物的基因组信息并解析其系统发育多样性。研究人员采用CONCOCT、Metabat、DAS Tool、metaWRAP等多种分箱工具对组装得到的contigs进行分箱,并用CheckM软件评估分箱得到的基因组质量,筛选出完整性>50%、污染度<10%的高质量MAGs。最终获得178个MAGs,代表26个原核生物门,其中16个门为首次在深渊沉积物中报道,包括芽单胞菌门(Gemmatimonadetes)、疣微菌门(Verrucomicrobia)等;基于43个保守单拷贝蛋白编码基因构建的系统发育树显示,这些MAGs涵盖了深渊环境中已知的主要原核类群,还包含多个未培养的新型进化分支,如属于DPANN超门的Candidatus Diapherotrites古菌,其基因组与细菌存在较近的系统发育关系,推测可能通过水平基因转移获得了细菌的代谢基因。实验所用关键产品:CheckM、GTDB-Tk、RAxML等生物信息学分析工具。

3.4 微生物代谢功能解析
本环节旨在解析深渊微生物的代谢潜力与适应性机制。研究人员通过KEGG、CAZy等数据库对178个MAGs的基因进行功能注释,结果显示39%的MAGs(n=178)为混合营养型,同时具备异养代谢与无机碳固定能力,涉及6种不同的自养途径,其中3-羟基丙酸循环是最普遍的自养途径,存在于43个MAGs中;87%的MAGs(n=178)含有有氧呼吸相关基因,81%的MAGs(n=178)含有厌氧呼吸相关基因,76%的MAGs(n=178)为兼性厌氧型,表明深渊微生物具有极强的代谢灵活性,可适应沉积物中的氧化还原波动;此外,还发现大量参与化能自养的基因,如硝化、CO氧化、硫化物氧化相关基因,说明深渊微生物可通过氧化无机化合物获取能量。实验所用关键产品:KAAS、dbcan等功能注释工具。
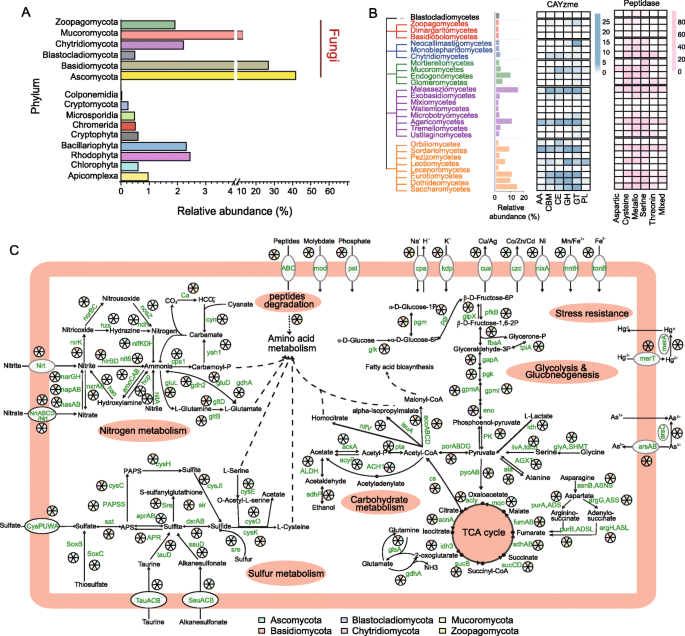
3.5 真核微生物群落与代谢功能分析
本环节的核心目标是解析深渊真核微生物的组成与代谢功能。通过Kaiju软件对宏基因组序列进行分类注释,发现真核微生物占总序列的0.69%,其中真菌占真核序列的87.42%,主要类群为子囊菌门(41.73%)、担子菌门(26.82%)、毛霉门(12.64%);进一步的代谢功能注释显示,这些真菌首次被发现具备同化/异化硝酸盐还原、硫酸盐还原及硫化氢氧化的代谢途径,可参与深渊沉积物的氮、硫循环,其基因组中还含有大量碳水化合物活性酶(CAZymes)和肽酶基因,表明真菌可降解复杂的有机质,在深渊碳循环中发挥重要作用。实验所用关键产品:Kaiju、KEGG等分析工具。
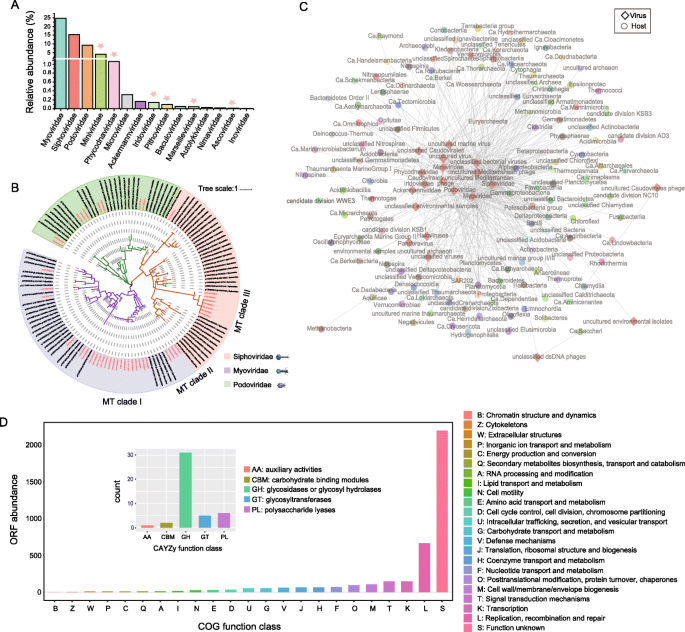
3.6 病毒组结构与功能分析
本环节旨在解析深渊病毒的群落组成与生态功能。通过Kaiju软件分析宏基因组中的病毒序列,发现病毒占总序列的0.12%,主要为双链DNA病毒,其中有尾噬菌体目(Caudovirales)占主导,包括肌病毒科(24.62%)、长尾病毒科(19.70%)、短尾病毒科(9.40%),还首次在深渊沉积物中发现了较高丰度的巨型病毒(如拟菌病毒科,占4.16%);系统发育分析显示,有尾噬菌体目存在独特的深渊进化分支,病毒-宿主互作分析表明长尾病毒科与最多的宿主类群相关联;功能注释发现40个病毒编码的辅助代谢基因(AMGs),参与碳、氮、硫代谢,如编码亚硝酸盐还原酶的nirK基因、编码ATP硫酸化酶的CysN/NodQ基因,表明病毒可通过调控宿主的代谢过程影响深海生物地球化学循环。实验所用关键产品:Kaiju、eggNOG-mapper等分析工具。
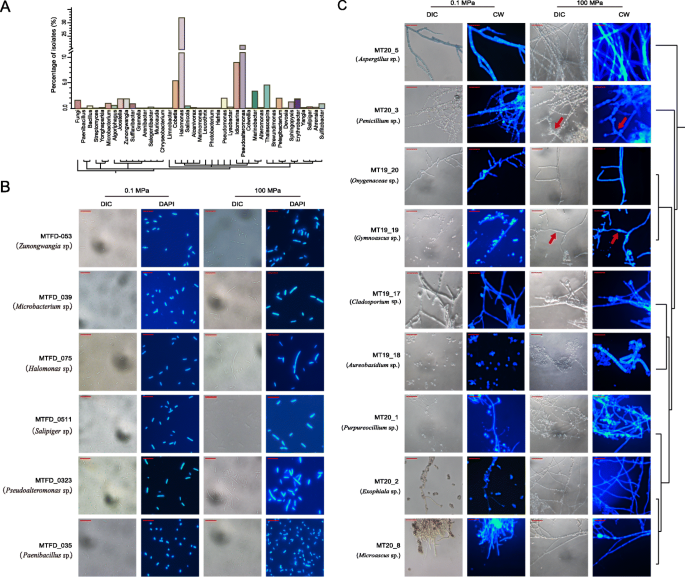
3.7 大规模微生物培养与分离株表征
本环节的核心目标是获取深渊微生物的纯培养物并表征其适应性特征。研究人员采用24种不同的培养基,结合不同的培养条件(温度、氧浓度、抗生素添加等)对沉积物样本进行大规模培养,通过16S rRNA基因或ITS序列测序对分离株进行分类鉴定,最终获得1070株细菌和19株真菌分离株,其中19株细菌的16S rRNA基因序列与已知物种的同源性≤97%,为潜在新种;对分离株进行100MPa高压培养实验,发现部分细菌和真菌在高压下出现形态变化,如细菌细胞分裂后仍保持连接、真菌菌丝肿胀等,表明这些分离株具有耐压特性,可适应深渊的高静水压力环境。实验所用关键产品:多种定制化培养基、高压培养装置、Nikon Eclipse 80i荧光显微镜。
4. Biomarker研究及发现成果
本研究中的Biomarker主要包括微生物的分类群、代谢基因及功能模块,其筛选与验证逻辑为:基于深度宏基因组数据筛选在深渊沉积物中特异性存在或高丰度的微生物类群与代谢基因,结合培养验证及功能注释明确其生物学意义。
研究过程中,从挑战者深渊沉积物宏基因组中筛选出多个特征性Biomarker:在分类群层面,混合营养型原核微生物(占MAGs的39%,n=178)、兼性厌氧型微生物(占MAGs的76%,n=178)、具备硝酸盐/硫酸盐还原功能的真菌是深渊沉积物的特征性类群;在代谢基因层面,参与3-羟基丙酸循环的基因、病毒编码的辅助代谢基因(如nirK、CysN/NodQ)是深渊环境的特异性功能Biomarker。这些Biomarker的来源为挑战者深渊10840米深度的沉积物样本,通过宏基因组注释、培养验证等方法进行验证,其中混合营养型微生物的比例、兼性厌氧型微生物的比例等数据均具有统计学意义(基于178个MAGs的分析)。
核心成果方面,这些Biomarker揭示了深渊微生物独特的适应性机制:混合营养型与兼性厌氧型微生物的高比例表明,深渊微生物可通过灵活切换代谢模式适应低营养、氧化还原波动的极端环境;真菌参与硝酸盐、硫酸盐还原的代谢途径为首次发现,表明真菌在深渊氮、硫循环中发挥重要作用;病毒编码的辅助代谢基因则揭示了病毒在深海生物地球化学循环中的调控作用。这些发现不仅为极端环境微生物的适应性机制研究提供了新的Biomarker,也为深海生物地球化学循环的模型构建补充了新的功能模块。
