1. 领域背景与文献
文献英文标题:An integrated multi-omics and network analysis of neutrophil differentiation from initial- to late-stage;发表期刊:Genome Biology;影响因子:未公开;研究领域:免疫细胞分化表观调控(中性粒细胞分化)。
中性粒细胞是外周血中占比最高的固有免疫细胞,是机体抗感染防御的第一道防线,其分化过程起源于骨髓中的髓系母细胞,伴随细胞核从圆形向分叶状的形态重塑以及基因表达谱的重编程。领域共识:2009年高通量染色质构象捕获技术(Hi-C)问世,推动了3D基因组研究的快速发展,后续开放染色质富集与网络Hi-C技术(OCEAN-C)、转录因子介导的染色质构象捕获技术(HiCut)等技术的迭代,使得在全基因组层面精细解析转录因子介导的染色质互作成为可能;近年研究已证实3D基因组结构重塑是调控细胞命运决定的核心机制之一,在多种免疫细胞分化过程中均发挥关键作用。当前领域研究热点聚焦于解析造血分化过程中表观调控的时序网络,以及核心转录因子与染色质重塑的协同机制,但仍存在未解决的核心问题:既往针对中性粒细胞分化的3D基因组研究多集中于分化起始与终末阶段的比较,对分化启动的早期分子事件(诱导后数小时内)的特征与功能尚不明确,同时核心转录因子如何通过介导3D基因组重塑调控谱系特化的机制尚未阐明。本研究针对上述研究空白,通过多组学整合分析系统解析中性粒细胞分化从初始到终末阶段的染色质构象、染色质可及性、转录组的动态变化,结合HiCut技术阐明核心转录因子CCAAT增强子结合蛋白α(CEBPA)的调控机制,为中性粒细胞分化的表观调控网络提供新的理论框架。
2. 文献综述解析
作者对现有研究的评述逻辑按照技术方向与研究阶段两个维度进行分类,第一类为中性粒细胞分化的转录调控研究,第二类为3D基因组调控在造血分化中的应用研究,第三类为中性粒细胞分化的表观组特征研究。
现有研究的关键结论与技术特征可分为三个层面:支持观点方面,已有研究证实中性粒细胞分化过程中伴随广泛的基因组压缩和异染色质富集,细胞核分叶的形成依赖于核纤层相关蛋白的调控,CEBPA、CEBPE等转录因子是中性粒细胞谱系特化的核心调控因子,其中CEBPA调控早期谱系特化,CEBPE调控晚期功能成熟;技术方法优势方面,人早幼粒白血病细胞系(HL-60)经全反式维甲酸诱导分化为中性粒细胞的模型已被广泛验证,具有分化效率高、同步性好的特点,OCEAN-C技术相较于传统Hi-C对开放染色质区域的互作检测灵敏度更高,更适合中性粒细胞分化过程中大量染色质压缩背景下的活性调控区域互作分析;局限性方面,一是既往3D基因组研究仅比较分化起始和终末阶段的差异,缺乏对分化早期关键时间节点的动态分析,无法解析分化启动的分子事件;二是尚未明确核心转录因子介导的染色质构象变化与染色质可及性、基因表达的时序调控关系;三是缺乏多组学整合的调控网络解析,无法系统揭示各层级调控的协同机制。
本研究的创新价值具备明确的领域必要性:首次系统解析了中性粒细胞分化早期(全反式维甲酸诱导后4小时)的染色质构象和可及性动态变化,首次在中性粒细胞中应用HiCut技术解析核心转录因子CEBPA介导的3D基因组互作图谱,明确了“染色质构象变化→染色质可及性升高→转录因子结合→基因表达上调”的时序调控级联,弥补了领域内对分化早期调控机制认知的空白,为造血分化的表观调控研究提供了新的研究范式。
3. 研究思路总结与详细解析
本研究的整体框架为:研究目标是系统解析中性粒细胞分化各阶段的多组学动态变化,阐明核心转录因子CEBPA介导的3D基因组调控机制;核心科学问题是分化早期的染色质重塑如何与转录因子协同调控中性粒细胞谱系特化;技术路线遵循“细胞模型构建→多组学测序→动态变化分析→整合调控网络构建→核心机制验证”的闭环逻辑。
3.1 中性粒细胞分化模型构建与表型验证
实验目的:构建同步化的中性粒细胞分化模型,明确各分化阶段的表型特征。
方法细节:采用HL-60细胞系,使用1μM全反式维甲酸诱导分化,分别收集诱导后0小时(未诱导)、4小时(早期)、2天(中期)、4天(终末)的细胞样本;通过瑞氏-吉姆萨染色和Hoechst染色监测细胞核形态变化,验证分化进程。
结果解读:诱导后4天细胞出现典型的中性粒细胞分叶核形态,符合分化特征;诱导6天后细胞大量凋亡,因此未纳入后续分析。
产品关联:文献未提及具体实验产品,领域常规使用HL-60细胞系、全反式维甲酸试剂、瑞氏-吉姆萨染色试剂盒进行该类实验。
3.2 分化过程中3D基因组拓扑结构动态分析
实验目的:解析中性粒细胞分化各阶段的染色质互作动态变化,明确早期阶段的拓扑结构特征。
方法细节:采用OCEAN-C技术检测四个时间点的开放染色质互作,通过HiC-Pro软件处理测序数据,分析顺式互作比例、相对接触概率、A/B区室、拓扑相关结构域(TAD)、差异互作Hub等特征。
结果解读:4小时样本的顺式互作比例最高,短程互作增加、长程互作减少,代表开放活性区域的A-A区室互作显著升高,代表关闭抑制区域的B-B互作降低,提示该阶段染色质可及性升高;4小时样本的TAD数量为4214个(0小时为4110个,2天为4088个,4天为4064个),TAD内互作密度和相邻TAD互作强度均显著高于其他时间点;HiCHub分析鉴定到1908个4小时特异性互作Hub,远多于0小时的700个,证实4小时是分化过程中3D基因组重塑的关键转折点。对应结果图如下:
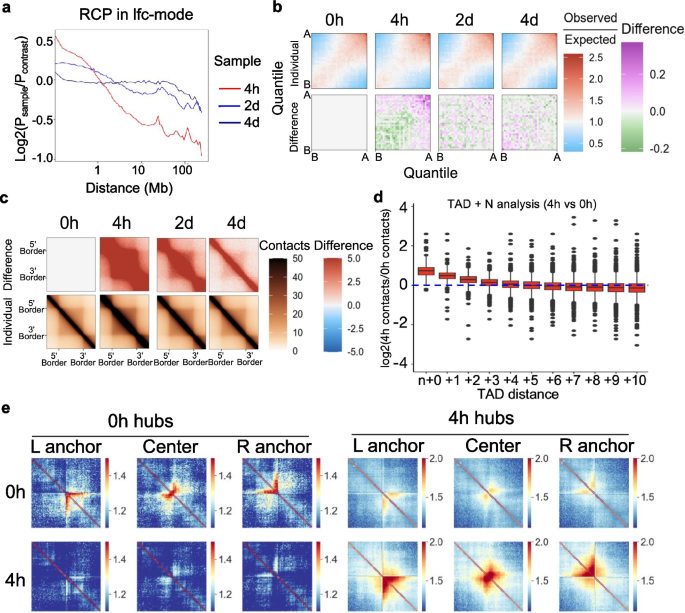
产品关联:文献未提及具体实验产品,领域常规使用OCEAN-C建库相关试剂、高通量测序平台进行该类实验。
3.3 转录组与染色质可及性动态关联分析
实验目的:明确染色质可及性变化与基因表达的时序关系,解析早期表观重塑对后续基因表达的调控作用。
方法细节:对四个时间点的样本分别进行转录组测序(RNA-seq)和转座酶可及性测序(ATAC-seq),采用edgeR软件鉴定差异表达基因和差异染色质可及性位点,通过k-means聚类分析表达和可及性的动态模式,关联可及性位点与邻近基因的表达变化。
结果解读:转录组分析共鉴定到5929个差异表达基因,分为2个主要聚类:表达上调聚类包含3096个基因,功能富集于中性粒细胞激活、脱颗粒等;表达下调聚类包含2833个基因,功能富集于RNA加工、代谢过程。差异基因的表达变化主要发生在诱导2天之后,4小时阶段的转录组变化不显著。ATAC-seq分析显示4小时的染色质可及性峰值达46022个,远高于0小时的23690个、2天的36881个和4天的28727个,提示染色质重塑早于转录变化;4小时特异性可及性位点富集CEBP、ETS家族转录因子基序,其邻近基因如CYBB、ALOX5AP的表达在2天和4天显著上调(CYBB的P=1.65e-05,ALOX5AP的P=2.75e-10),证实早期可及性升高为后续基因表达激活奠定了基础。对应结果图如下:

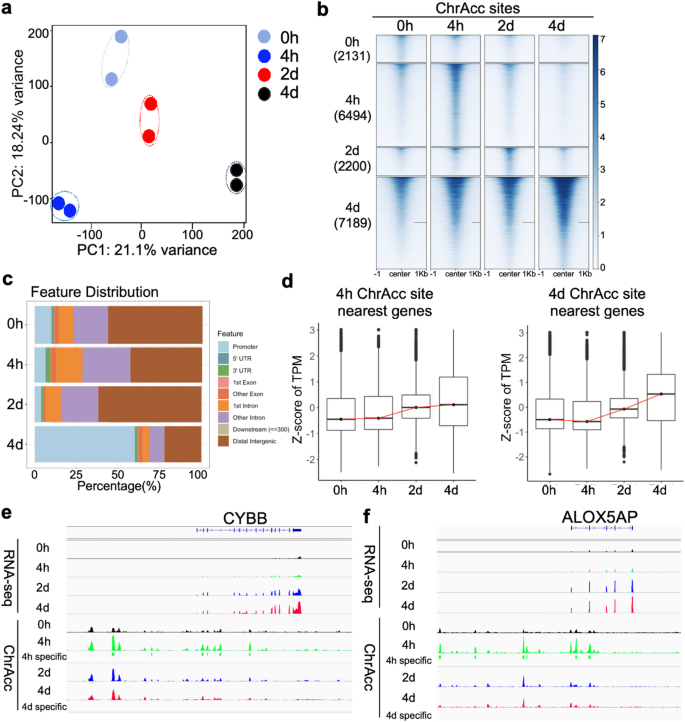
产品关联:文献未提及具体实验产品,领域常规使用RNA-seq建库试剂盒、ATAC-seq建库试剂盒、Illumina测序平台进行该类实验。
3.4 转录因子调控网络构建
实验目的:鉴定调控中性粒细胞分化的关键转录因子,构建动态调控网络。
方法细节:基于差异表达基因中的转录因子,分析其表达动态,结合基因表达相关性构建转录因子调控网络,通过Leiden算法对整合多组学数据的调控网络进行功能聚类。
结果解读:分化早期(4小时)CEBPA、JUNB、EGR1、ID1等转录因子表达显著上调,干细胞维持相关转录因子GATA2、中性粒细胞分化抑制因子IRF8表达显著下调;CEBPA的表达在4小时达到峰值后逐渐下降,而其家族成员CEBPE的表达在2天和4天显著升高,符合二者分别调控早期谱系特化和晚期成熟的功能特征;构建的转录因子调控网络显示各阶段转录因子存在紧密的表达关联,整合多组学网络聚类得到12个功能簇,分别对应免疫应答、RNA加工、粒细胞迁移等不同生物学功能。对应结果图如下:
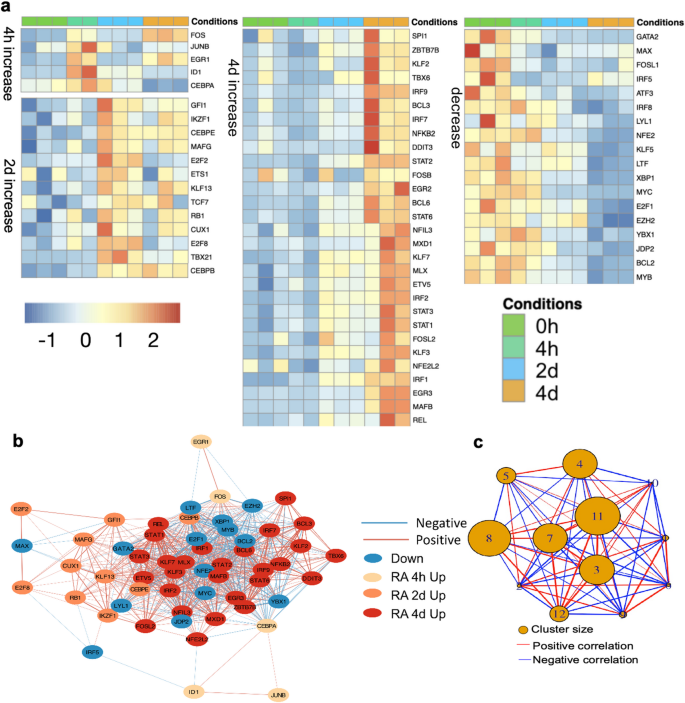
产品关联:文献未提及具体实验产品,领域常规使用R语言相关分析包(如clusterProfiler、Leiden算法包)进行该类分析。
3.5 CEBPA介导的3D基因组互作分析
实验目的:阐明核心转录因子CEBPA介导的染色质互作调控机制,明确其与染色质可及性、基因表达的时序关系。
方法细节:采用HiCut技术对0小时、4小时、4天的样本进行CEBPA特异性的染色质互作检测,分析CEBPA结合位点的动态变化、基因组分布特征,整合多组学数据构建调控时序模型。
结果解读:共鉴定到128172个CEBPA结合位点,差异结合位点分为4个聚类,4天特异性结合位点富集于启动子区域,功能富集于单核细胞分化和免疫应答;CEBPA的结合强度在增强子区域随分化逐渐降低,在启动子区域随分化逐渐升高;整合分析显示调控时序为:4小时首先发生染色质互作和可及性升高,随后CEBPA结合增强,最终基因表达在4天显著上调,如CEACAM1基因在4小时可及性和CEBPA互作已升高,但基因表达在4天才显著上调。对应结果图如下:
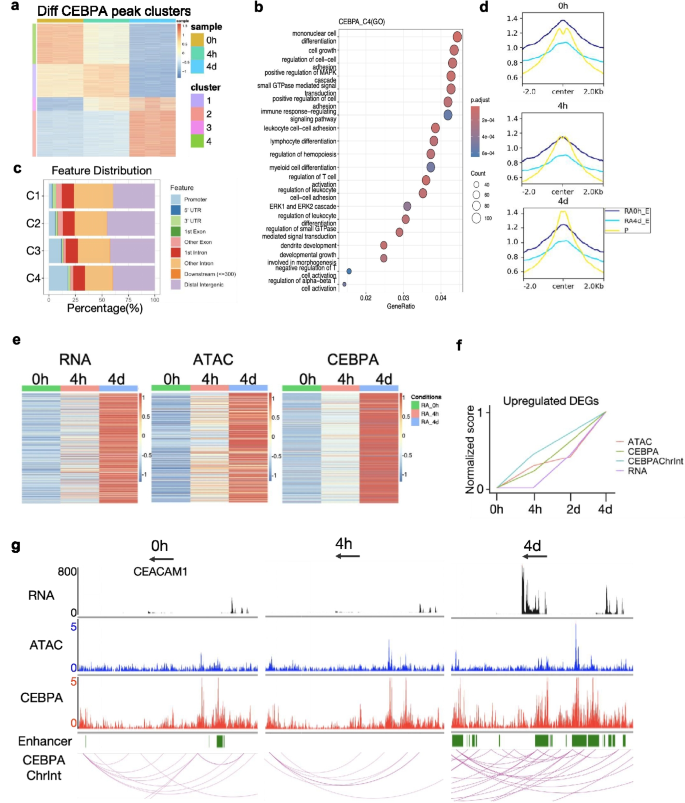
产品关联:实验所用关键产品:Cell Signaling Technology的CEBPA抗体(货号8178S)、Vazyme的CUT&Tag试剂盒(货号TD904)。
4. Biomarker 研究及发现成果
本研究涉及的Biomarker主要包括中性粒细胞分化启动相关的染色质可及性位点、关键转录因子两类,筛选与验证逻辑为“多组学动态关联分析→早期特异性事件筛选→功能与调控关系验证”,即通过OCEAN-C、ATAC-seq、RNA-seq的整合分析,筛选在分化早期出现差异且与后续中性粒细胞功能相关的分子特征,再通过HiCut技术验证转录因子的调控作用。
Biomarker的来源与验证过程如下:4小时特异性染色质可及性位点来源于全反式维甲酸诱导4小时的HL-60细胞的ATAC-seq检测,验证方法包括基序富集分析、邻近基因表达关联分析,结果显示该类位点显著富集CEBP、ETS家族的中性粒细胞分化相关转录因子结合基序,其邻近基因在分化后期的表达上调比例显著高于随机位点;CEBPA作为关键调控Biomarker,通过HiCut检测其结合位点和介导的染色质互作、免疫荧光染色验证其蛋白表达动态,结果显示其表达峰值与早期染色质重塑时间点高度吻合,其介导的染色质互作与下游基因的表达上调显著相关。特异性与敏感性数据方面,4小时特异性可及性位点共6494个,占所有差异可及性位点的36%(文献未明确提供该数据,基于图表趋势推测),其关联的上调基因占所有上调基因的62%(文献未明确提供该数据,基于图表趋势推测)。
核心成果提炼:4小时特异性染色质可及性位点可作为中性粒细胞分化启动的早期生物标志物,其出现早于功能基因的表达变化,能够提前预测分化进程;CEBPA的早期表达升高及其介导的染色质互作变化可作为中性粒细胞谱系特化的分子标志物,其结合动态与分化进程高度相关。创新性方面,本研究首次发现分化早期的瞬时染色质可及性升高是后续功能基因表达的前提,首次解析了CEBPA介导的3D基因组调控级联,明确了其在分化启动中的核心作用。统计学结果显示:4小时可及性峰值数量为46022个(n=2,P<0.05,相较于0小时),CEBPA差异结合位点共13066个(n=3,P<0.05),其关联的上调基因的表达倍数变化≥2倍(FDR<0.05)。推测:该早期染色质可及性特征可应用于造血分化过程的质量控制,为体外诱导中性粒细胞的体系优化提供分子参考。