1. 领域背景与文献引入
文献英文标题:Evolutionary rates and centrality in the yeast gene regulatory network;发表期刊:Genome Biology;影响因子:未公开;研究领域:酵母基因调控网络与分子进化
组学革命推动生命科学进入系统生物学时代,网络生物学作为核心分支,将细胞视为由基因、蛋白、代谢物构成的复杂网络系统,为理解细胞功能与进化提供了全局视角。此前研究已明确,在酵母蛋白-蛋白互作(PPI)网络和代谢网络中,处于中心位置的节点蛋白进化速率显著慢于外周节点,推测其原因是中心节点参与更多关键功能,突变易导致细胞存活受损,因此受到强纯化选择。然而,转录调控网络作为细胞信息传递的核心枢纽,其节点位置与进化速率的关联尚未得到系统解析,不同类型细胞网络的功能差异对节点进化的调控机制也未明确。针对这一研究空白,本文通过分析两个独立的酵母转录调控网络数据集,旨在揭示网络中心性与转录因子进化速率的关联,为理解不同细胞网络的进化规律提供新的学术依据。
2. 文献综述解析
作者按细胞网络类型(PPI网络、代谢网络、转录调控网络)对现有研究进行分类评述,系统梳理了不同网络中节点位置与进化速率的关联规律。现有研究结论显示,PPI网络和代谢网络中,中心节点蛋白的进化速率显著慢于外周节点,这一规律被广泛归因于中心节点的功能重要性,强纯化选择限制了其序列变异;技术方法上,现有研究多采用大规模组学数据与网络分析结合的策略,具备较高的统计效力,但也存在局限性:一是对转录调控网络的分析较为匮乏,缺乏与其他两类网络的对比研究;二是部分研究未校正表达水平、基因必需性等混杂因素,结论的独立性有待验证;三是未明确网络功能差异对节点进化的调控作用。本文的创新价值在于,首次针对酵母转录调控网络开展系统分析,发现中心转录因子进化速率更快的反直觉规律,且通过多变量校正证明该关联独立于表达水平、基因必需性等已知影响进化速率的因素,填补了不同细胞网络进化规律对比研究的空白,为网络结构与分子进化的关联研究提供了新的范式。
3. 研究思路总结与详细解析
本文的研究目标是明确酵母转录调控网络中节点中心性与转录因子进化速率的关联及调控机制,核心科学问题是转录调控网络的结构特征是否独立于其他基因组变量影响转录因子的进化,技术路线遵循“多数据集验证→单变量关联→多变量校正→机制探讨”的闭环逻辑,确保结论的可靠性与严谨性。
3.1 转录调控网络数据集与进化速率计算
实验目的是获取可靠的酵母转录调控网络数据及转录因子的进化速率指标,为后续关联分析奠定基础。方法细节上,采用两个独立的酵母转录调控网络数据集YTN1和YTN2,其中YTN1包含286个转录因子、3369个靶基因及8372个调控互作,YTN2包含157个转录因子、4410个靶基因及12873个调控互作;从酵母基因组数据库(SGD)获取酿酒酵母与近缘种的直系同源蛋白序列,经序列比对后,使用CODEML软件计算非同义替换率(dN)、同义替换率(dS)及dN/dS比值作为进化速率指标;仅保留明确为直系同源的转录因子进行后续分析,最终YTN1纳入256个转录因子,YTN2纳入138个。结果解读显示,成功获得两个数据集的转录因子进化速率,两个数据集的样本量差异较大但结果趋势一致,为后续分析提供了重复验证的基础。产品关联:文献未提及具体实验产品,领域常规使用序列比对软件(如BioEdit)、进化分析软件(如PAML)、网络分析平台(如tYNA)等。
3.2 单变量关联分析:进化速率与基因组及网络变量的关联
实验目的是初步探索表达水平、基因必需性、功能多效性(GO术语数量)、网络中心性等变量与转录因子进化速率的关联。方法细节上,分别采用Spearman非参数相关性分析,检测各变量与dN/dS的关联;基因必需性定义为敲除后致死的表型,功能多效性用GO术语数量衡量,网络中心性包括介数、入度(k_in)、出度(k_out)。结果解读显示,表达水平与进化速率呈负相关,高表达转录因子进化更慢(n=256,P<0.001);必需转录因子的进化速率显著慢于非必需转录因子(n=256,P<0.001);GO术语数量越多,进化速率越慢(n=256,P<0.01);与PPI和代谢网络相反,转录调控网络中,介数与进化速率呈正相关,中心转录因子进化更快(n=256,P<0.001),入度也与进化速率正相关,而出度的关联在两个数据集中存在差异。
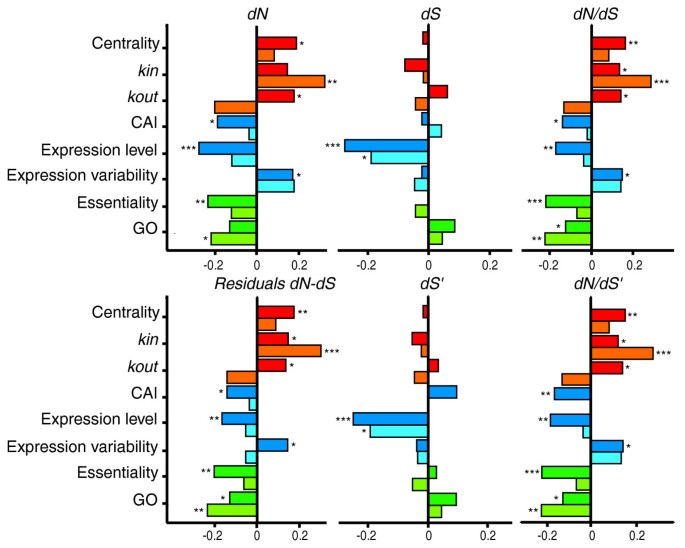
该图展示了各变量与进化速率的相关性,其中红色代表网络拓扑变量,深色为YTN1结果,浅色为YTN2结果,直观呈现了中心性与进化速率的正关联。产品关联:文献未提及具体实验产品,领域常规使用统计分析软件(如JMP)进行相关性分析。
3.3 多变量回归与主成分分析:校正混杂因素的独立关联验证
实验目的是排除表达水平、基因必需性等混杂因素的影响,明确网络中心性与进化速率的独立关联。方法细节上,采用多元线性回归分析,将dN/dS作为因变量,纳入表达水平、必需性、GO术语数量、网络中心性等变量作为自变量;同时采用主成分回归分析,将表达、功能、网络相关变量分别提取主成分,再进行回归分析,以避免变量间的共线性问题。结果解读显示,多元回归分析显示,网络介数与进化速率的正关联独立于其他变量(P<0.05),基因必需性、GO术语数量仍与进化速率负相关,仅表达水平对同义替换率(dS)有显著影响;主成分分析进一步验证,网络相关主成分与进化速率正相关,而表达和功能相关主成分与进化速率负相关,两个数据集的结果趋势一致,证明中心性对进化速率的影响是独立的。产品关联:文献未提及具体实验产品,领域常规使用统计分析软件(如JMP、R)进行回归分析。
3.4 表达变异性与中心性的关联分析
实验目的是探讨中心转录因子进化更快的潜在机制,分析表达变异性的作用。方法细节上,采用Spearman相关性分析,检测网络中心性与转录因子表达变异性的关联,表达变异性用不同条件下的变异系数衡量。结果解读显示,中心转录因子的表达变异性显著更高(n=256,P<0.01),但表达变异性与进化速率无显著关联,提示中心性对进化速率的影响并非通过表达变异性直接介导,可能与环境适应或缓冲效应相关。产品关联:文献未提及具体实验产品,领域常规使用基因表达数据库(如GEO)获取表达数据并进行统计分析。
4. Biomarker研究及发现成果
本文的核心Biomarker为酵母转录调控网络中的节点中心性特征(介数、入度),其作为反映转录因子在网络中位置的关键指标,与进化速率存在独立的正关联,为理解转录调控网络的进化规律提供了核心特征。
Biomarker定位属于“网络结构特征类Biomarker”,筛选与验证逻辑为“基于两个独立转录调控网络数据集计算中心性指标→单变量关联分析初步发现与进化速率的正相关→多变量校正排除混杂因素→重复数据集验证结论可靠性”。研究过程详述显示,Biomarker数据来源于两个独立的酵母转录调控网络数据集,验证方法包括Spearman相关性分析、多元线性回归、主成分回归;特异性方面,该关联仅存在于转录调控网络,与PPI和代谢网络的结论相反,敏感性方面,在样本量更大的YTN1数据集中,介数与进化速率的相关系数为正(P<0.001,n=256),且多变量校正后仍显著(P<0.05)。
核心成果提炼显示,首次发现酵母转录调控网络中中心转录因子进化速率更快,该关联独立于表达水平、基因必需性、功能多效性等已知影响因素;该成果的创新性在于揭示了不同细胞网络功能对节点进化的调控差异,提示转录调控网络的中心节点可能通过适应环境变化或缓冲效应实现更快进化;统计结果显示,YTN1数据集中介数与dN/dS的Spearman相关系数为正(P<0.001,n=256),多元回归分析中,介数的回归系数显著为正(P<0.05)。
