1. 领域背景与文献引入
文献英文标题:Raptor genomes reveal evolutionary signatures of predatory and nocturnal lifestyles;发表期刊:Genome Biology;影响因子:10.806(2019年);研究领域:鸟类进化基因组学、捕食适应性进化、夜行性演化机制
猛禽作为陆地生态系统中的顶级捕食者,涵盖鸮形目(夜行)、隼形目和鹰形目(昼行)三个非单系类群,其独特的生态位和生活习性使其成为适应性进化研究的理想模型。此前已有部分猛禽物种(如游隼、金雕)的基因组被测序,揭示了与飞行、捕食相关的部分形态和生理适应性特征,但研究多集中在单个类群,缺乏对三个猛禽目的全基因组比较分析,无法揭示共同的捕食适应性分子基础;对于夜行性鸟类的研究,已发现部分物种丢失了色觉基因,但缺乏对多个夜行性鸟类类群的系统比较,感官系统的功能权衡机制(如色觉丢失与夜视增强的协同演化)尚未明确,同时现有研究多依赖基因组序列分析,缺乏转录组层面的表达验证,无法明确基因表达变化在夜行性适应中的作用。在此背景下,本研究通过构建4种高质量猛禽参考基因组,结合16种猛禽的基因组和转录组数据,系统解析了猛禽捕食生活方式的共同分子特征,以及夜行性鸟类的适应性演化机制,为鸟类适应性进化研究提供了新的全基因组视角。
2. 文献综述解析
作者以猛禽的分类类群(三个目)和生活习性(昼行/夜行)为核心分类维度,系统梳理了猛禽和非猛禽的基因组研究现状,明确了现有研究的成果与不足,进而凸显本研究的创新价值。
现有研究已证实猛禽作为顶级捕食者在形态(如利爪、敏锐视觉)和生理(如高效呼吸系统)层面存在适应性特征,部分已测序的猛禽基因组鉴定出与飞行、捕食相关的正选择基因,但这些研究多聚焦于单个猛禽目,缺乏跨目比较,无法揭示三个猛禽目共同的捕食适应性分子基础;对于夜行性鸟类的研究,已发现部分物种丢失了色觉基因,但缺乏对多个夜行性鸟类类群的比较,感官系统的功能权衡机制尚未得到系统解析,同时现有研究多依赖基因组序列分析,缺乏转录组层面的表达验证,无法明确基因表达变化在夜行性适应中的作用。本研究通过整合20种鸟类的基因组和转录组数据,首次实现了三个猛禽目的全基因组比较,同时结合昼行性与夜行性鸟类的多组学分析,填补了猛禽适应性进化研究的空白,为理解捕食生活方式和夜行性的分子演化机制提供了全面的证据。
3. 研究思路总结与详细解析
本研究的核心目标是解析猛禽捕食生活方式和夜行性的分子演化机制,围绕“构建高质量参考基因组→比较基因组分析捕食适应性→比较分析夜行性演化特征→转录组验证基因表达变化”的闭环逻辑链条展开,通过多组学技术系统揭示了猛禽的适应性分子特征。
3.1 猛禽基因组测序与组装
本环节的核心目标是构建高质量的猛禽参考基因组,为后续比较基因组分析提供可靠的基础数据。研究人员采集了20种鸟类(其中16种为猛禽)的血液样本,针对欧亚雕鸮、东方角鸮、普通鵟、红隼4种猛禽,采用Illumina HiSeq平台进行高覆盖度(>185×)全基因组鸟枪法测序,构建了不同插入片段长度的短文库(170bp、500bp等)和长配对末端文库(2Kb、5Kb等);考虑到猛禽基因组的高杂合性,同时使用SOAPdenovo2和Platanus软件进行de novo组装,并结合从头预测、同源基因预测和血液转录组数据进行蛋白编码基因注释,最终通过组装统计、转录组映射和单拷贝直系同源基因评估,获得了scaffold N50为7.49-29.92 Mb的高质量参考基因组,蛋白编码基因数量约16000-18000个,转座子占比约9.2%,与其他鸟类基因组组成一致;另外12种猛禽和4种非猛禽的基因组未进行组装,仅与近缘物种参考基因组进行比对以减少分析偏差。
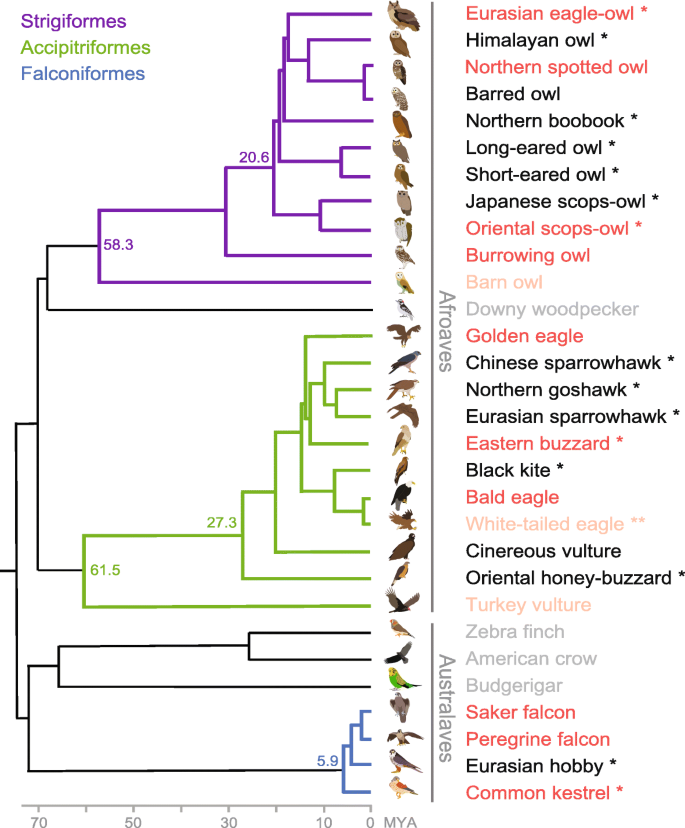
文献未提及具体实验产品,领域常规使用Illumina测序平台、SOAPdenovo2、Platanus等基因组组装软件、BUSCO等组装质量评估工具。
3.2 猛禽与非猛禽的比较进化分析
本环节旨在识别猛禽适应捕食生活方式的共同分子特征。研究人员构建了25种鸟类(23种高质量基因组、2种低质量基因组)的直系同源基因家族,通过CAFÉ软件分析基因家族的扩张与收缩,发现三个猛禽目共同祖先的基因家族在感官感知、解剖结构形态发生、突触后密度及学习功能等方面显著扩张(P<0.05,Fisher精确检验);通过计算dN/dS比值鉴定正选择基因,发现RHCE和CENPQ在三个猛禽目共同祖先分支中均为正选择基因,另有148个基因显示加速的dN/dS,涉及视觉转导、线粒体呼吸链、脂质代谢等功能;进一步分析GC3含量发现,神经系统发育、中枢神经元分化及运动相关基因在猛禽中具有高GC3偏好,提示这些基因可能通过表观遗传调控增强适应性;同时鉴定了三个猛禽目共有的高度保守区域,集中在眼睛、感官器官、肌肉、上皮及肢体发育等功能,进一步证实这些是猛禽捕食适应性的关键功能模块。
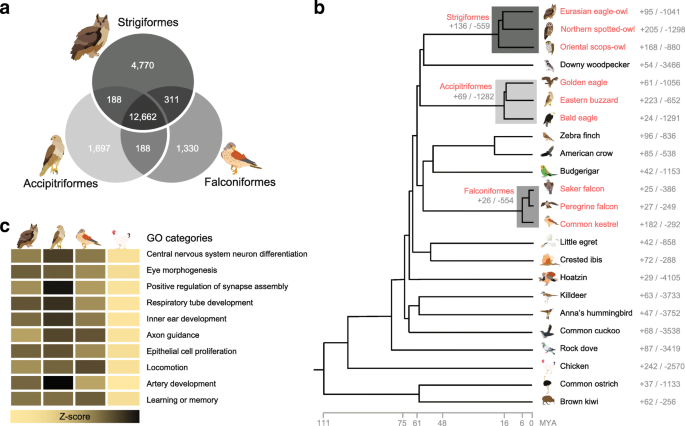
文献未提及具体实验产品,领域常规使用OrthoMCL、CAFÉ、PAML等比较基因组学分析软件。
3.3 夜行性与昼行性鸟类的比较进化分析
本环节的核心目标是解析夜行性鸟类适应夜间环境的分子演化机制。研究人员对比了夜行性鸟类(鸮形目、无翼目、夜鹰目)与昼行性鸟类的基因组特征,发现夜行性鸟类共同丢失了紫/紫外敏感视蛋白基因SWS1,视觉相关基因家族显著收缩;正选择基因分析显示,14个基因在三个夜行性类群中均为正选择,98个基因在至少两个夜行性类群中为正选择,涉及声音感知、伤口愈合、皮肤发育等功能;6个光检测相关基因(RHO、BEST1、PDE6B等)和视黄醇代谢基因RDH8显示加速的dN/dS,其中RHO编码的视紫红质是低光视觉的关键受体,且在夜行性鸟类中具有高GC3偏好;此外,SLC51A基因具有夜行性鸟类特有的氨基酸序列,该基因参与胆汁酸转运,可能通过调节昼夜节律相关基因表达影响夜行性适应,而昼行性的穴居鸮在该基因位点的序列变化与其他夜行性鸟类不同,进一步支持该基因与夜行性的关联。
3.4 感官系统适应性与转录组差异分析
本环节旨在验证夜行性鸟类感官系统的功能权衡及基因表达变化。研究人员分析了25种鸟类的嗅觉受体(OR)基因多样性,发现夜行性鸟类的α-OR基因多样性显著高于昼行性鸟类(P<0.05,Mann-Whitney U检验),鸮形目的γ-c-OR基因多样性更高,提示夜行性鸟类通过增强嗅觉感知弥补视觉的限制;计算感官系统相关基因的dN/dS比值发现,视觉相关基因在夜行性鸟类中显著升高(P<0.05,Mann-Whitney U检验),听觉和昼夜节律相关基因在鸮形目和无翼目中也显示加速进化;同时对13种猛禽和5种非猛禽的血液转录组进行差异表达分析,发现鸮形目与昼行性猛禽相比,视觉相关基因PDCL低表达、WFS1高表达,3个昼夜节律相关基因(ATF4、PER3、NRIP1)低表达,2个基因(BTBD9、SETX)高表达,提示转录组重编程参与了夜行性适应,但研究也指出血液转录组可能无法完全代表视觉系统的基因表达,需进一步验证视网膜组织的表达谱。
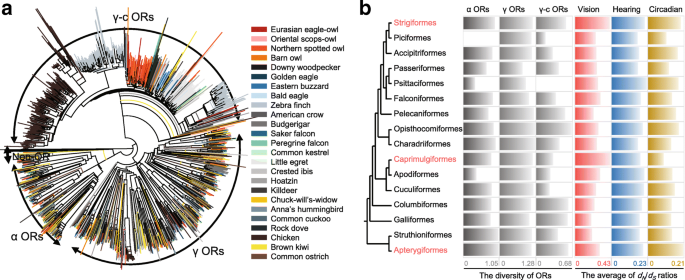
文献未提及具体实验产品,领域常规使用Trinity、TopHat2、edgeR、limma等转录组分析软件。
4. Biomarker研究及发现成果
本研究鉴定了与猛禽捕食适应性和夜行性相关的两类分子标记,通过“基因组筛选→多类群比较→转录组验证”的完整逻辑链条,系统揭示了这些分子标记的功能关联和演化意义。
Biomarker定位方面,捕食适应性相关分子标记包括三个猛禽目共同扩张的基因家族(感官感知、解剖发育相关)、正选择基因RHCE和CENPQ、加速进化的148个基因(如SLC24A1、NDUFS3),筛选逻辑为通过比较猛禽与非猛禽的基因组,鉴定保守的适应性分子特征;夜行性相关分子标记包括丢失的SWS1基因、正选择基因(RHO、TFF2等)、加速进化的光检测和视黄醇代谢基因、差异表达的视觉和昼夜节律基因,筛选逻辑为通过比较夜行性与昼行性鸟类的基因组和转录组,鉴定与夜行性适应相关的分子特征。
研究过程详述:捕食适应性分子标记通过构建直系同源基因家族、计算dN/dS比值、分析GC3含量等方法鉴定,在25种鸟类基因组中进行验证,其中基因家族扩张分析采用Fisher精确检验(P<0.05),正选择基因分析采用似然比检验(校正后P<0.05);夜行性分子标记中,SWS1基因的丢失通过基因组序列比对确认,正选择基因和加速进化基因通过dN/dS分析鉴定,差异表达基因通过血液转录组的RPKM定量、TMM校正和moderated t检验(P<0.05)鉴定,其中RHO基因的GC3偏好通过序列分析确认,SLC51A基因的特有氨基酸序列通过多物种比对验证。
核心成果提炼:捕食适应性分子标记揭示了猛禽作为顶级捕食者在感官、肌肉、循环和呼吸系统的共同分子基础,为理解捕食生活方式的演化提供了全基因组证据;夜行性分子标记揭示了感官系统的功能权衡机制,即通过丢失色觉基因、增强夜视和嗅觉感知适应夜间环境,其中RHO基因的加速进化和高GC3偏好是夜视增强的关键,差异表达的昼夜节律基因提示转录组重编程参与夜行性适应。统计学结果方面,基因家族扩张收缩分析P<0.05(Fisher精确检验),正选择基因分析校正后P<0.05(似然比检验),感官系统基因dN/dS比较P<0.05(Mann-Whitney U检验),转录组差异表达P<0.05(moderated t检验),所有数据均基于至少20种鸟类的样本量。
