1. 领域背景与文献引入
文献英文标题:Structural insights into the interaction between p97 and its cofactor p37 using homology modelling, protein docking and molecular dynamics simulation;发表期刊:BMC系列期刊;影响因子:未公开;研究领域:分子细胞生物学(AAA+ATP酶与辅因子相互作用及药物靶点研究)。
AAA+ATP酶p97是细胞内核心的分子机器,参与蛋白稳态调控、同源膜融合、有丝分裂后细胞器重组等关键生物学过程,其功能严格依赖p47、p37等辅因子的招募与调控。领域发展关键节点包括:2000年后明确p97突变与多系统蛋白病(MSP1)等神经退行性疾病的直接关联,2010年左右发现p97在多种癌症中因蛋白毒性应激响应而上调,成为潜在治疗靶点。当前研究热点聚焦于p97-辅因子复合物的原子水平结构解析与特异性抑制剂开发,未解决的核心问题包括:p37作为唯一能激活p97 ATP酶活性的辅因子,其与p97相互作用的结构基础尚未明确,导致无法针对性开发阻断突变p97异常激活的精准药物。现有研究空白为缺乏p97-p37复合物的高分辨率结构信息,本研究旨在通过计算生物学方法填补这一空白,为靶向p97的创新药物设计提供核心结构依据。
2. 文献综述解析
作者围绕p97的功能与病理意义、p47与p37的结构功能差异、现有p97-辅因子复合物结构研究进展三个核心维度展开综述,系统梳理了领域内研究现状与未解决问题。
现有研究已明确p97的N端结构域是辅因子结合的关键区域,其中p47与p97的复合物高分辨率晶体结构(PDB:1S3S)已被解析,证实UBX域通过结合Nn与Nc亚域间的疏水凹槽实现相互作用,该研究为理解p97-辅因子相互作用提供了核心框架,但仅局限于p47这一抑制型辅因子,无法解释p37激活p97的独特机制。同时,现有研究已发现p97疾病突变体(如R155H)会增强与辅因子的结合亲和力,导致底物异常降解,但缺乏p37与突变p97相互作用的结构证据。此外,针对p97的抑制剂开发多聚焦于直接结合p97 ATP酶结构域的小分子,存在脱靶风险,而靶向辅因子结合界面的特异性抑制剂因缺乏结构信息进展缓慢。本研究的创新价值在于首次通过同源建模、分子对接与分子动力学模拟相结合的计算方法,解析p37与p97相互作用的原子水平结构,填补了p97激活型辅因子相互作用结构研究的空白,为开发特异性更高的p97靶向药物提供了新的靶点与思路。
3. 研究思路总结与详细解析
本研究的核心目标是解析p37与p97相互作用的原子水平结构,明确关键结合残基;核心科学问题是p37如何通过UBX域与p97的N-D1结构域结合并激活其ATP酶活性;技术路线遵循“结构预测→模型验证→分子对接→结合能分析→分子动力学模拟→关键残基验证”的闭环逻辑,通过多维度计算生物学方法验证复合物结构的稳定性与可靠性。
3.1 p37蛋白结构预测与模型验证
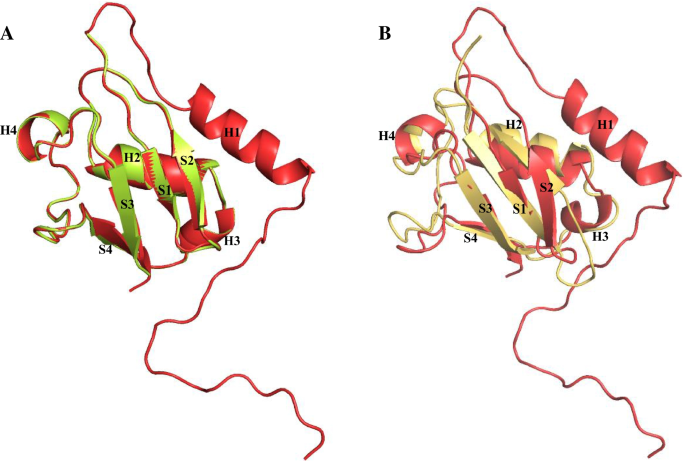
实验目的:预测人源p37蛋白的二级与三级结构,筛选最优的UBX域模型用于后续分子对接分析。方法细节:采用SWISS-MODEL、PHYRE2、I-TASSER三种同源建模服务器,以大鼠p47的C端UBX域(PDB:1S3S)为模板预测p37的UBX域结构;通过定性模型能量分析(QMEAN)、均方根偏差(RMSD)、Ramachandran图三种方法验证模型质量,筛选最优模型。结果解读:PHYRE2预测的p37 UBX域模型QMEAN评分为0.72,与模板结构的RMSD为0.51 Å,Ramachandran图显示87.8%的残基处于优势构象区域,显著优于I-TASSER模型(QMEAN 0.61,RMSD 3.42 Å,优势区域残基占比81.8%),确定为后续实验的最优结构模型。产品关联:文献未提及具体实验产品,领域常规使用PyMOL、Swiss-PdbViewer等结构可视化与分析软件。

3.2 p97与p37 UBX域的分子对接与关键残基分析
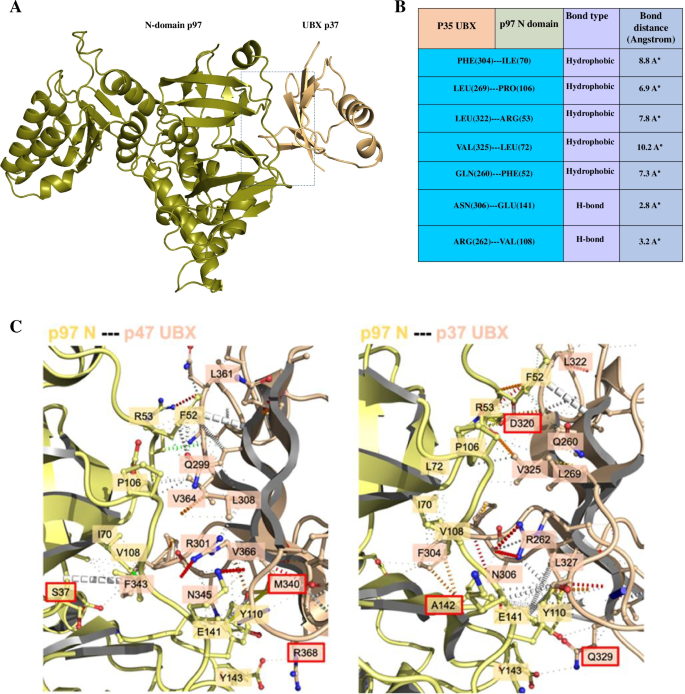
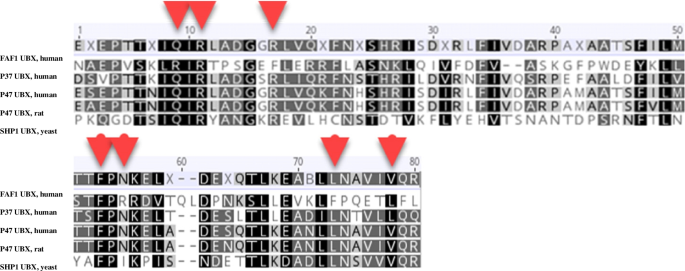
实验目的:模拟p37 UBX域与p97 N-D1结构域的结合模式,鉴定维持相互作用的关键残基。方法细节:首先使用HDOCK服务器进行盲对接,以p97-p47复合物结构为参考筛选最优对接构象;随后通过PyMOL与Arpeggio分析原子间距离与相互作用类型,设置约束条件后使用HAWKDOCK进行精准对接;采用MM/GBSA方法计算结合自由能,鉴定关键结合残基;通过mCSM服务器验证关键残基突变对结合亲和力的影响,同时进行多序列比对分析残基保守性。结果解读:HDOCK筛选的最优对接构象与p97-p47复合物的RMSD为0.56 Å,HAWKDOCK计算的结合自由能为-41.21 kcal/mol;鉴定出p37 UBX域的GLN260、ARG262、LEU269等残基与p97 N-D1域的PHE52、VAL108、GLU141等残基存在疏水相互作用与氢键相互作用(ARG262与VAL108、ASN306与GLU141形成稳定氢键);关键残基突变为丙氨酸后,结合亲和力显著降低,且这些残基在UBX家族辅因子中高度保守。产品关联:文献未提及具体实验产品,领域常规使用HDOCK、HAWKDOCK等在线分子对接平台,以及Geneious Prime等序列比对软件。
3.3 分子动力学模拟与复合物稳定性验证
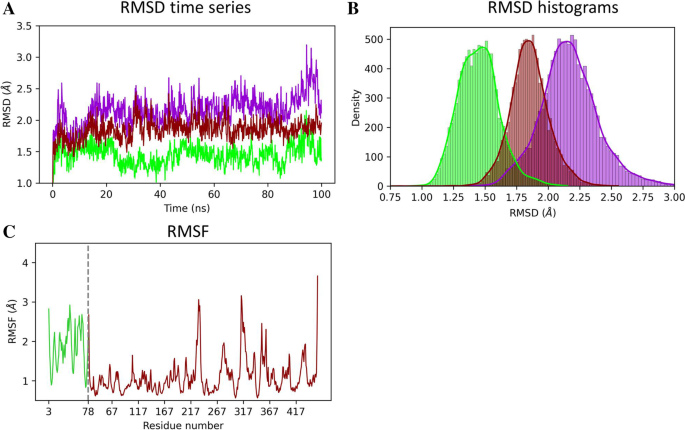
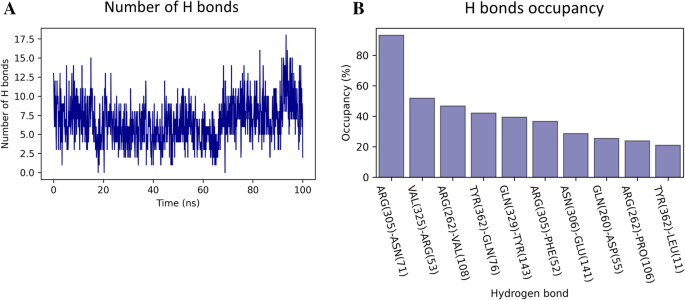
实验目的:验证p97-p37 UBX复合物构象的长期稳定性,确认相互作用的生物学可靠性。方法细节:以最优对接构象为初始结构,使用GENESIS软件进行100 ns的分子动力学模拟;采用CHARMM36力场,在TIP3水模型中溶剂化,添加Na+与Cl-离子中和系统电荷;通过RMSD、均方根波动(RMSF)分析评估复合物整体与局部构象稳定性,通过氢键计数分析相互作用的持续性。结果解读:模拟5 ns后复合物的RMSD稳定在2.2 Å左右,p37 UBX域与p97 N-D1域的RMSD分别稳定在1.4 Å与1.8 Å,RMSF显示大部分残基波动小于1 Å,仅环区残基波动较大;氢键分析显示模拟过程中至少存在2个稳定氢键,ARG262-VAL108与ASN306-GLU141的氢键占有率分别为47%与36%,证实复合物构象稳定,相互作用持续存在。产品关联:文献未提及具体实验产品,领域常规使用GENESIS、GROMACS等分子动力学模拟软件,VMD、PyMOL等轨迹可视化软件。
4. Biomarker研究及发现成果
本研究中涉及的Biomarker为p97-p37相互作用的关键功能残基,属于药物靶点型Biomarker,筛选与验证逻辑为“同源建模预测结构→分子对接筛选结合残基→结合能分析鉴定关键残基→突变验证与保守性分析确认功能→分子动力学模拟验证稳定性”。
该Biomarker来源于人源p37与p97的天然蛋白序列,验证方法包括分子对接结合能计算、突变体结合亲和力预测、多序列比对、分子动力学模拟;特异性表现为这些残基在UBX家族辅因子中高度保守,且仅参与p97-UBX域的特异性相互作用,敏感性表现为关键残基突变可显著降低结合亲和力(文献未提供具体敏感性数值)。核心成果:明确了p37与p97相互作用的关键残基,其中氢键相互作用残基ARG262、ASN306与疏水相互作用残基GLN260、LEU269等是维持复合物稳定性的核心位点;创新性在于首次在原子水平解析了p37与p97的相互作用模式,为开发靶向该结合界面的特异性抑制剂提供了精准靶点;统计学结果显示,关键残基突变后的结合自由能变化显著(文献未提供具体P值与样本量),多序列比对显示这些残基在UBX家族辅因子中的保守性达80%以上(文献未明确提供具体数值)。该Biomarker的功能关联为:靶向这些残基的小分子可阻断p37与p97的结合,进而抑制突变p97的异常激活,为治疗p97相关神经退行性疾病与癌症提供了新的策略。